本周完结:单细胞+空间转录组,Python全流程实战教学!
- 2026-03-09 14:50:27

写在前面



报名联系客服微信[Biomamba_zhushou]:



内容计划&大纲


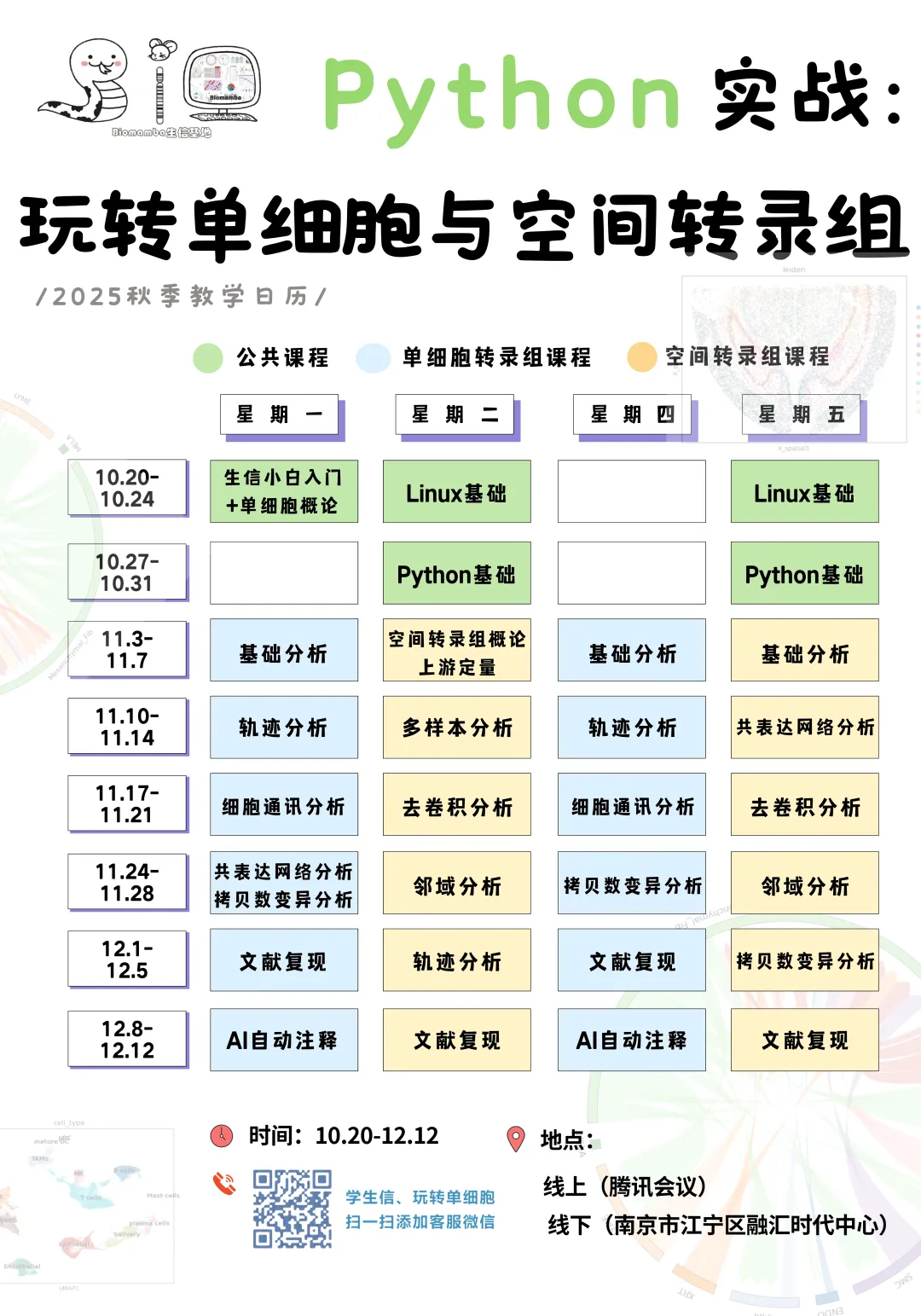

所见即所得
Linux基础课学习手册


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:


Python基础课学习手册




单细胞-基础分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
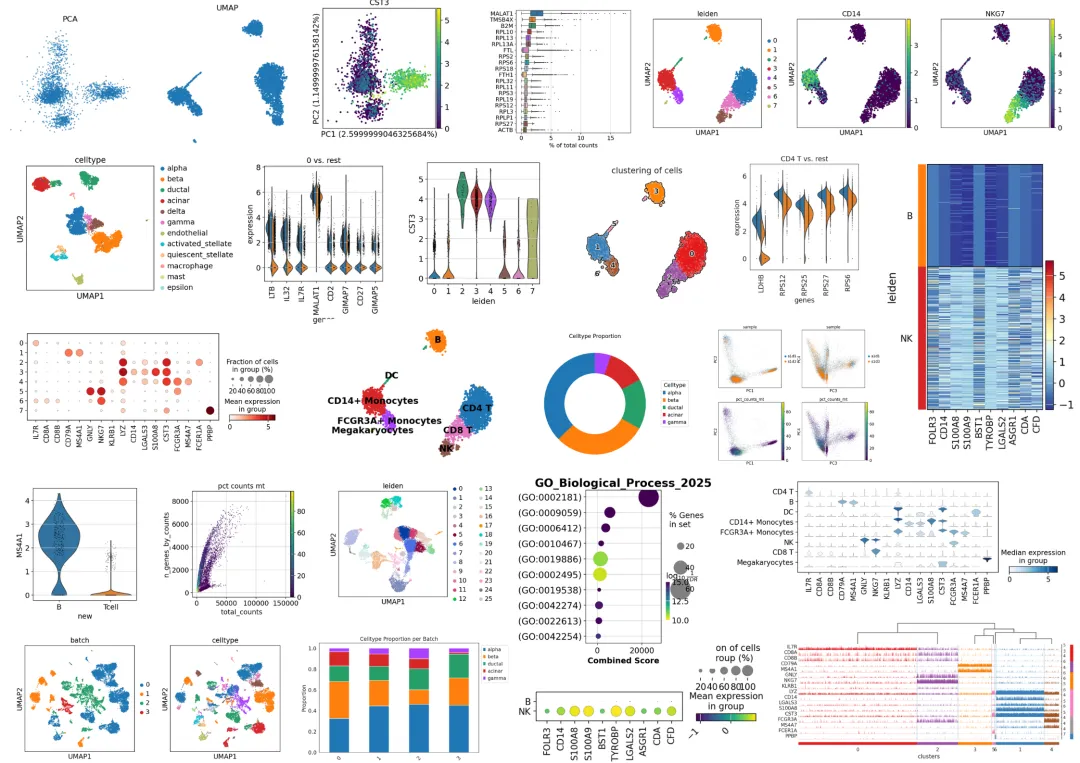


单细胞-进阶分析-轨迹分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
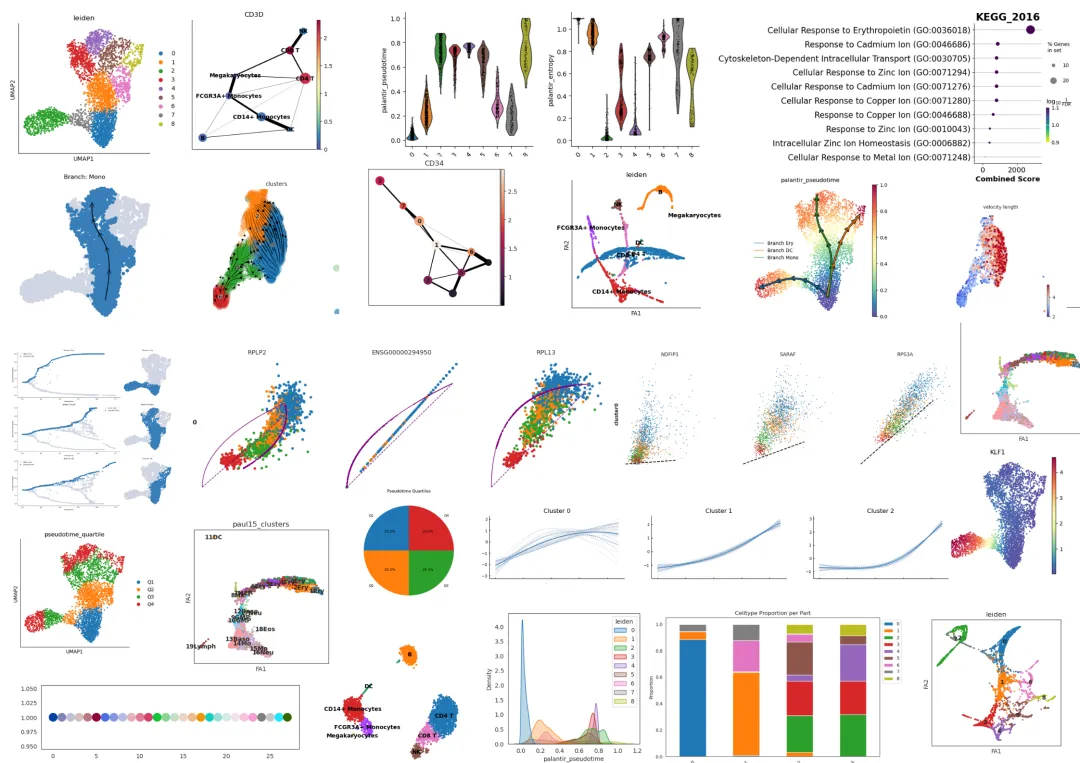


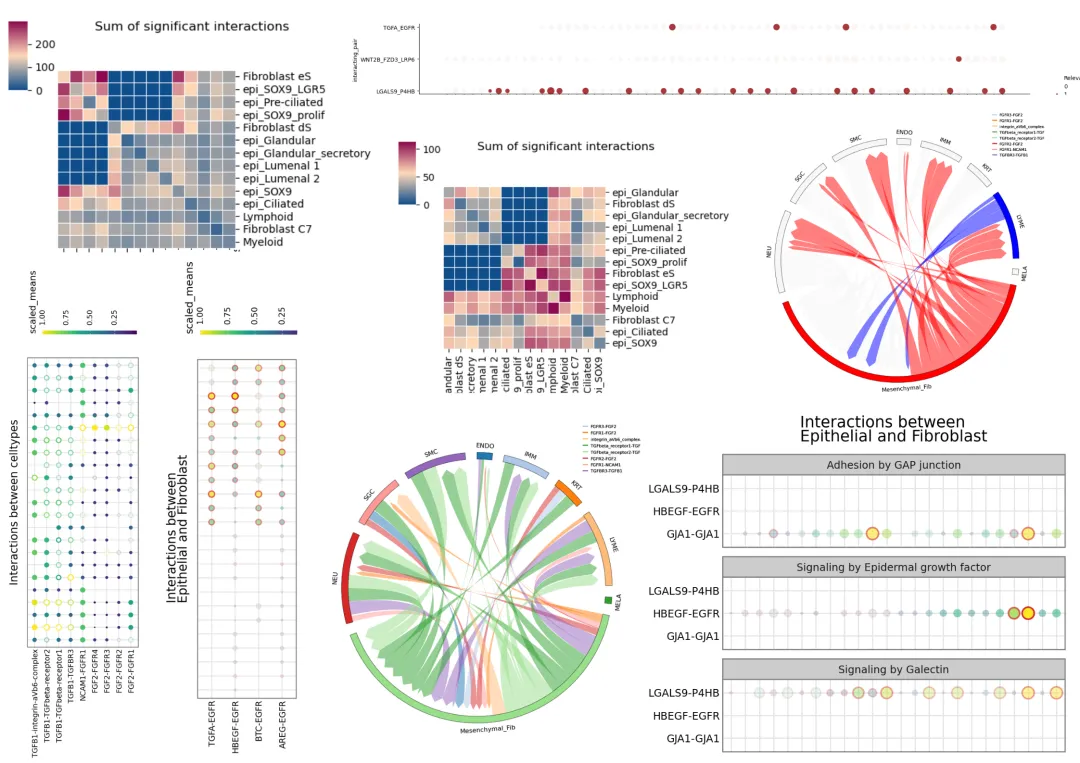
单细胞-进阶分析-细胞通讯分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:

教程目录:
零、欢迎关注
一、前言
1.1 定义
1.2 互作预测过程
1.3 不同细胞软件的比较
1.3.1 基于规则的工具
1.3.2 基于数据的工具
1.3.3 混合模型
1.3.4 其他分支
1.3.5 实验追踪细胞间相互作用
二、CellPhoneDB文献解读
2.1 摘要
2.2 数据库概述
2.3 分析方法概述
2.4 实际应用
2.5 小结
三、准备工作
3.1 环境准备
3.2 库准备
四、cellphonedb
4.1 下载数据库
4.2 构建数据库
4.3 输入数据详情
4.4 计算方法介绍
4.4.1 cpdb_analysis_method.call
4.4.2 cpdb_statistical_analysis_method.call
4.4.3 cdpb_degs_analysis_method.call
4.5 示例代码
4.6 示例数据-方法1
4.6.1 输入文件
4.6.2 互作对预测
4.6.3 结果解读
4.6.4 思考?
4.7 示例数据-方法2
4.8 示例数据-方法3
4.9 人纤维化皮肤病单细胞数据实操
4.9.1 输入文件
4.9.2 准备文件
4.9.3 互作对预测
4.9.4 结果解读
4.9.5 探索CellphoneDB结果
4.9.6 可视化

单细胞-进阶分析-共表达网络分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_yunying]领取:
教程图片集锦:

教程目录:
零、欢迎关注
一、前言
1.1 研究背景
1.2 主要结果
1.3 小结
二、准备工作
三、基于表达相关性
四、基于Kmeans聚类
五、基于pyscenic
5.1 文献解读
5.1.1 SCENIC工作流程
5.1.2 在小鼠脑组织的应用
5.1.3 在复杂癌症中的应用
5.1.4 在黑色素瘤中的应用
5.1.5 小结
5.2 数据库下载
5.3 loom文件准备
5.4 运行pyscenic
5.5 下游分析
5.5.1 基因aucell降维
5.5.2 vlnplot
5.5.3 umap
5.5.4 dotplot

单细胞-进阶分析-拷贝数变异分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:

教程目录:
零、欢迎关注
一、前言
二、准备工作
三、infercnvpy
四、通过CNV谱进行聚类并识别肿瘤细胞
4.1 cnv聚类分群
4.2 cnv展示umap
4.3 scanpy展示cnv结果
4.4 肿瘤细胞分类
4.5 肿瘤和正常细胞分开绘制热图
五、内嵌copykat
5.1 数据读入
5.2 参数详解
5.3 运行copycat
5.4 计算每个细胞的cnv分数
5.5 可视化
5.6 通过cnv谱进行聚类并识别肿瘤细胞
5.7 肿瘤和正常细胞分开绘制热图
六、对比R版本的infercnv
七、如何获取基因在染色体上的位置


单细胞-文献复现学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_yunying]领取:
原文集锦:
复现图片集锦:

教程目录:
零、欢迎关注
一、文献解读
1.1 背景介绍
1.2 主要内容
1.3 总结讨论:
二、数据下载
三、数据整理
四、细胞注释
4.1 降维图
4.2 小提琴图
五、降维展示
六、细胞比例统计
6.1 整体统计
6.2 免疫细胞
6.3 非免疫细胞
七、上皮细胞肿瘤细胞鉴定
7.1 数据准备
7.2 参数详解
7.3 运行infercnvpy
7.4 计算每个细胞的cnv分数
7.5 可视化
7.6 通过CNV谱进行聚类并识别肿瘤细胞
7.6.1 cnv聚类分群
7.6.2 cnv展示UMAP
7.6.3 scanpy展示cnv结果
7.6.4 肿瘤细胞分类
7.6.5 单独绘制肿瘤细胞
八、上皮细胞轨迹分析
8.1 降维分群
8.2 预处理
8.3 可视化
8.4 运行Palantir
8.4.1 获取细胞坐标
8.4.2 定义分化起点和终点
8.4.3 拟时间推断
九、上皮细胞EMT评分
十、CD8T轨迹分析
10.1 T细胞注释
10.2 CD8 T细胞注释
10.3 预处理
10.4 可视化
10.5 运行Palantir
10.5.1 获取细胞坐标
10.5.2 定义分化起点和终点
10.5.3 拟时间推断
十一、上皮细胞互作分析
11.1 数据预处理
11.2 互作对预测
11.3 结果解读
11.4 探索cellphonedb结果
11.5 可视化
十二、软件版本
十三、单细胞教程全收录
十四、欢迎致谢

单细胞-AI自动注释学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:
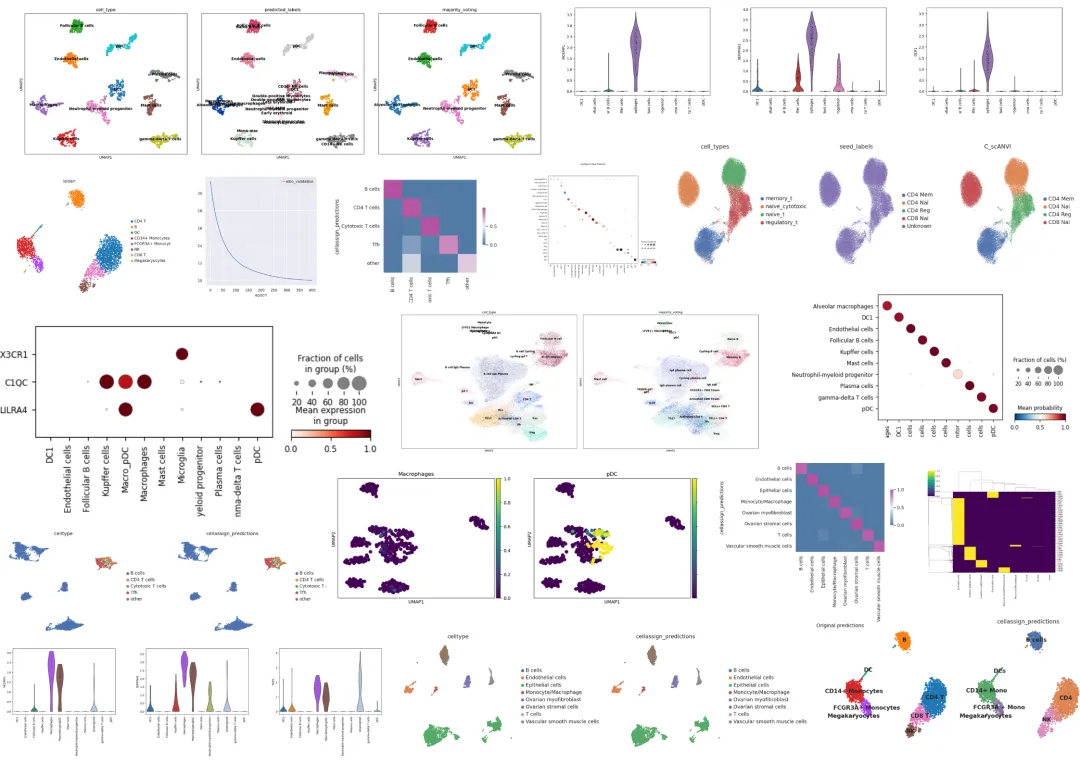

教程目录:
零、欢迎关注
一、准备工作
1.1 环境准备
1.2 加载库
二、CellTypist
2.1 下载测试数据
2.2 CellTypist内置模型注释
2.3 自定义模型进行注释
2.4 CellTypist进行多标签分类
2.4.1 数据下载
2.4.2 内置模型+best match模式
2.4.3 内置模型+prob match模式
2.4.4 自定义模型+prob match模式
2.4.5 检查模型驱动基因
2.5 大规模跨数据集应用
2.5.1 数据下载
2.5.2 数据预处理
2.5.3 训练集的特征选择
2.5.4 开始预测
2.5.5 结果一致性比较
三、scVI

空间转录组-概论及上游定量学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:

教程目录:
零、欢迎关注
一、空间转录组概论&常见平台的上游定量
1.1 背景与发展历程
1.2 技术分类
1.3 实验流程
1.3.1 10x Visium
1.3.2 SeekSpace(高通量条码捕获+空间分辨率优化)
1.3.3 Stereo-seq
(1)Stereo-seq的DNA Nanoball(DNB)技术
1.4 空间转录组平台对比
二、上游测序数据定量
2.1 10x Visium平台
2.1.1 软件安装
2.1.2 示例数据下载
2.1.3 参考基因组构建(适用于非模式动物)
2.1.4 定量
2.1.5 结果文件概况
2.1.6 Space Ranger Metrics说明
2.2 SeekSpace平台
2.3 Stereo-seq平台

空间转录组-基础分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:
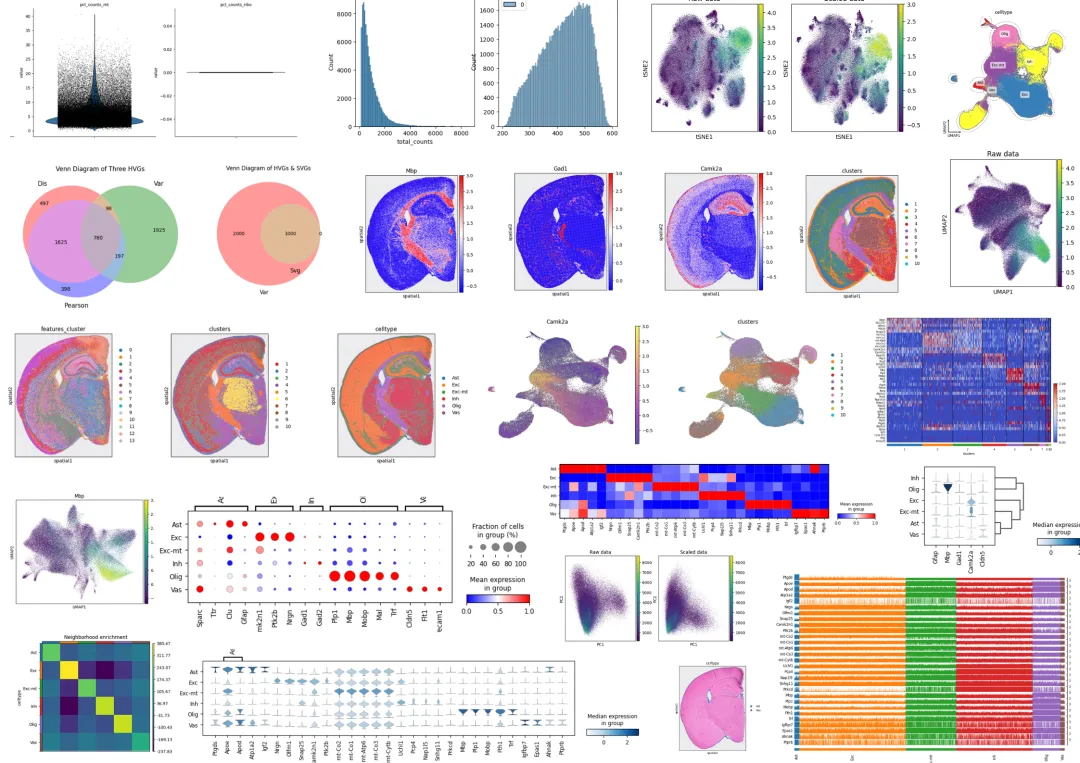
教程目录:
零、欢迎关注
一、添加空间坐标和图像信息(早期版本)
二、添加QC指标(线粒体基因+核糖体基因)
三、动态过滤(Adaptive Filtering)
四、归一化
五、选择高度可变的基因
六、t-SNE
七、寻找差异marker基因
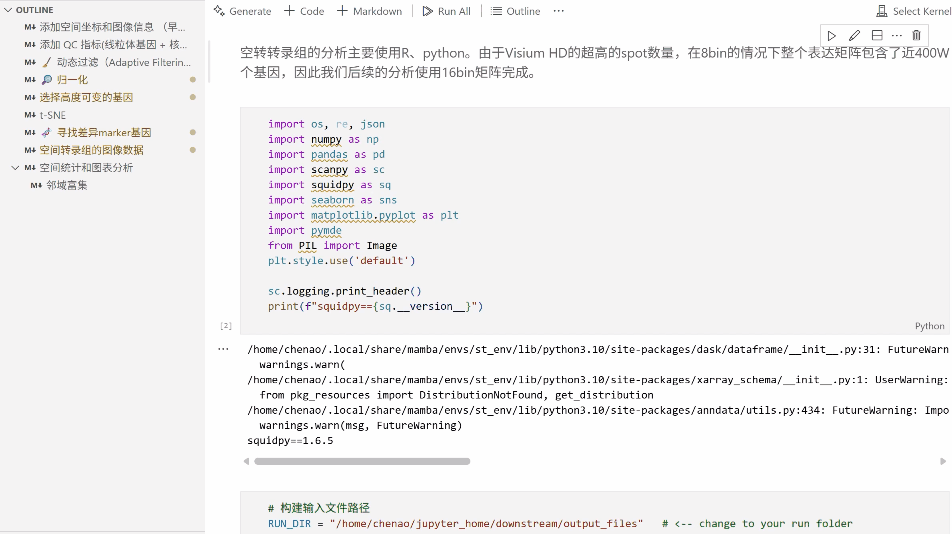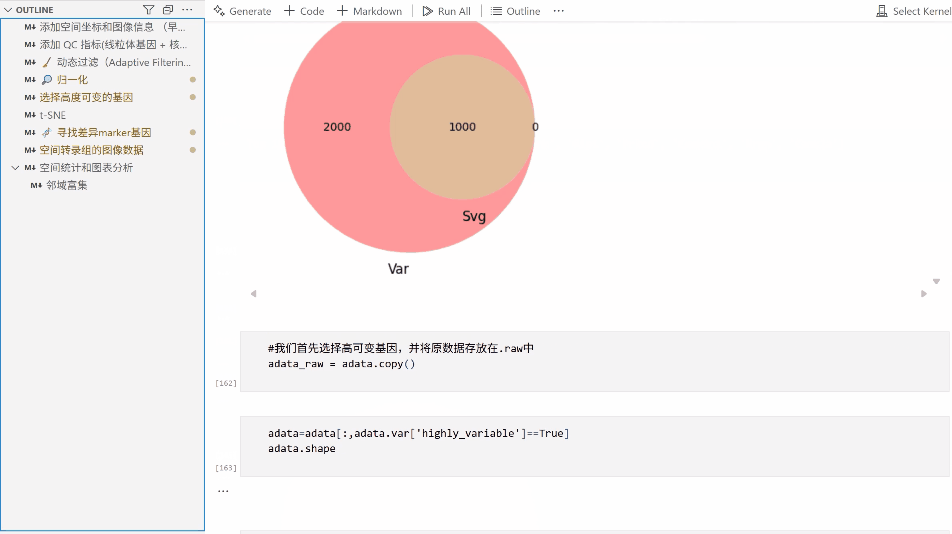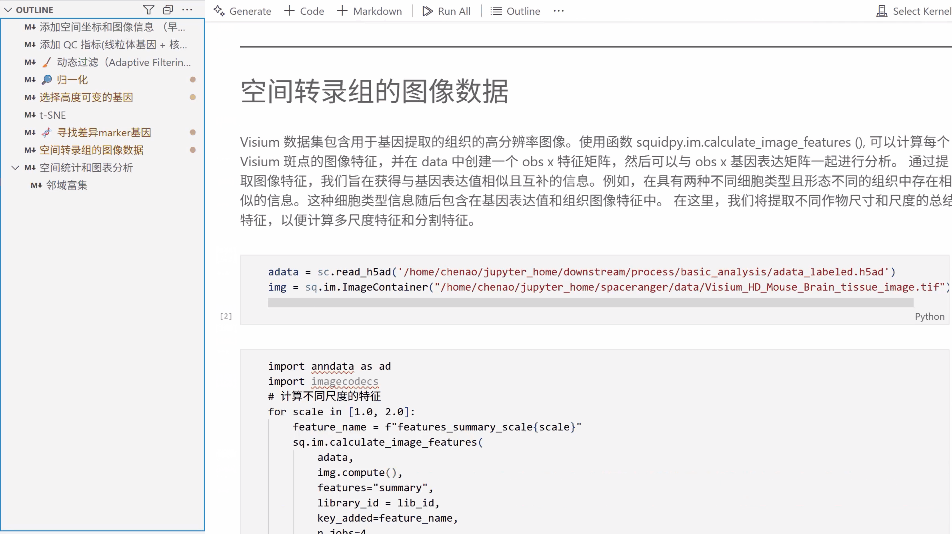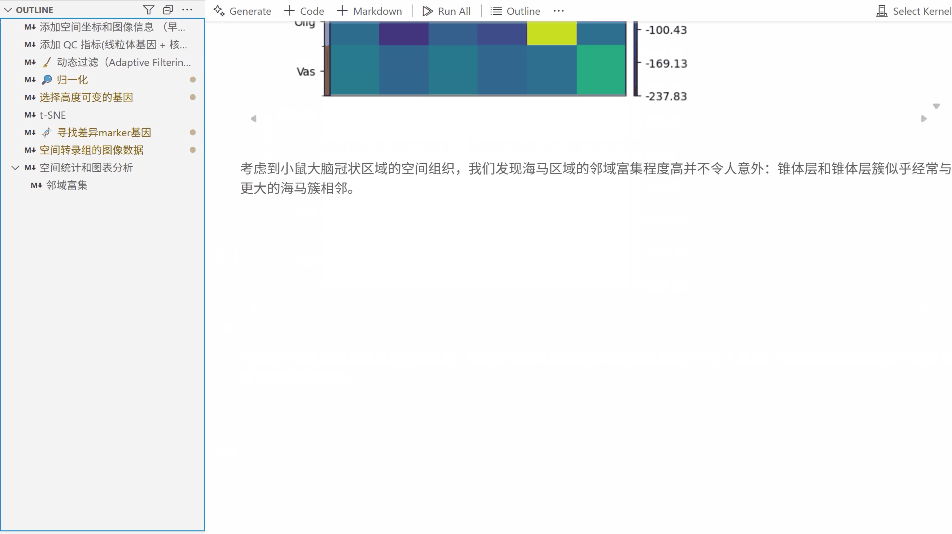
八、空间转录组的图像数据
九、空间统计和图表统计

空间转录组-进阶分析-多样本分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:

教程目录:
零、欢迎关注
一、数据整合
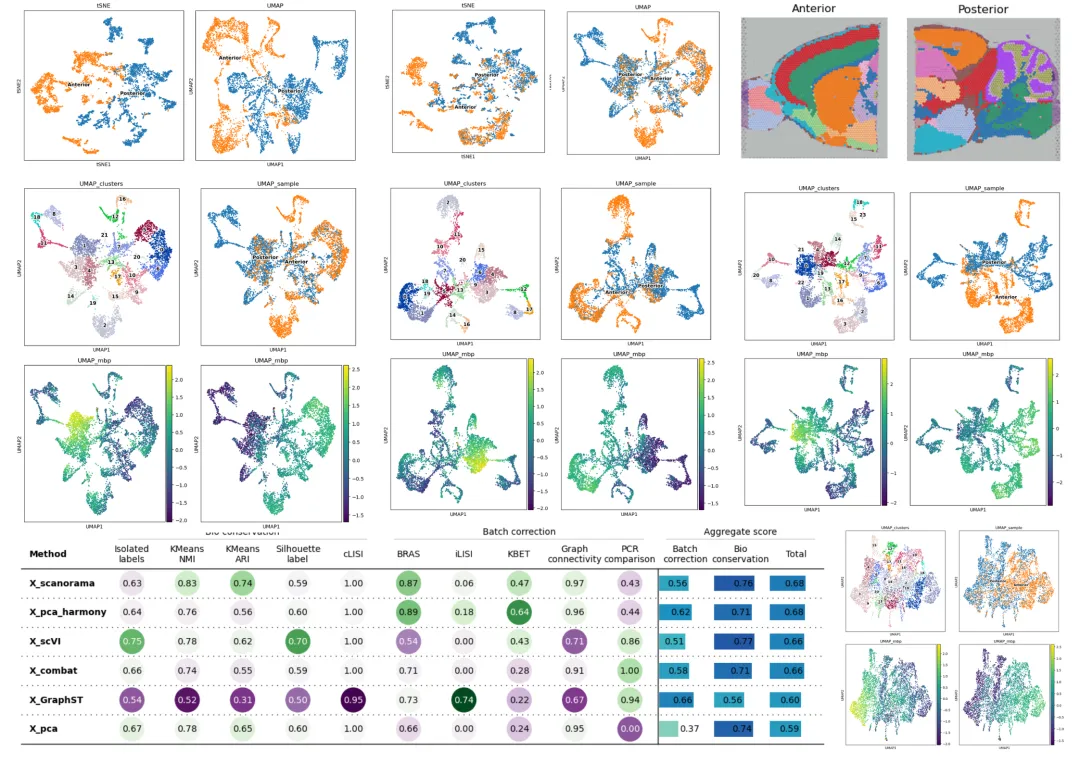
1.1 数据整合模型的比较
1.2 导入数据
1.3 过滤初始数据(不推荐)
1.4 基础处理,均一化(normalize)
1.5 聚类
1.6 harmony去批次
1.7 重新聚类
1.8 Scanorama
1.9 Combat矫正
1.10 BBKNN矫正
二、深度学习模型
2.1 基于变分自编码器的模型
2.2 GraphST

空间转录组-进阶分析-共表达网络分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:

教程目录:
零、欢迎关注
一、SCENIC分析空间转录组转录因子
1.1 基因调控网络推断,生成共表达模块
1.1.1 使用GRNBoost2算法推断基因调控网络(GRN)
1.2 Cistarget预测
1.3 转录因子的细胞富集
二、可视化AUC矩阵
2.1 数据输入
2.2 提取相关数据整合
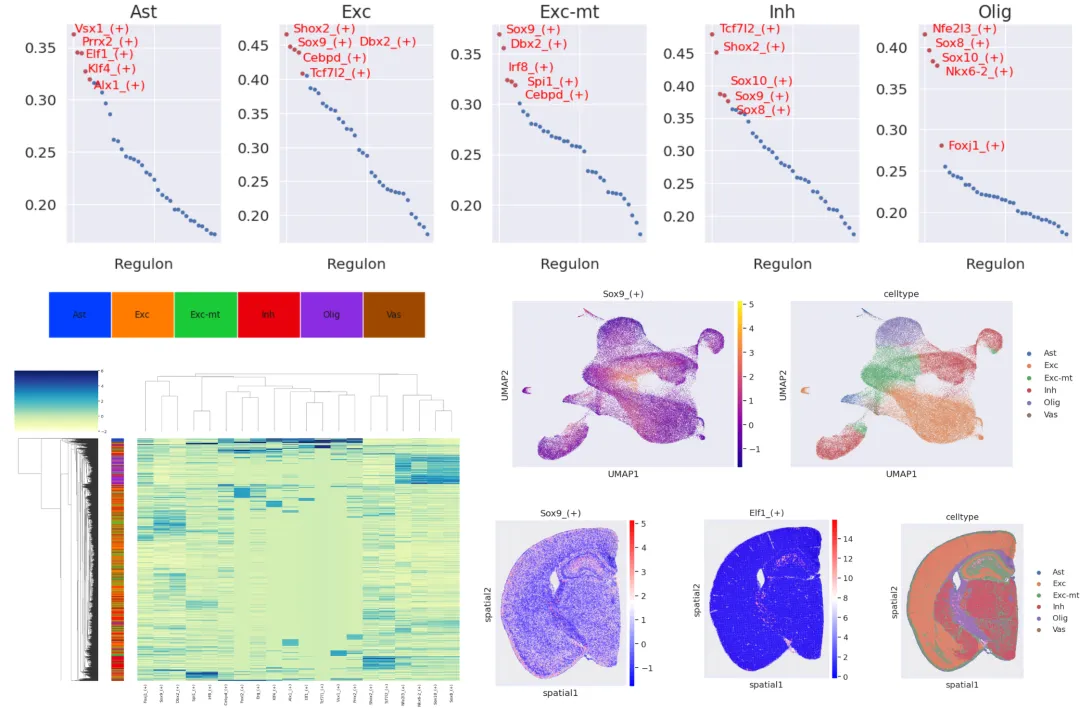
2.3 差异regulons
2.4 结合空间样本的TF活性可视化
2.5 TF活性热图

空间转录组-进阶分析-去卷积分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:
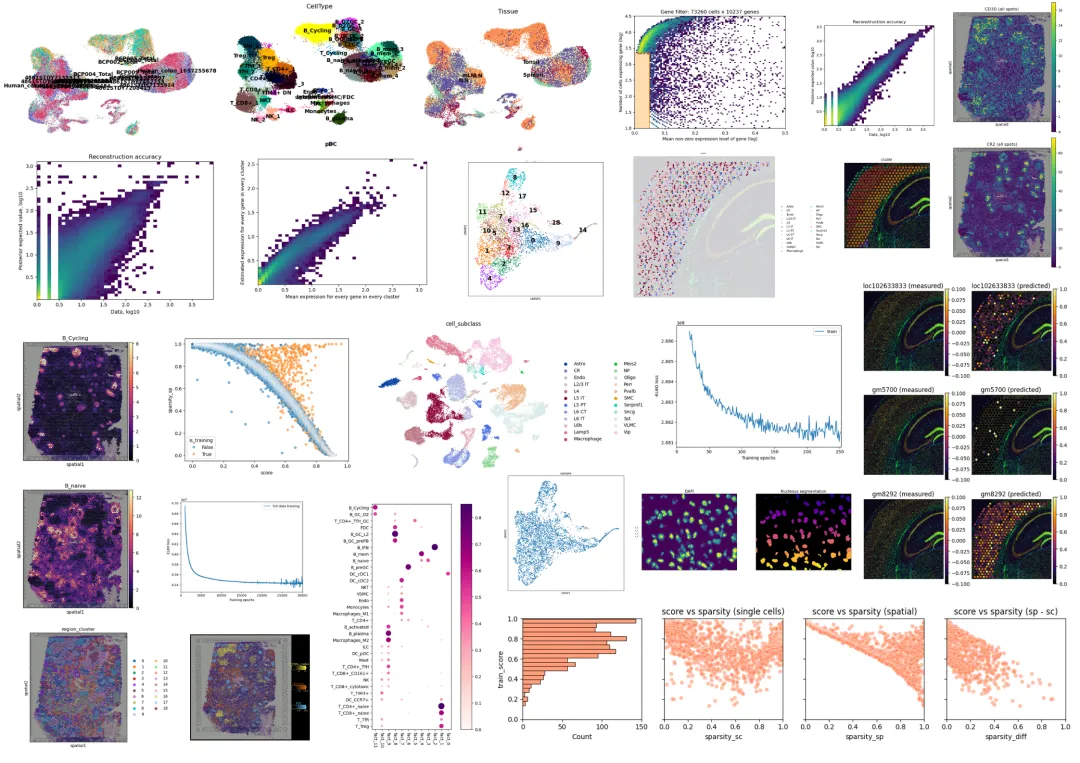

教程目录:
零、欢迎关注
一、Cell2location
1.1 Cell2location映射到空间转录组
1.1.1 加载安装的库
1.1.2 价值单细胞转录组参考数据
1.1.3 参考细胞类型特征估计(Estimation of reference cell type signatures)------NB回归)
1.1.4 检查QC质量图表
1.2 数据和模型读取
1.2.1 Cell2location:空间映射
1.2.2 可视化细胞类型丰度
1.2.3 下游分析
(1)通过聚类来区分不同组织区域
1.2.4 非负矩阵分解(NMF)识别细胞区室/组织区域
(1)输出结果说明
1.2.5 估计空间数据中每个基因的细胞类型特异性表达
二、Tangram
2.1 加载空间转录组和单细胞参考数据
2.2 预处理
2.3 数据对齐
2.4 细胞类型映射
2.5 通过对齐单细胞数据获得新的空间数据
2.6 通过比对单细胞数据进行反卷积

空间转录组-进阶分析-邻域分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_zhushou]领取:
教程图片集锦:
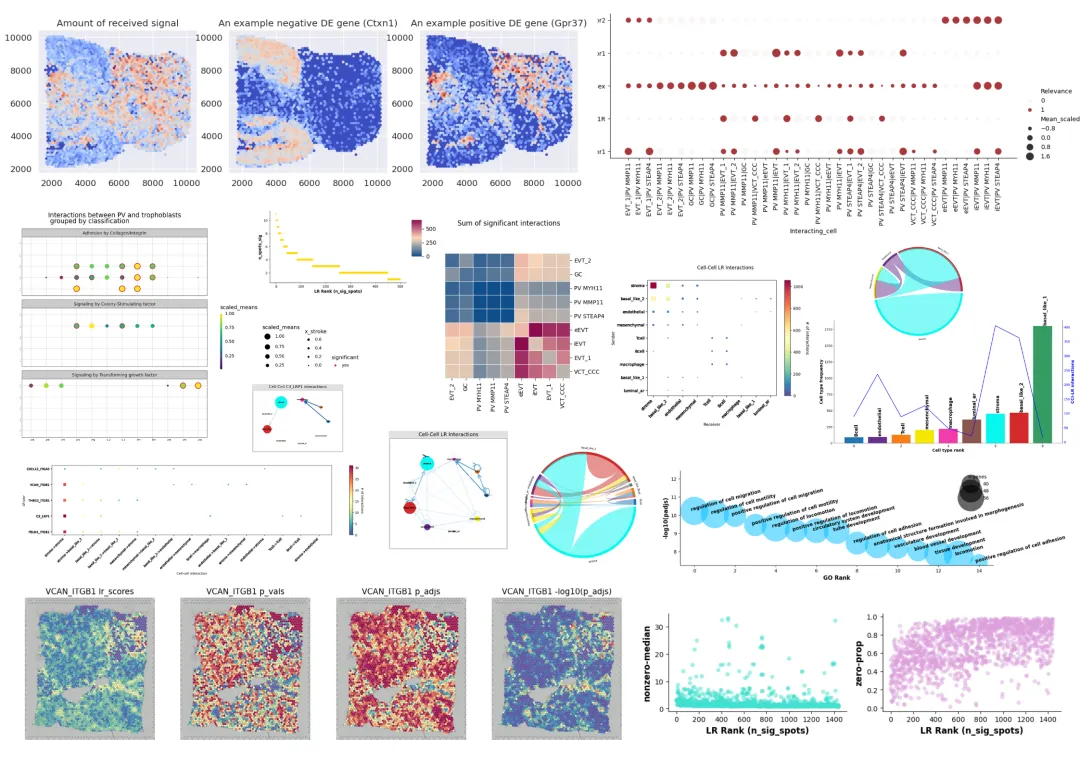

教程目录:
零、欢迎关注
一、CellphoneDB
1.1 检查版本信息
1.2 安装CellphoneDB
1.3 输入文件
1.4 检查输入文件
1.5 运行统计分析
1.6 输出文件信息
1.7 解释CellphoneDB结果
1.8 基础结果可视化
1.9 按递归排序
二、commot
2.1 安装
2.2 测试文件
2.2.1 导入所需库和包
2.2.2 预处理空间数据文件
2.2.3 空间通讯信号推断
三、stlearn
3.1 StLearn细胞间相互作用分析
3.1.1 环境配置
3.1.2 数据加载和预处理
3.1.3 运行受配体分析
3.1.4 P值矫正
3.1.5 按显著程度可视化LR的整体排名
3.1.6 判定绘图
3.1.7 下游可视化
(1)受配体对的统计可视化
(2)LR解释结果可视化
(3)预测重要的CCIs
(4)检查相互作用和细胞类型频率相关性
(5)CCI可视化
(6)空间细胞类型的相互作用
3.2 作者建议-可视化技巧

空间转录组-进阶分析-轨迹分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_yunying]领取:
教程图片集锦:
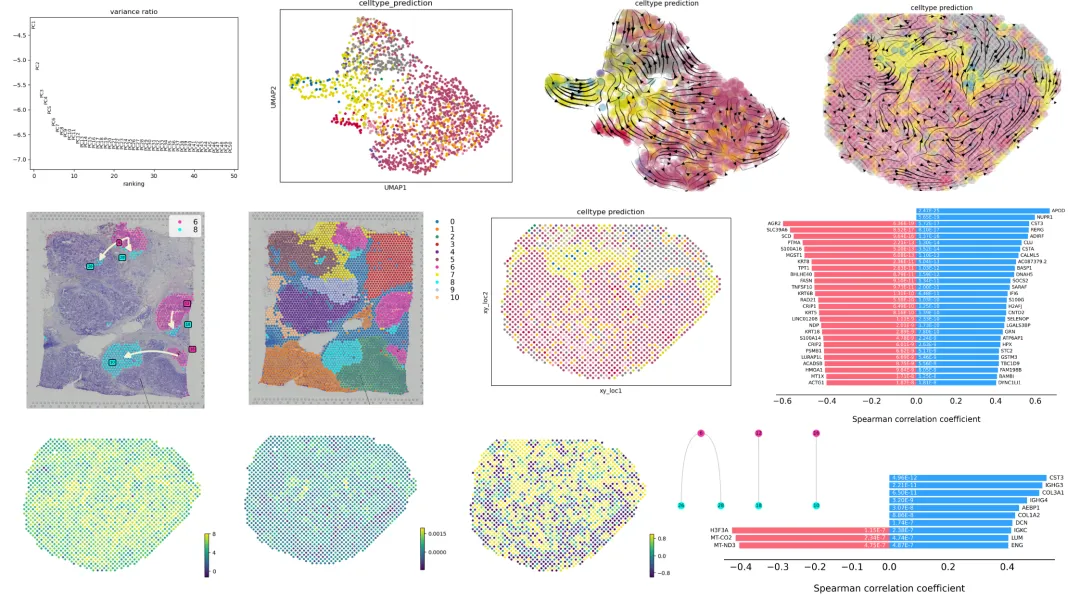

教程目录:
零、欢迎关注
一、stLearn_pse
1.1数据准备
1.1.1 读取和预处理数据
1.1.2 聚类
1.2 空间轨迹推理
1.2.1 选择分化起点(根节点)
1.2.2 空间轨迹推断--全体水平
1.2.3 检测过渡标志
二、SIRV
2.1 准备工作
2.2 SIRV实现流程
2.2.1 输入数据
2.2.2 域适配(Domain Adaptation / Alignment)
2.2.3 基于scRNA-seq训练模型 / 回归
2.2.4 将预测的velocity映射到空间
2.2.5 标签转移
2.3 运行示例
2.3.1 加载所需的库
2.3.2 读取示例数据
2.3.3 补全信息
2.3.4 常规降维
2.3.5 降维聚类
2.3.6 velocity推断流程
2.3.7 可视化流线图
2.3.8 局部流向箭头图
2.3.9 比较补全前后信息
2.3.10 评估velocity相似性

空间转录组-进阶分析-拷贝数变异分析学习资料


同我们以前的课程一样,我们给大家准备了学习手册和学习资料,大家可联系客服微信[Biomamba_yunying]领取:
教程图片集锦:
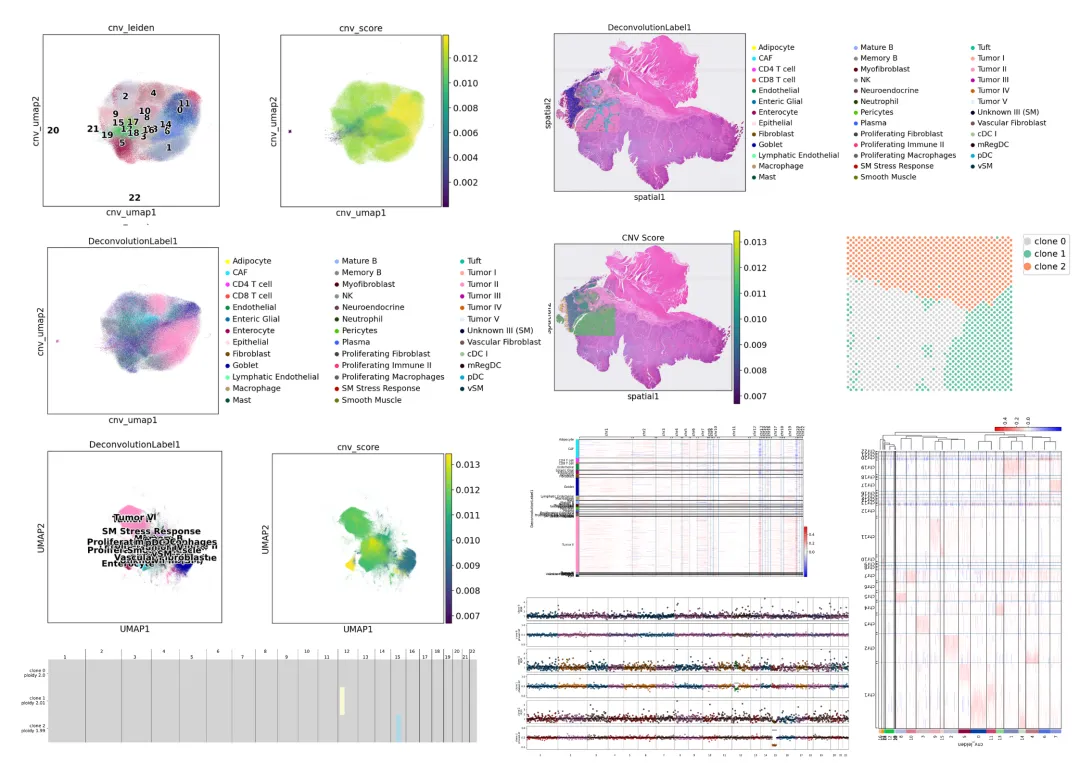

教程目录:
零、欢迎关注
一、使用模拟数据运行CalicoST
1.1 下载数据
1.2 运行CalicoST
二、复制configuration文件来用于推断CNA和癌症克隆
2.1 加载结果到python中进行可视化


报名费用


两个月的课程,单个只要4999¥,两班联报,优惠多多!详情咨询客服微信[Biomamba_zhushou]
有其它任何想法的同学也欢迎随时联系我们,更欢迎看看我们的价值观:想钱想疯了?


线下学习环境




除了知识之外,现场还能够给大家提供:

各类饮料、零食小吃



如何联系我们


已有生信基地联系方式的同学无需重复添加


