在Linux服务器中部署omicverse-web,助力组学分析
- 2026-04-19 07:31:34

一边学习,一边总结,一边分享!

我们这里使用的是西柚服务器,他们的下载网络确实很快,有国际专线,前面我们在zenodo数据中下载T2T泛基因组,轻轻松松搞定,2026年Pan-genome可能作为顶刊的一个方向,如何快速下载T2T-Pan-genome数据?。春节期间,可领取200元立减券:西柚云服务器立减优惠活动,或输入优惠码:BioinfoDu。

写在前面
Steorra开发了OmicVerse(OmicClaw),给我们组学分析带来了很大的便利性,非常优秀的软件。此外,Steorra也做非常详细的教程,也在他自己的账号下分享了教程。但是,作为的一名使用者,无论怎么再怎么优秀的软件,得自己使用上才可以。若是一味的纸上谈兵,那都是没有任何意义。 在前面的教程,我们分享了在Linux中安装omicverse / OmicClaw,Bulk RNA和单细胞分析“信手捏来”?,此教程也初步提到omicverse-web的安装,但未做“步骤性”的教程。
相关网址
1. Github仓库
https://github.com/Starlitnightly/omicverse-web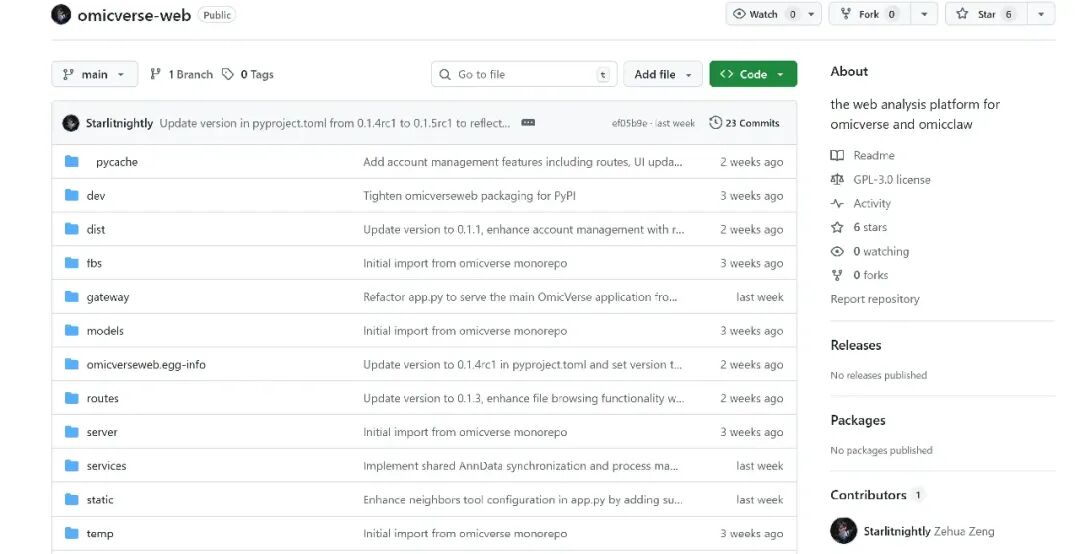
2. 中文帮助文档
https://github.com/Starlitnightly/omicverse-web/blob/main/README_CN.md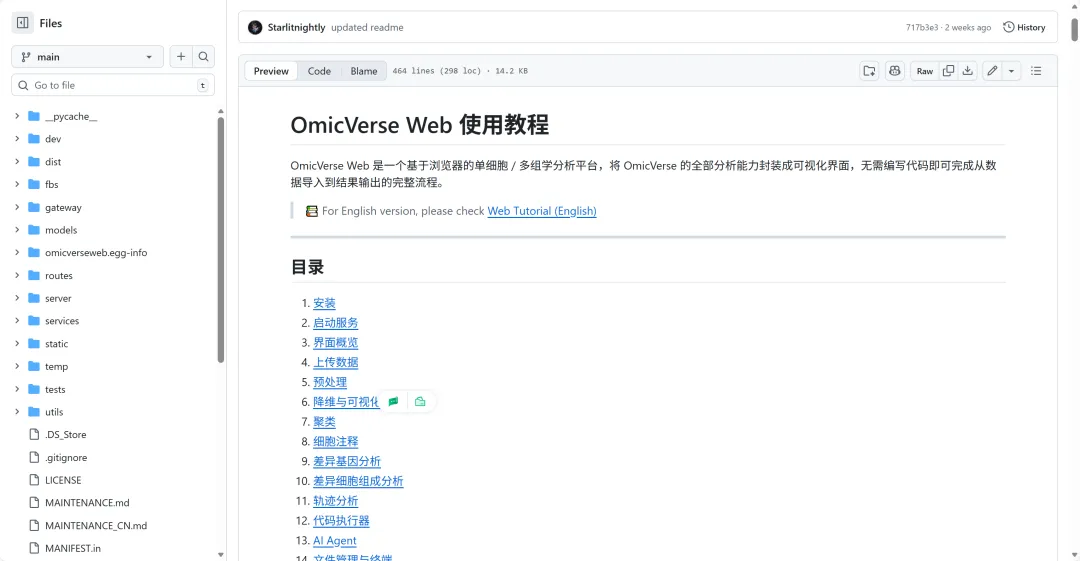
安装教程
在安装的omicverse-web前,我个人还是建议大家创建一个新的环境。
1. 创建环境
mamba create -n omicverseweb python=3.10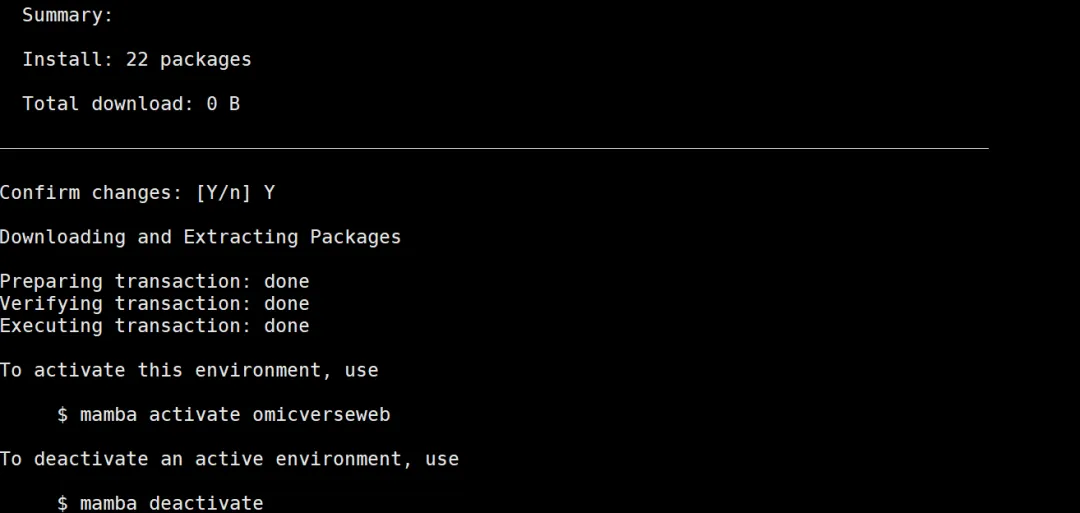
2. 激活环境
mamba activate omicverseweb
3. 安装对应模块
我是在环境中安装omicverse-web,此环境基本没有多余的python包,我们这里参考借鉴安装omicverse的教程,提前安装相关的包(此操作仅供参考)。
安装 PyTorch 和 PyTorch Geometric (PyG):
# 对于 CUDA 支持(使用 'nvcc --version' 检查您的 CUDA 版本)conda install pytorch torchvision torchaudio pytorch-cuda=11.8 -c pytorch -c nvidia# 或仅使用 CPU 安装conda install pytorch torchvision torchaudio cpuonly -c pytorch# 安装 PyTorch Geometricconda install pyg -c pyg4. 安装omicverse-web
在安装omicverse-web时,在我们自己的服务器中,会出现缺失一些Python包,可能每个人遇到的缺失包不一样,你缺失什么包就使用pip安装什么包。
4.1 sympy包版本不对
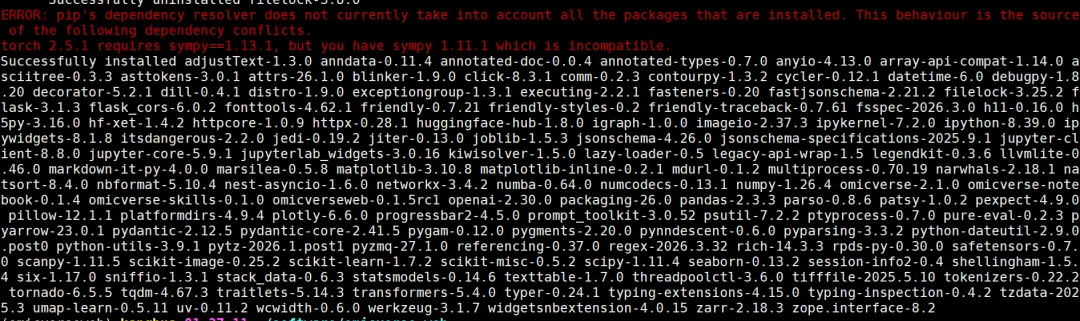
安装对应版本
pip install sympy==1.13.14.2 缺少flatbuffers包
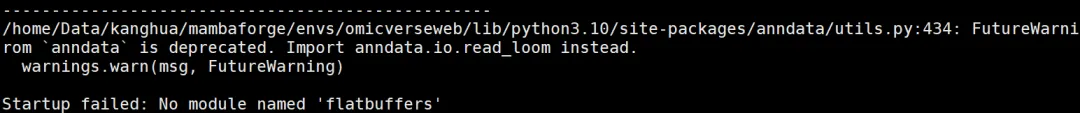
安装
pip install flatbuffers...............
5. 启动omicverse-web
安装完成后,在终端执行:
omicverse-web服务默认在 http://localhost:5050 启动(端口被占用时自动顺延至 5051、5052 …)。看到以下输出即表示启动成功:
* OmicVerse Web running on http://localhost:5050在浏览器中打开该地址即可进入平台。
6. 可选参数
omicverse-web --port 8080# 指定端口omicverse-web --no-debug # 关闭调试模式(生产环境推荐)omicverse-web --remote # 远程模式(配合 SSH 隧道)7. 界面概览
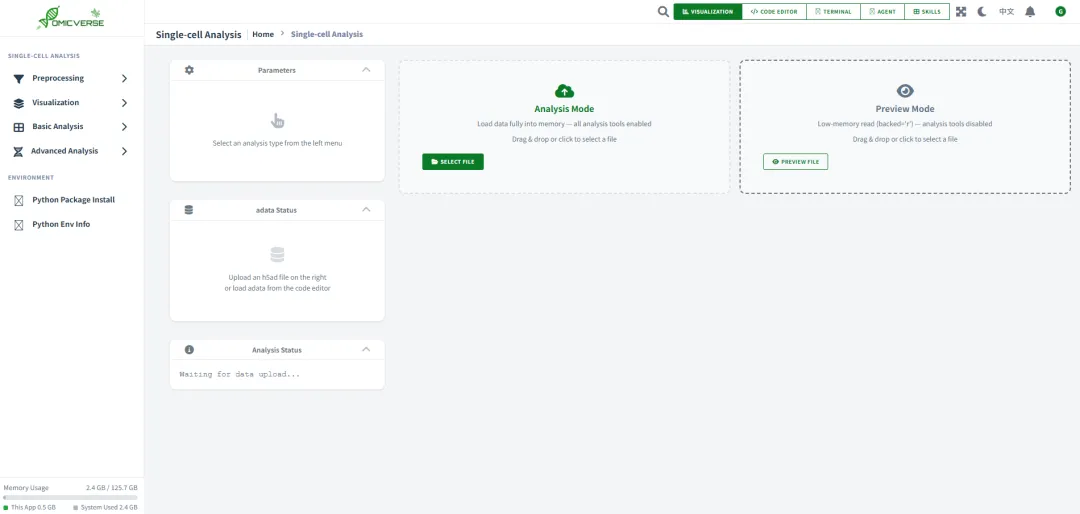
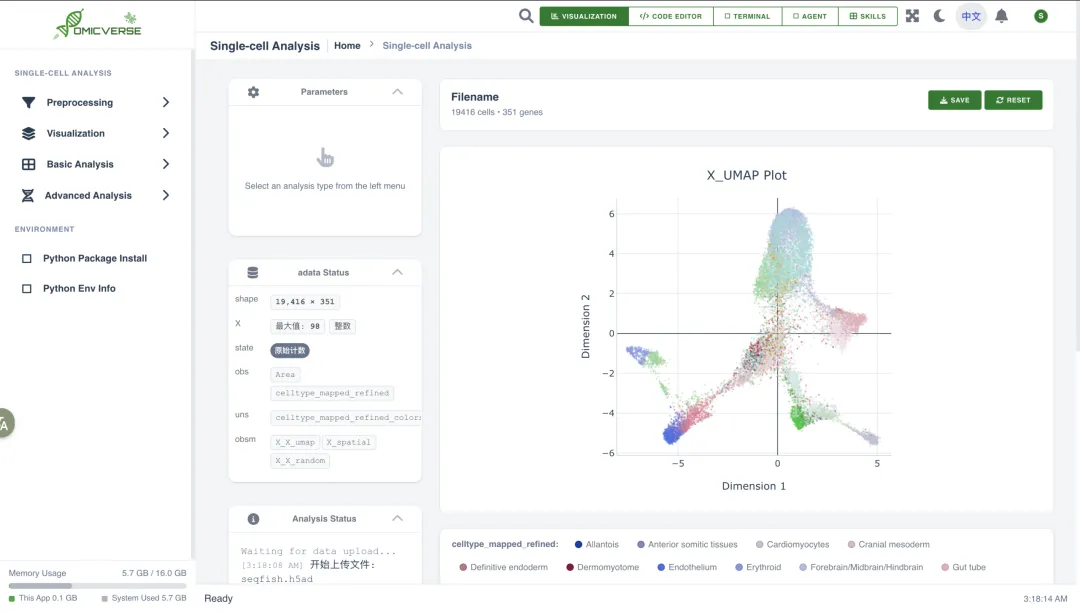
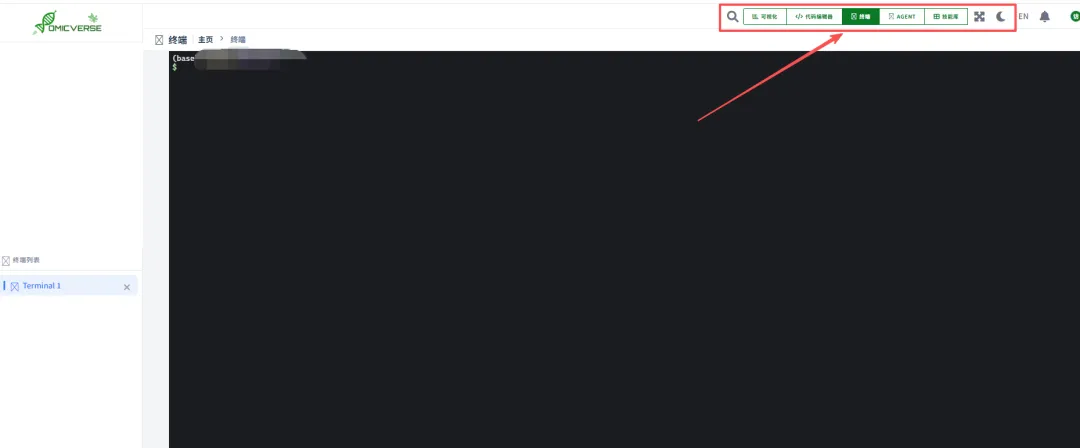
在左上角也有很多的小窗口,供自己使用。
若我们的教程对你有所帮助,请
点赞+收藏+转发,这是对我们最大的支持。
欢迎关注《BioinfoR生信笔记》
关于自我简介可查看「BioinfoR生信筆記」关注须知! BioinfoR生信筆記,仅有微信社群。关于社群请详细查看「BioinfoR生信筆記」入群声明,里面有你想了解的内容。
BioinfoR生信筆記 ,注于分享生物信息学相关知识和R语言绘图教程。发表论文投稿及招聘信息请使用word格式或MarkDown格式发送到bioinfor2025@163.com,均为无偿。
2025已离你我而去,2026加油!!
往期部分文章
1. 最全WGCNA教程(替换数据即可出全部结果与图形)
推荐大家购买最新的教程,若是已经购买以前WGNCA教程的同学,可以在对应教程留言,即可获得最新的教程。(注:此教程也仅基于自己理解,不仅局限于此,难免有不恰当地方,请结合自己需求,进行改动。)
2. 精美图形绘制教程
3. 转录组分析教程
4. 转录组下游分析
BioinfoR生信筆記 ,注于分享生物信息学相关知识和R语言绘图教程。
