相关性分析(基于Python)6—— 皮尔逊相关系数的核心性质与边界约束
- 2026-04-21 07:32:46
1皮尔逊相关系数的基础代数性质
对于总体中的两个随机变量X和Y,总体皮尔逊相关系数的定义为:
其中、分别为X和Y的总体均值,、分别为两者的总体标准差,为两者的总体协方差。
对于样本容量为的样本,样本皮尔逊相关系数的定义为:
其中分别为和的样本均值。
基于上述定义,我们可以直接推导出皮尔逊相关系数的四个基础代数性质。
性质1:对称性
皮尔逊相关系数具有严格的对称性,即交换两个变量的位置,相关系数的数值与符号完全保持不变:
证明:根据协方差的定义,乘法满足交换律,因此 。分母是两个变量标准差的乘积,交换 和 的位置后,乘积结果保持不变。因此整体的比值不会发生任何变化。
样本相关系数的对称性同理,分子的乘积求和项交换 和 的位置后结果不变,分母的平方和乘积同样不受变量顺序影响,因此 。
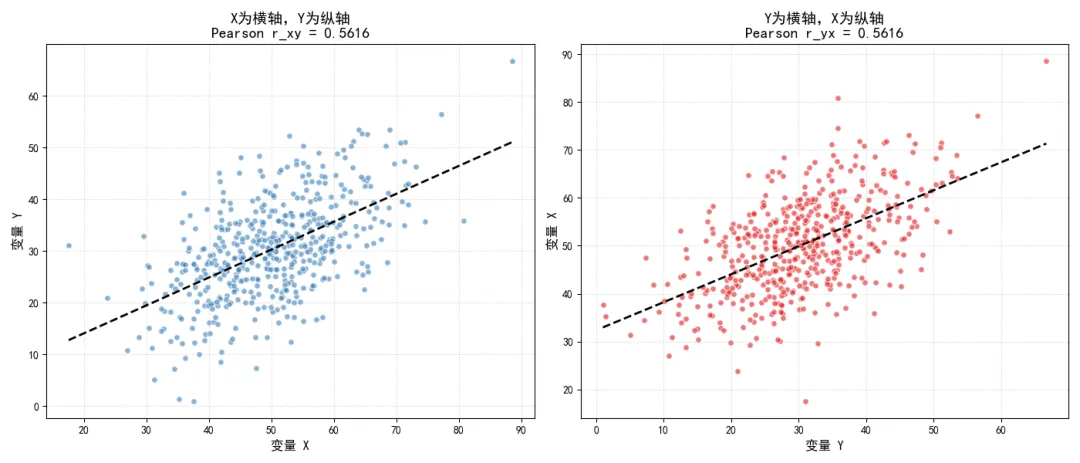
这个性质看说明皮尔逊相关系数度量的是两个变量之间的线性关联强度,不区分自变量与因变量,即无论我们计算身高对体重的相关系数,还是体重对身高的相关系数,得到的结果完全一致。
我们通过一段代码验证这个性质,同时可视化变量交换前后的散点分布与相关系数结果。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子保证可复现
np.random.seed(42)
# 生成具有线性关系的原始数据
n = 500
x = np.random.normal(50, 10, n)
y = 0.6 * x + np.random.normal(0, 8, n)
# 计算两种顺序的相关系数
r_xy, _ = stats.pearsonr(x, y)
r_yx, _ = stats.pearsonr(y, x)
# 创建可视化画布
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(14, 6))
# 绘制X-Y散点图
ax1.scatter(x, y, alpha=0.6, color='#377eb8', s=30, edgecolors='white')
slope1, intercept1, _, _, _ = stats.linregress(x, y)
x_fit1 = np.linspace(min(x), max(x), 100)
ax1.plot(x_fit1, slope1 * x_fit1 + intercept1, color='black', linestyle='--', linewidth=2)
ax1.set_title(f'X为横轴,Y为纵轴\nPearson r_xy = {r_xy:.4f}', fontsize=14)
ax1.set_xlabel('变量 X', fontsize=12)
ax1.set_ylabel('变量 Y', fontsize=12)
ax1.grid(True, linestyle=':', alpha=0.6)
# 绘制Y-X散点图
ax2.scatter(y, x, alpha=0.6, color='#e41a1c', s=30, edgecolors='white')
slope2, intercept2, _, _, _ = stats.linregress(y, x)
x_fit2 = np.linspace(min(y), max(y), 100)
ax2.plot(x_fit2, slope2 * x_fit2 + intercept2, color='black', linestyle='--', linewidth=2)
ax2.set_title(f'Y为横轴,X为纵轴\nPearson r_yx = {r_yx:.4f}', fontsize=14)
ax2.set_xlabel('变量 Y', fontsize=12)
ax2.set_ylabel('变量 X', fontsize=12)
ax2.grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
# 输出验证结果
print(f"Y与X的相关系数r_yx: {r_yx:.6f}")
print(f"两个相关系数是否相等: {np.isclose(r_xy, r_yx)}")
执行结果如下:

性质2:边界性
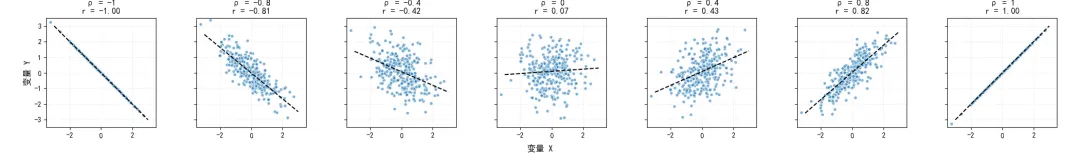
皮尔逊相关系数的取值被严格限制在区间内,即:
当且仅当 与 存在完全线性函数关系时,等号成立。其中 对应完全正线性相关, 对应完全负线性相关。
证明: 该性质可由柯西-施瓦茨不等式导出。对于任意两个具有有限二阶矩的随机变量 和 ,柯西-施瓦茨不等式给出:
将不等式两侧同时开平方,得到:
将不等式两侧同时除以右侧的项,恰好就是皮尔逊相关系数的定义式,因此可以直接得出 。
等号成立的充要条件是柯西-施瓦茨不等式的等号成立条件,即存在常数和,使得以概率1成立。当时,;当时,。
样本相关系数的边界性推导完全一致,只需将期望替换为样本求和,将总体方差替换为样本平方和,最终可以得到的结论。
我们通过代码可视化不同相关系数下的散点分布,直观展示相关系数从到的变化过程,以及完全线性相关的边界情况。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
n = 300
x = np.random.normal(0, 1, n)
# 定义不同的相关系数目标值
rho_list = [-1, -0.8, -0.4, 0, 0.4, 0.8, 1]
fig, axes = plt.subplots(1, 7, figsize=(21, 3), sharey=True)
for ax, rho in zip(axes, rho_list):
# 生成对应相关系数的Y变量
if rho == 1:
y = x
elif rho == -1:
y = -x
else:
# 根据线性关系生成带噪声的Y,保证理论相关系数为rho
y = rho * x + np.random.normal(0, np.sqrt(1 - rho**2), n)
# 计算实际样本相关系数
r, _ = stats.pearsonr(x, y)
# 绘制散点图
ax.scatter(x, y, alpha=0.6, s=20, edgecolors='white')
# 绘制回归线
slope, intercept, _, _, _ = stats.linregress(x, y)
x_fit = np.linspace(-3, 3, 100)
ax.plot(x_fit, slope * x_fit + intercept, color='black', linestyle='--', linewidth=1.5)
ax.set_title(f'ρ = {rho}\nr = {r:.2f}', fontsize=12)
ax.set_xlim(-3.5, 3.5)
ax.set_ylim(-3.5, 3.5)
ax.grid(True, linestyle=':', alpha=0.4)
ax.set_aspect('equal')
axes[0].set_ylabel('变量 Y', fontsize=12)
fig.supxlabel('变量 X', fontsize=12)
plt.tight_layout()
plt.show()
执行结果如下:
性质3:标准化变量的协方差等价性
若对 和 进行Z-Score标准化,得到标准化变量 和 :
则标准化变量的协方差,与原始变量的皮尔逊相关系数完全相等:
证明: 首先计算标准化变量的期望与方差。根据期望的线性性质,
同理 。根据方差的性质,
同理 。
根据协方差的定义,
将 和 的表达式代入:
样本层面的推导完全一致,标准化后的样本变量 和 ,其样本协方差与样本相关系数完全相等。
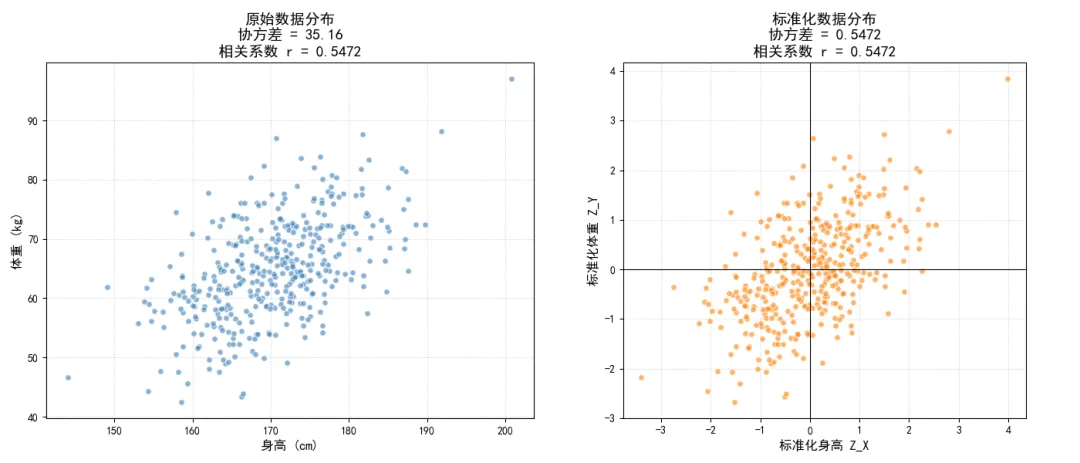
这个性质表明皮尔逊相关系数是剔除了变量自身尺度与位置影响后,纯粹的线性协同波动程度。
我们通过代码验证这个等价性,同时对比原始数据与标准化数据的分布变化。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 生成带量纲差异的原始数据
n = 400
# X为身高数据,单位厘米,均值170,标准差8
x = np.random.normal(170, 8, n)
# Y为体重数据,单位千克,均值65,标准差10
y = 0.7 * x + np.random.normal(0, 7, n) - 54
# 计算原始数据的相关系数与协方差
r_original, _ = stats.pearsonr(x, y)
Cov_original = np.cov(x, y, ddof=1)[0, 1]
# 对数据进行Z-Score标准化
z_x = (x - np.mean(x)) / np.std(x, ddof=1)
z_y = (y - np.mean(y)) / np.std(y, ddof=1)
# 计算标准化数据的相关系数与协方差
r_standardized, _ = stats.pearsonr(z_x, z_y)
Cov_standardized = np.cov(z_x, z_y, ddof=1)[0, 1]
# 创建可视化画布
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(14, 6))
# 绘制原始数据散点图
ax1.scatter(x, y, alpha=0.6, color='#377eb8', s=30, edgecolors='white')
ax1.set_title(f'原始数据分布\n协方差 = {Cov_original:.2f}\n相关系数 r = {r_original:.4f}', fontsize=14)
ax1.set_xlabel('身高 (cm)', fontsize=12)
ax1.set_ylabel('体重 (kg)', fontsize=12)
ax1.grid(True, linestyle=':', alpha=0.6)
# 绘制标准化数据散点图
ax2.scatter(z_x, z_y, alpha=0.6, color='#ff7f00', s=30, edgecolors='white')
ax2.axhline(0, color='black', lw=0.8)
ax2.axvline(0, color='black', lw=0.8)
ax2.set_title(f'标准化数据分布\n协方差 = {Cov_standardized:.4f}\n相关系数 r = {r_standardized:.4f}', fontsize=14)
ax2.set_xlabel('标准化身高 Z_X', fontsize=12)
ax2.set_ylabel('标准化体重 Z_Y', fontsize=12)
ax2.grid(True, linestyle=':', alpha=0.6)
ax2.set_aspect('equal')
plt.tight_layout()
plt.show()
# 输出验证结果
print(f"原始数据协方差: {Cov_original:.4f}")
print(f"原始数据相关系数: {r_original:.6f}")
print(f"标准化数据协方差: {Cov_standardized:.6f}")
print(f"标准化数据相关系数: {r_standardized:.6f}")
print(f"标准化协方差与原始相关系数是否相等: {np.isclose(Cov_standardized, r_original)}")
执行结果如下:
性质4:独立变量的相关系数为0
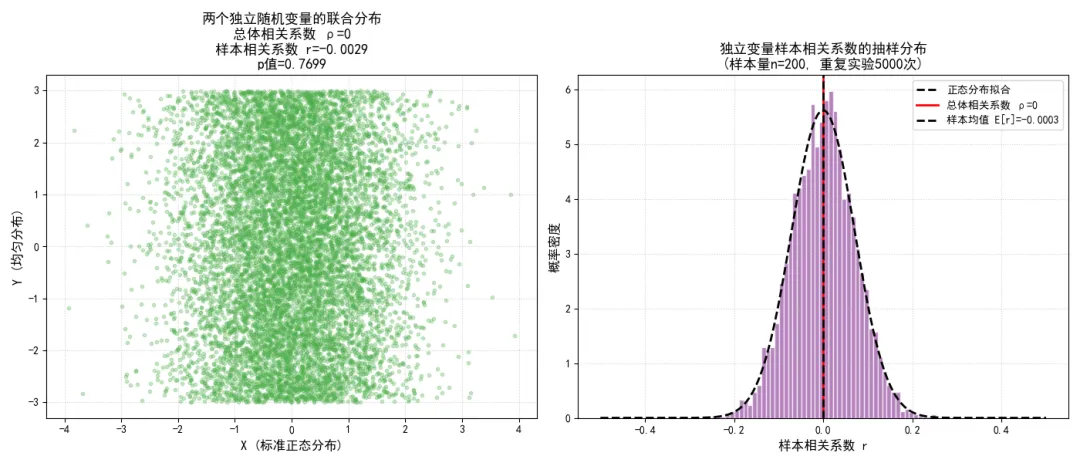
若随机变量 和 统计独立,则两者的总体皮尔逊相关系数。
证明: 根据统计独立性的定义,若 和 相互独立,则 。
将其代入协方差的展开式:
协方差为0,因此皮尔逊相关系数。
需要特别强调的是,这个性质的逆命题并不成立。相关系数为0仅能说明两个变量不存在线性依赖关系,无法证明它们相互独立,变量之间可能存在极强的非线性依赖关系,同时保持相关系数为0。
我们通过代码模拟两个独立的随机变量,验证其相关系数的分布特征,同时展示独立变量的联合分布形态。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 生成两个完全独立的随机变量
n = 10000
# X服从标准正态分布
x = np.random.normal(0, 1, n)
# Y服从均匀分布,与X完全独立
y = np.random.uniform(-3, 3, n)
# 计算样本相关系数
r, p_value = stats.pearsonr(x, y)
# 重复抽样实验,展示相关系数的抽样分布
n_experiments = 5000
sample_size = 200
r_distribution = np.zeros(n_experiments)
for i in range(n_experiments):
x_sample = np.random.normal(0, 1, sample_size)
y_sample = np.random.uniform(-3, 3, sample_size)
r_sample, _ = stats.pearsonr(x_sample, y_sample)
r_distribution[i] = r_sample
# 创建可视化画布
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(14, 6))
# 绘制独立变量的联合散点图
ax1.scatter(x, y, alpha=0.3, s=10, color='#4daf4a')
ax1.set_title(f'两个独立随机变量的联合分布\n总体相关系数 ρ=0\n样本相关系数 r={r:.4f}\np值={p_value:.4f}', fontsize=13)
ax1.set_xlabel('X (标准正态分布)', fontsize=12)
ax1.set_ylabel('Y (均匀分布)', fontsize=12)
ax1.grid(True, linestyle=':', alpha=0.6)
# 绘制相关系数的抽样分布直方图
ax2.hist(r_distribution, bins=50, density=True, alpha=0.7, color='#984ea3', edgecolor='white')
# 绘制正态分布拟合曲线
mean_r = np.mean(r_distribution)
std_r = np.std(r_distribution)
x_grid = np.linspace(-0.5, 0.5, 200)
pdf = stats.norm.pdf(x_grid, loc=mean_r, scale=std_r)
ax2.plot(x_grid, pdf, 'k--', linewidth=2, label='正态分布拟合')
# 标注总体相关系数0的位置
ax2.axvline(0, color='red', linestyle='-', linewidth=2, label='总体相关系数 ρ=0')
ax2.axvline(mean_r, color='black', linestyle='--', linewidth=2, label=f'样本均值 E[r]={mean_r:.4f}')
ax2.set_title(f'独立变量样本相关系数的抽样分布\n(样本量n={sample_size}, 重复实验{n_experiments}次)', fontsize=13)
ax2.set_xlabel('样本相关系数 r', fontsize=12)
ax2.set_ylabel('概率密度', fontsize=12)
ax2.legend()
ax2.grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
执行结果如下:
2线性变换下的不变性与符号规则
皮尔逊相关系数最具实用价值的性质之一,是它对变量的线性变换具有严格的不变性。
我们先定义变量的线性变换。对于随机变量 和 ,我们构造两个新的随机变量 和 :
其中 为任意常数,且 (若 或 为,变换后的变量为常数,方差为,无法计算相关系数)。
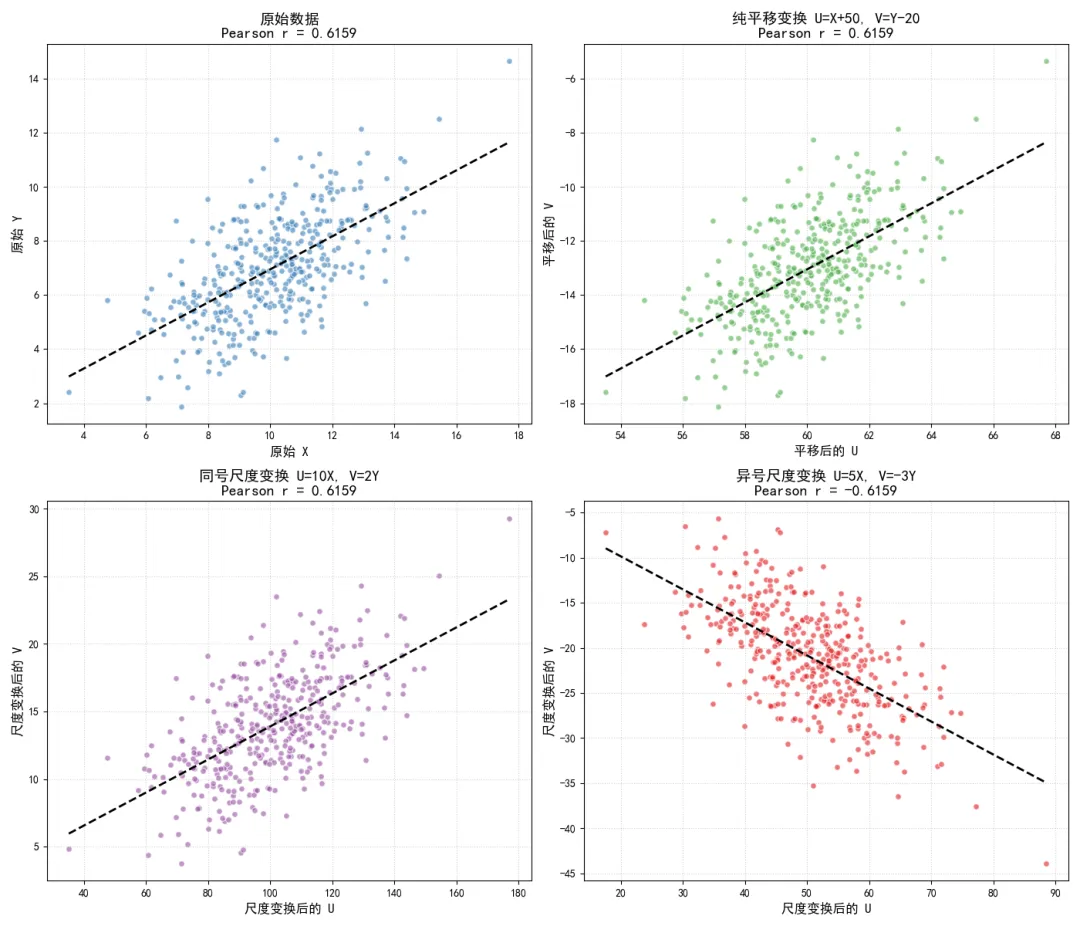
核心结论是:对变量进行任意线性变换,皮尔逊相关系数的绝对值保持不变,符号仅由两个变量的尺度变换系数的乘积符号决定。平移变换对相关系数无任何影响。
我们分两步完成这个结论的严谨推导。
性质1:平移变换的绝对不变性
当尺度系数 时,线性变换退化为纯平移变换:
此时可以证明,变换后的相关系数与原始相关系数完全相等:
证明: 首先计算 和 的期望:
去中心化后的偏差项为:
可以看到,平移变换完全不改变变量去中心化后的偏差项。因此协方差保持不变:
同时,平移变换也不改变变量的方差:
协方差与方差均未发生变化,因此相关系数。
这个性质的实践意义极强。它说明,对变量进行任何平移操作,比如将摄氏度转换为开尔文温度(加273.15)、将日期转换为距离某一天的天数、对收入数据进行常数项调整,都完全不会改变变量之间的皮尔逊相关系数。
性质2:尺度变换的符号规则与绝对值不变性
当平移系数 时,线性变换退化为纯尺度变换:
此时变换后的相关系数为:
其中为符号函数,当括号内的数值大于时返回,小于时返回。
证明: 首先计算 和 的期望与去中心化偏差:
计算协方差:
计算方差:
将协方差与标准差代入相关系数定义式:
上述结果表明:尺度变换不会改变相关系数的绝对值,即无论我们将变量放大或缩小多少倍,相关系数的绝对值始终保持不变;尺度变换仅会改变相关系数的符号,即当两个变量的尺度系数乘积为正(同号)时,相关系数符号不变;当乘积为负(异号)时,相关系数符号反转。
完整线性变换的综合性质
结合平移变换与尺度变换的性质,我们可以得到完整线性变换下的最终结论。对于任意线性变换 ,变换后的相关系数为:
平移系数 和 完全不影响最终的相关系数,只有尺度系数 和 会影响相关系数的符号,且不会改变其绝对值。
这个性质直接解释了为什么相关系数是无量纲的统计量,因此我们不需要考虑变量的量纲差异,就可以直接比较不同变量对之间的相关强度。
我们通过代码模拟三种典型的线性变换场景,可视化变换前后的散点分布与相关系数变化,验证上述性质。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 生成原始数据
n = 400
x = np.random.normal(10, 2, n)
y = 0.7 * x + np.random.normal(0, 1.5, n)
r_original, _ = stats.pearsonr(x, y)
# 场景1:纯平移变换
u1 = x + 50# X加50
v1 = y - 20# Y减20
r1, _ = stats.pearsonr(u1, v1)
# 场景2:同号尺度变换
u2 = 10 * x # X放大10倍
v2 = 2 * y # Y放大2倍
r2, _ = stats.pearsonr(u2, v2)
# 场景3:异号尺度变换
u3 = 5 * x # X放大5倍
v3 = -3 * y # Y放大3倍并反转符号
r3, _ = stats.pearsonr(u3, v3)
# 创建可视化画布
fig, axes = plt.subplots(2, 2, figsize=(14, 12))
axes = axes.flatten()
# 绘制原始数据
axes[0].scatter(x, y, alpha=0.6, color='#377eb8', s=30, edgecolors='white')
slope, intercept, _, _, _ = stats.linregress(x, y)
x_fit = np.linspace(min(x), max(x), 100)
axes[0].plot(x_fit, slope * x_fit + intercept, color='black', linestyle='--', linewidth=2)
axes[0].set_title(f'原始数据\nPearson r = {r_original:.4f}', fontsize=14)
axes[0].set_xlabel('原始 X', fontsize=12)
axes[0].set_ylabel('原始 Y', fontsize=12)
axes[0].grid(True, linestyle=':', alpha=0.6)
# 绘制纯平移变换数据
axes[1].scatter(u1, v1, alpha=0.6, color='#4daf4a', s=30, edgecolors='white')
slope1, intercept1, _, _, _ = stats.linregress(u1, v1)
x_fit1 = np.linspace(min(u1), max(u1), 100)
axes[1].plot(x_fit1, slope1 * x_fit1 + intercept1, color='black', linestyle='--', linewidth=2)
axes[1].set_title(f'纯平移变换 U=X+50, V=Y-20\nPearson r = {r1:.4f}', fontsize=14)
axes[1].set_xlabel('平移后的 U', fontsize=12)
axes[1].set_ylabel('平移后的 V', fontsize=12)
axes[1].grid(True, linestyle=':', alpha=0.6)
# 绘制同号尺度变换数据
axes[2].scatter(u2, v2, alpha=0.6, color='#984ea3', s=30, edgecolors='white')
slope2, intercept2, _, _, _ = stats.linregress(u2, v2)
x_fit2 = np.linspace(min(u2), max(u2), 100)
axes[2].plot(x_fit2, slope2 * x_fit2 + intercept2, color='black', linestyle='--', linewidth=2)
axes[2].set_title(f'同号尺度变换 U=10X, V=2Y\nPearson r = {r2:.4f}', fontsize=14)
axes[2].set_xlabel('尺度变换后的 U', fontsize=12)
axes[2].set_ylabel('尺度变换后的 V', fontsize=12)
axes[2].grid(True, linestyle=':', alpha=0.6)
# 绘制异号尺度变换数据
axes[3].scatter(u3, v3, alpha=0.6, color='#e41a1c', s=30, edgecolors='white')
slope3, intercept3, _, _, _ = stats.linregress(u3, v3)
x_fit3 = np.linspace(min(u3), max(u3), 100)
axes[3].plot(x_fit3, slope3 * x_fit3 + intercept3, color='black', linestyle='--', linewidth=2)
axes[3].set_title(f'异号尺度变换 U=5X, V=-3Y\nPearson r = {r3:.4f}', fontsize=14)
axes[3].set_xlabel('尺度变换后的 U', fontsize=12)
axes[3].set_ylabel('尺度变换后的 V', fontsize=12)
axes[3].grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
# 输出验证结果
print(f"原始数据相关系数: {r_original:.6f}")
print(f"纯平移变换后相关系数: {r1:.6f} (与原始相等: {np.isclose(r1, r_original)})")
print(f"同号尺度变换后相关系数: {r2:.6f} (与原始相等: {np.isclose(r2, r_original)})")
print(f"异号尺度变换后相关系数: {r3:.6f} (与原始符号相反、绝对值相等: {np.isclose(np.abs(r3), np.abs(r_original))})")
执行结果如下:
3几何性质与线性回归的内在关联
3.1 相关系数与向量夹角的严格对应
在容量为 的样本空间中,我们可以将两个变量的观测值映射为n维欧几里得空间中的两个向量:
这两个向量是原始数据去中心化后的结果,向量的起点位于样本空间的原点,每个分量对应一个样本的观测偏差。
根据线性代数的定义,两个向量的内积等于向量模长的乘积乘以向量夹角的余弦值:
其中 为两个向量在 维空间中的夹角,取值范围为。
我们将内积与模长的表达式展开:
将上述表达式代入内积公式,两侧同时除以,可以得到:
上述结果表明:样本皮尔逊相关系数,等于n维样本空间中两个去中心化数据向量夹角的余弦值。
当 时,,两个向量完全共线且同向,对应完全正线性相关;当 时,,两个向量在 维空间中相互正交,对应无线性相关关系;当 时,,两个向量完全共线且反向,对应完全负线性相关。
3.2 相关系数与线性回归系数的代数关系
一元线性回归中,我们试图用X的线性函数来拟合 ,拟合方程为:
其中 为 对 的回归系数,代表 每变化一个单位, 的平均变化量; 为截距项。
根据最小二乘法,回归系数 的最优估计值为:
我们将这个公式与皮尔逊相关系数的定义式结合,可以推导出回归系数与相关系数的内在关联:
其中 和 分别为 和 的样本标准差。
同理,若我们用 来拟合 ,得到 对 的回归系数:
从这两个公式可以得出以下结论:一是回归系数的符号与相关系数的符号完全一致;二是回归系数的大小由相关系数和两个变量的标准差之比共同决定,相关系数反映了线性关系的紧密程度,标准差之比则反映了两个变量的尺度差异;三是两个方向的回归系数的乘积,等于相关系数的平方:
这个结论表明相关系数它是两个方向回归系数的几何均值。
3.3 相关系数的平方与决定系数
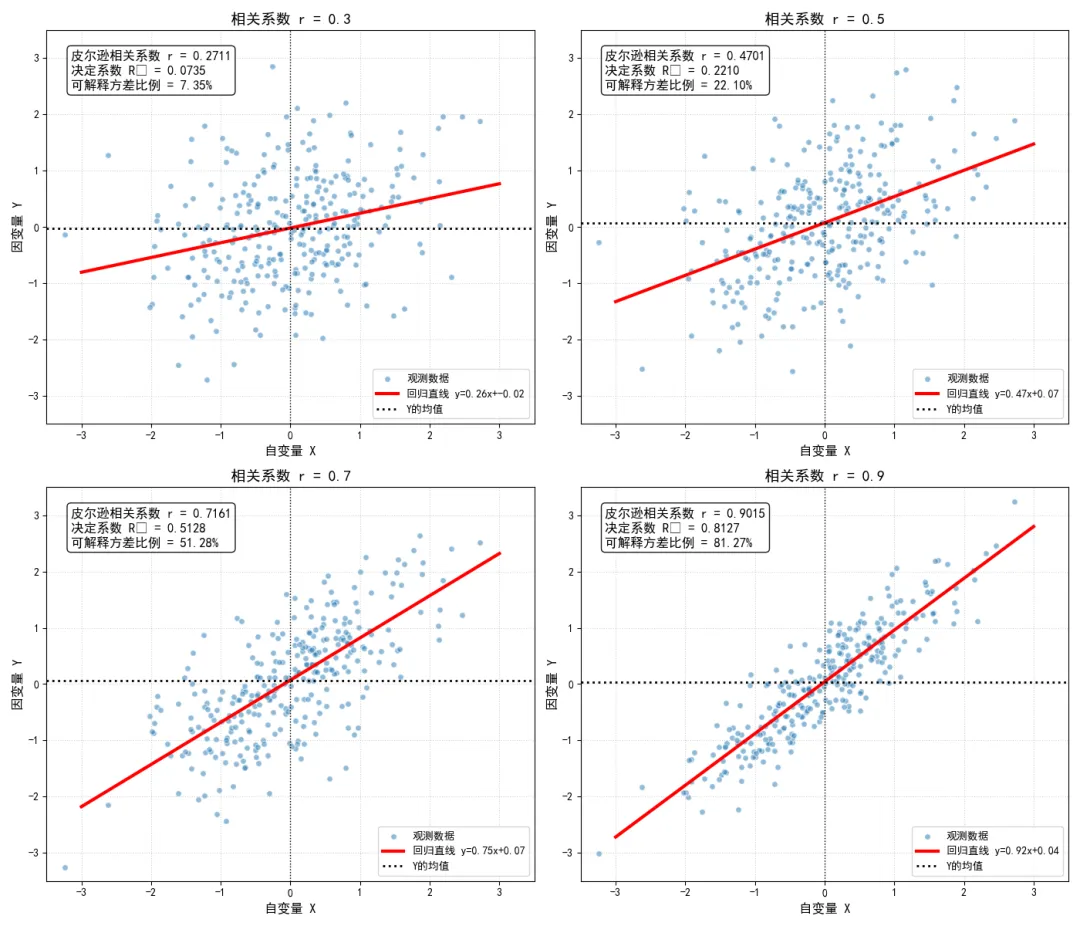
在线性回归中,决定系数 是评估模型拟合效果的核心指标,它代表了因变量的总方差中,能够被自变量的线性关系解释的比例。
我们可以将Y的总方差拆解为两部分:
等式左侧为总平方和SST,代表 的总波动;右侧第一项为回归平方和SSR,代表模型能够解释的波动;第二项为残差平方和SSE,代表模型无法解释的随机波动。
决定系数 的定义为:
我们可以通过严格的代数推导证明,在一元线性回归中,决定系数 恰好等于皮尔逊相关系数的平方:
证明: 根据回归方程的拟合值,可以得到。 将其代入回归平方和SSR:
将代入,同时,即:
而总平方和SST = 。 因此:
这个推导表明:相关系数的平方,代表了两个变量之间线性关系能够解释的方差比例。
当 时,,说明 的方差中有 可以被 的线性关系解释;当 时,,说明仅有 的方差可以被解释,即使相关系数在统计上显著,其实际的解释能力也非常有限。
我们通过代码可视化相关系数、回归系数、决定系数三者之间的关系,直观展示不同相关系数下的回归拟合效果与方差解释率。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
n = 300
x = np.random.normal(0, 1, n)
# 定义不同的相关系数目标值
rho_list = [0.3, 0.5, 0.7, 0.9]
fig, axes = plt.subplots(2, 2, figsize=(14, 12))
axes = axes.flatten()
for ax, rho in zip(axes, rho_list):
# 生成对应相关系数的Y变量
y = rho * x + np.random.normal(0, np.sqrt(1 - rho**2), n)
# 计算相关系数、回归系数、决定系数
r, _ = stats.pearsonr(x, y)
slope, intercept, r_value, p_value, std_err = stats.linregress(x, y)
r_squared = r_value ** 2
# 生成拟合线与置信区间
x_fit = np.linspace(-3, 3, 100)
y_fit = slope * x_fit + intercept
# 绘制散点图
ax.scatter(x, y, alpha=0.5, s=30, edgecolors='white', label='观测数据')
# 绘制回归线
ax.plot(x_fit, y_fit, color='red', linestyle='-', linewidth=3, label=f'回归直线 y={slope:.2f}x+{intercept:.2f}')
# 绘制均值基准线
ax.axhline(np.mean(y), color='black', linestyle=':', linewidth=2, label='Y的均值')
ax.axvline(0, color='black', linestyle=':', linewidth=1)
# 添加统计信息文本
info_text = (
f"皮尔逊相关系数 r = {r:.4f}\n"
f"决定系数 R² = {r_squared:.4f}\n"
f"可解释方差比例 = {r_squared*100:.2f}%"
)
ax.text(0.05, 0.95, info_text, transform=ax.transAxes, fontsize=12,
verticalalignment='top', bbox=dict(boxstyle='round', facecolor='white', alpha=0.9))
ax.set_title(f'相关系数 r = {rho}', fontsize=14)
ax.set_xlabel('自变量 X', fontsize=12)
ax.set_ylabel('因变量 Y', fontsize=12)
ax.set_xlim(-3.5, 3.5)
ax.set_ylim(-3.5, 3.5)
ax.grid(True, linestyle=':', alpha=0.6)
ax.legend(loc='lower right')
plt.tight_layout()
plt.show()
执行结果如下:
4样本相关系数的抽样性质与偏差校正
性质1:一致性
样本相关系数 是总体相关系数 的一致估计量。即当样本量 趋向于无穷大时, 依概率收敛于:
证明: 根据大数定律,样本协方差依概率收敛于总体协方差;样本标准差、依概率收敛于总体标准差、。
根据连续映射定理,随机变量序列的连续函数的极限,等于随机变量极限的连续函数。皮尔逊相关系数是协方差与标准差的连续函数,因此:
这个性质表明,只要样本量足够大,样本相关系数会无限接近总体的真实相关系数。无论总体相关系数的真实值是多少,随着样本量的增加,抽样误差会逐渐缩小,估计结果会越来越稳定。
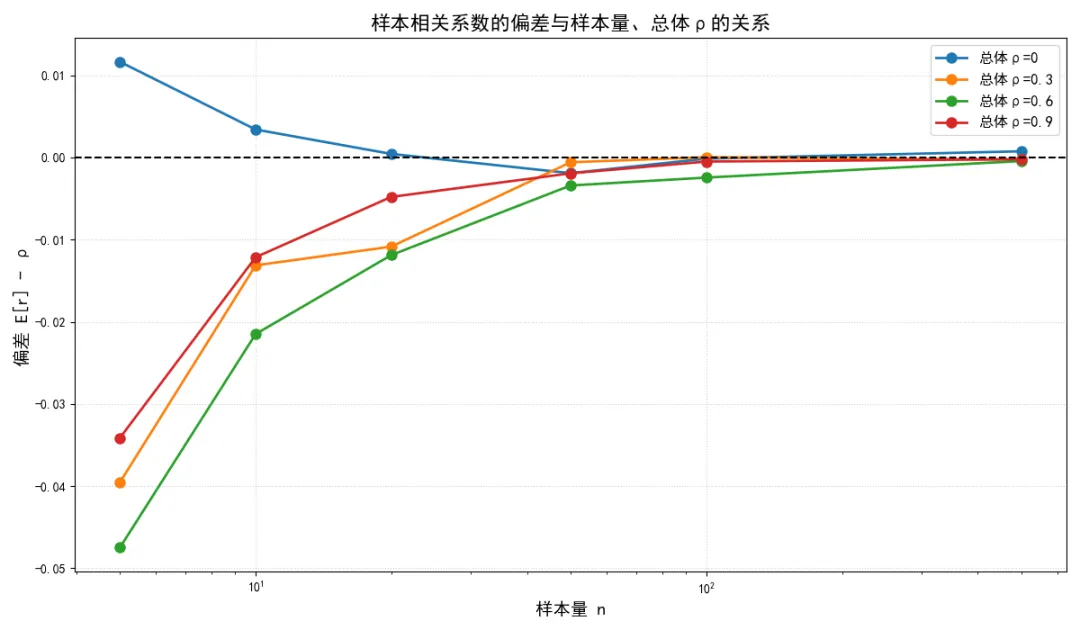
性质2:有偏性
样本相关系数 是总体相关系数 的有偏估计量。即样本相关系数的期望不等于总体真实相关系数:
偏差的来源与样本量和总体相关系数的大小密切相关。当样本量较小时,偏差会非常明显,尤其是当 时,偏差会急剧增大;当 时,样本相关系数 的期望 ,此时估计是无偏的;当 时,样本相关系数的绝对值会系统性地小于总体相关系数的绝对值,即 ;随着样本量 的增大,偏差会逐渐趋近于,这与一致性的结论一致。
我们可以通过模拟实验直观展示这种偏差的存在,以及样本量和总体相关系数对偏差大小的影响。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
import time
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 实验参数设置
n_experiments = 5000# 减少到5000次实验(仍具有统计意义)
rho_list = [0, 0.3, 0.6, 0.9] # 总体相关系数
sample_sizes = [5, 10, 20, 50, 100, 500] # 不同样本量
print("开始模拟...")
start_time = time.time()
# 存储结果
bias_results = np.zeros((len(rho_list), len(sample_sizes)))
# 进行模拟实验 - 内存友好版本
for i, rho in enumerate(rho_list):
print(f"正在处理 ρ={rho}...")
for j, n in enumerate(sample_sizes):
r_values = np.zeros(n_experiments)
# 方式1:直接循环,每次只生成当前实验的数据(内存友好)
for k in range(n_experiments):
# 生成二元正态分布数据(使用更简单的方法)
x = np.random.randn(n)
# 使用条件分布生成相关数据:y = ρ*x + √(1-ρ²)*ε
epsilon = np.random.randn(n)
y = rho * x + np.sqrt(1 - rho ** 2) * epsilon
# 计算相关系数
r_values[k] = np.corrcoef(x, y)[0, 1]
# 计算偏差
mean_r = np.mean(r_values)
bias = mean_r - rho
bias_results[i, j] = bias
print(f" 样本量 n={n}: 偏差={bias:.6f}")
end_time = time.time()
print(f"\n模拟完成!总耗时: {end_time - start_time:.2f} 秒")
# 可视化偏差结果
fig, ax = plt.subplots(figsize=(12, 7))
for i, rho in enumerate(rho_list):
ax.plot(sample_sizes, bias_results[i, :], marker='o', linewidth=2,
markersize=8, label=f'总体ρ={rho}')
# 绘制零偏差基准线
ax.axhline(0, color='black', linestyle='--', linewidth=1.5)
ax.set_title('样本相关系数的偏差与样本量、总体ρ的关系', fontsize=16)
ax.set_xlabel('样本量 n', fontsize=14)
ax.set_ylabel('偏差 E[r] - ρ', fontsize=14)
ax.set_xscale('log')
ax.grid(True, linestyle=':', alpha=0.6)
ax.legend(fontsize=12)
plt.tight_layout()
plt.show()
# 输出偏差数值表
print("\n样本相关系数的偏差表 (行:总体ρ,列:样本量n)")
print("样本量:", sample_sizes)
print(np.round(bias_results, 6))
执行结果如下:
偏差校正方法
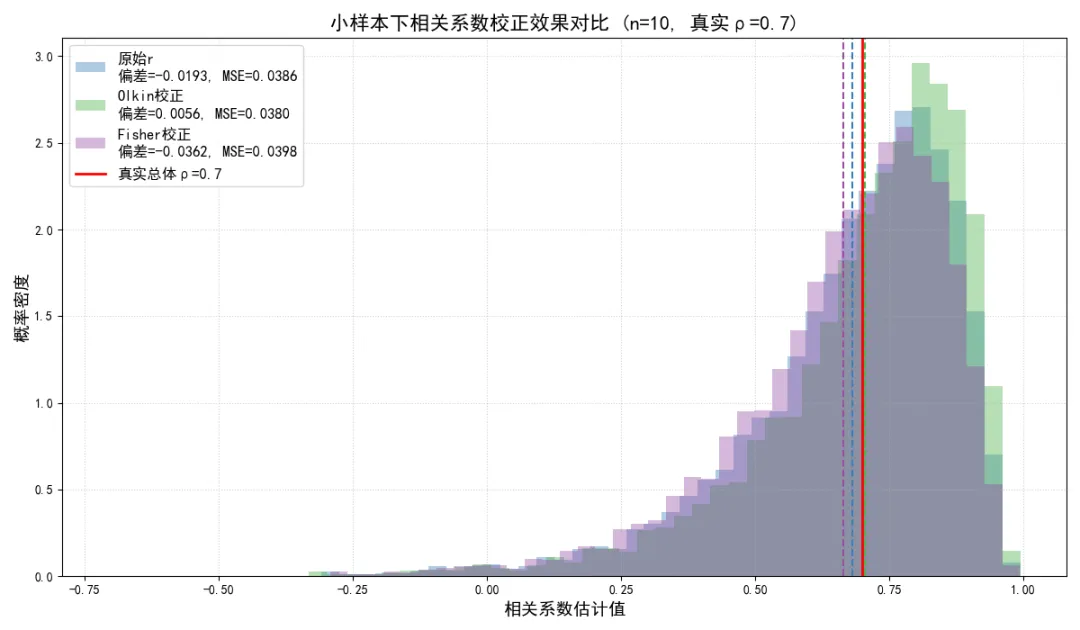
在小样本场景下,样本相关系数的偏差会对分析结果产生显著影响,因此需要对r进行偏差校正,得到更接近总体真实ρ的估计值。
目前应用最广泛的是Olkin & Pratt 提出的近似无偏校正公式:
这个公式适用于 的场景,能够有效减小小样本下的偏差。
另一种常用的校正方法是基于Fisher Z变换的校正。我们先对 进行Fisher Z变换得到 ,对 进行偏差校正后,再通过反变换得到校正后的相关系数。校正公式为:
我们通过模拟实验对比两种校正方法的效果,验证它们对偏差的改善程度。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 实验参数
rho_true = 0.7
sample_size = 10
n_experiments = 10000
# 存储结果
r_raw = np.zeros(n_experiments)
r_olkin = np.zeros(n_experiments)
r_fisher = np.zeros(n_experiments)
# 模拟实验
for i in range(n_experiments):
# 生成数据
cov_matrix = [[1, rho_true], [rho_true, 1]]
data = np.random.multivariate_normal([0, 0], cov_matrix, size = sample_size)
r, _ = stats.pearsonr(data[:, 0], data[:, 1])
# 原始相关系数
r_raw[i] = r
# Olkin & Pratt校正
if sample_size > 4:
r_olkin[i] = r * (1 + (1 - r ** 2) / (2 * (sample_size - 4)))
else:
r_olkin[i] = r
# Fisher Z变换校正
z_r = np.arctanh(np.clip(r, -0.99999, 0.99999))
z_corrected = z_r - r / (2 * (sample_size - 1))
r_fisher[i] = np.tanh(z_corrected)
# 计算偏差与均方误差
bias_raw = np.mean(r_raw) - rho_true
bias_olkin = np.mean(r_olkin) - rho_true
bias_fisher = np.mean(r_fisher) - rho_true
mse_raw = np.mean((r_raw - rho_true) ** 2)
mse_olkin = np.mean((r_olkin - rho_true) ** 2)
mse_fisher = np.mean((r_fisher - rho_true) ** 2)
# 可视化分布对比
fig, ax = plt.subplots(figsize=(12, 7))
# 绘制直方图
ax.hist(r_raw, bins=50, density=True, alpha=0.4, color='#377eb8',
label=f'原始r\n偏差={bias_raw:.4f}, MSE={mse_raw:.4f}')
ax.hist(r_olkin, bins=50, density=True, alpha=0.4, color='#4daf4a',
label=f'Olkin校正\n偏差={bias_olkin:.4f}, MSE={mse_olkin:.4f}')
ax.hist(r_fisher, bins=50, density=True, alpha=0.4, color='#984ea3',
label=f'Fisher校正\n偏差={bias_fisher:.4f}, MSE={mse_fisher:.4f}')
# 绘制真实ρ的基准线
ax.axvline(rho_true, color='red', linestyle='-', linewidth=2, label=f'真实总体ρ={rho_true}')
# 绘制各方法的均值
ax.axvline(np.mean(r_raw), color='#377eb8', linestyle='--', linewidth=1.5)
ax.axvline(np.mean(r_olkin), color='#4daf4a', linestyle='--', linewidth=1.5)
ax.axvline(np.mean(r_fisher), color='#984ea3', linestyle='--', linewidth=1.5)
ax.set_title(f'小样本下相关系数校正效果对比 (n={sample_size}, 真实ρ={rho_true})', fontsize=16)
ax.set_xlabel('相关系数估计值', fontsize=14)
ax.set_ylabel('概率密度', fontsize=14)
ax.legend(fontsize=12)
ax.grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
执行结果如下:
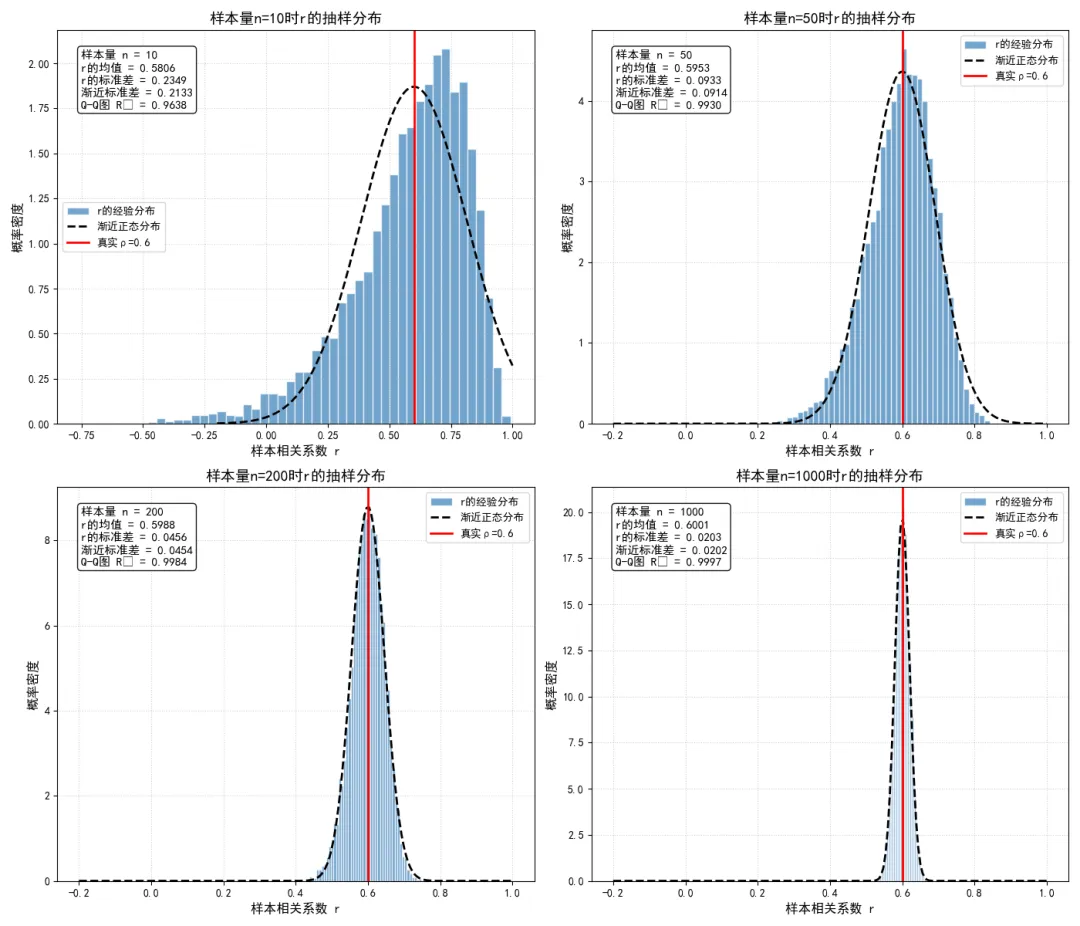
性质3:渐近正态性
当样本量 足够大时,样本相关系数 的抽样分布近似服从正态分布:
其中表示依分布收敛。
需要特别强调的是,这个渐近正态性仅在大样本下成立。当样本量较小,或者 时, 的抽样分布会呈现出强烈的偏态,完全不符合正态分布,此时须使用Fisher Z变换进行分布正态化。
我们通过代码对比不同样本量下, 的抽样分布与渐近正态分布的拟合效果,验证渐近正态性的适用条件。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 实验参数
rho_true = 0.6
sample_sizes = [10, 50, 200, 1000]
n_experiments = 10000
# 创建可视化画布
fig, axes = plt.subplots(2, 2, figsize=(14, 12))
axes = axes.flatten()
for ax, n in zip(axes, sample_sizes):
# 模拟生成样本相关系数
r_values = np.zeros(n_experiments)
for i in range(n_experiments):
cov_matrix = [[1, rho_true], [rho_true, 1]]
data = np.random.multivariate_normal([0, 0], cov_matrix, size = n)
r, _ = stats.pearsonr(data[:, 0], data[:, 1])
r_values[i] = r
# 计算渐近正态分布的参数
mean_asym = rho_true
std_asym = (1 - rho_true ** 2) / np.sqrt(n - 1)
# 绘制直方图
ax.hist(r_values, bins=50, density=True, alpha=0.7, color='#377eb8', edgecolor='white', label='r的经验分布')
# 绘制渐近正态分布曲线
x_grid = np.linspace(-0.2, 1.0, 200)
pdf_asym = stats.norm.pdf(x_grid, loc=mean_asym, scale=std_asym)
ax.plot(x_grid, pdf_asym, 'k--', linewidth=2, label='渐近正态分布')
# 绘制真实ρ的基准线
ax.axvline(rho_true, color='red', linestyle='-', linewidth=2, label=f'真实ρ={rho_true}')
# 计算Q-Q图的R²,评估正态拟合度
_, (_, _, r_squared) = stats.probplot(r_values, dist="norm", fit=True)
# 添加统计信息
info_text = (
f"样本量 n = {n}\n"
f"r的均值 = {np.mean(r_values):.4f}\n"
f"r的标准差 = {np.std(r_values):.4f}\n"
f"渐近标准差 = {std_asym:.4f}\n"
f"Q-Q图 R² = {r_squared:.4f}"
)
ax.text(0.05, 0.95, info_text, transform=ax.transAxes, fontsize=11,
verticalalignment='top', bbox=dict(boxstyle='round', facecolor='white', alpha=0.9))
ax.set_title(f'样本量n={n}时r的抽样分布', fontsize=14)
ax.set_xlabel('样本相关系数 r', fontsize=12)
ax.set_ylabel('概率密度', fontsize=12)
ax.legend()
ax.grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
执行结果如下:
5异常值与杠杆点的扰动性质
异常值与杠杆点的定义
在相关性分析中,我们将对相关系数产生强扰动的点分为两类:一是异常值,即指在因变量 方向上远离主体数据的点,即该点的 值与基于 的预测值之间存在极大的残差;二是杠杆点,即指在自变量 方向上远离主体数据的点,即该点的 值远大于或远小于其他样本的 值。高杠杆点即使残差很小,也会对相关系数和回归结果产生极强的影响。
单个数据点的影响力量化
我们可以通过影响函数来量化单个数据点对样本相关系数的影响力。具体来说,我们计算剔除第 个数据点后,样本相关系数的变化量,以此衡量该点的影响力:
其中表示剔除第 个数据点后,剩余样本计算得到的相关系数。
影响力的绝对值越大,说明该点对相关系数的扰动越强。当影响力的符号与原相关系数相反时,说明该点会削弱原有的相关关系;当符号相同时,说明该点会强化原有的相关关系。
在极端情况下,单个高杠杆点甚至可以完全决定相关系数的大小和符号,让原本无线性相关的数据呈现出极强的相关关系,或者让原本正相关的数据变成负相关。
我们通过代码模拟四种典型场景,可视化异常值与杠杆点对相关系数的扰动效果,同时量化每个点的影响力。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
n_base = 30
# 生成基础数据:无相关的随机数据
x_base = np.random.normal(0, 1, n_base)
y_base = np.random.normal(0, 1, n_base)
r_base, _ = stats.pearsonr(x_base, y_base)
# 场景1:原始无相关数据
x1 = x_base.copy()
y1 = y_base.copy()
r1, _ = stats.pearsonr(x1, y1)
# 场景2:加入Y方向的单个异常值
x2 = np.append(x_base, 0)
y2 = np.append(y_base, 8)
r2, _ = stats.pearsonr(x2, y2)
# 场景3:加入X方向的单个高杠杆点(正相关)
x3 = np.append(x_base, 10)
y3 = np.append(y_base, 10)
r3, _ = stats.pearsonr(x3, y3)
# 场景4:加入X方向的单个高杠杆点(负相关)
x4 = np.append(x_base, 10)
y4 = np.append(y_base, -10)
r4, _ = stats.pearsonr(x4, y4)
# 计算每个场景中异常点的影响力
defcalculate_influence(x, y):
n = len(x)
r_full, _ = stats.pearsonr(x, y)
influence = np.zeros(n)
for i in range(n):
x_drop = np.delete(x, i)
y_drop = np.delete(y, i)
r_drop, _ = stats.pearsonr(x_drop, y_drop)
influence[i] = r_full - r_drop
return influence
inf1 = calculate_influence(x1, y1)
inf2 = calculate_influence(x2, y2)
inf3 = calculate_influence(x3, y3)
inf4 = calculate_influence(x4, y4)
# 创建可视化画布
fig, axes = plt.subplots(2, 2, figsize=(14, 12))
axes = axes.flatten()
scenarios = [
(axes[0], x1, y1, r1, inf1, '场景1:原始无相关数据', '#377eb8'),
(axes[1], x2, y2, r2, inf2, '场景2:加入Y方向异常值', '#e41a1c'),
(axes[2], x3, y3, r3, inf3, '场景3:加入正相关高杠杆点', '#4daf4a'),
(axes[3], x4, y4, r4, inf4, '场景4:加入负相关高杠杆点', '#984ea3')
]
for ax, x, y, r, inf, title, color in scenarios:
# 绘制主体数据点
ax.scatter(x[:-1], y[:-1], alpha=0.7, s=50, edgecolors='white', label='主体数据')
# 绘制异常/杠杆点
if len(x) > n_base:
ax.scatter(x[-1], y[-1], color=color, s=150, marker='*', edgecolors='black', zorder=5, label='异常/杠杆点')
# 绘制回归线
slope, intercept, _, _, _ = stats.linregress(x, y)
x_fit = np.linspace(min(x)-1, max(x)+1, 100)
ax.plot(x_fit, slope * x_fit + intercept, color='black', linestyle='--', linewidth=2, label='整体回归线')
# 添加统计信息
info_text = (
f"整体相关系数 r = {r:.4f}\n"
f"剔除异常点后 r = {r - inf[-1]:.4f}\n"
f"异常点影响力 = {inf[-1]:.4f}"
)
ax.text(0.05, 0.95, info_text, transform=ax.transAxes, fontsize=11,
verticalalignment='top', bbox=dict(boxstyle='round', facecolor='white', alpha=0.9))
ax.set_title(title, fontsize=14)
ax.set_xlabel('X', fontsize=12)
ax.set_ylabel('Y', fontsize=12)
ax.grid(True, linestyle=':', alpha=0.6)
ax.legend()
plt.tight_layout()
plt.show()
执行结果如下:
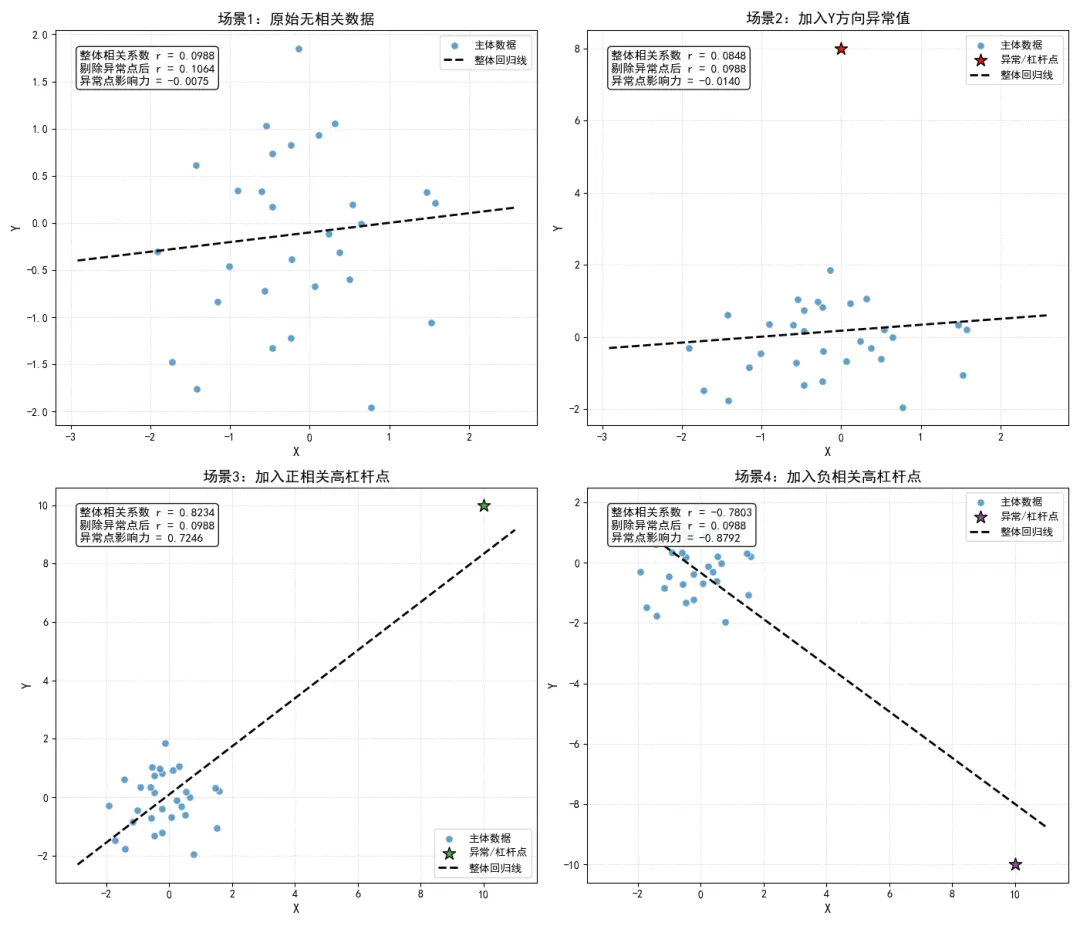
从模拟结果可以清晰地看到,单个高杠杆点可以让原本相关系数接近0的无相关数据,瞬间变成相关系数超过 的强相关数据,甚至可以反转相关系数的符号。这种极强的扰动性,是皮尔逊相关系数最致命的缺陷之一。
在实际数据分析中,我们必须在计算相关系数之前,通过散点图检查数据中是否存在异常值与高杠杆点。如果存在,需要根据业务逻辑判断该点是否为有效数据,若为无效数据则需要剔除,若为有效数据则需要使用更稳健的相关性度量方法。
6分组数据与聚合效应下的相关性质
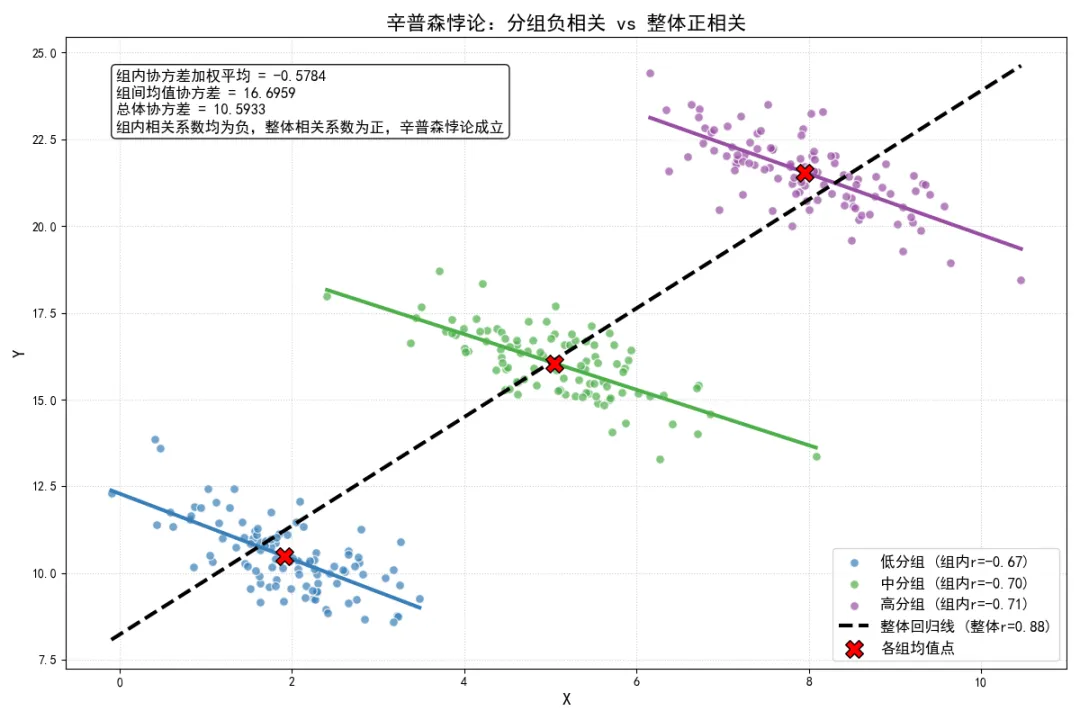
全相关定律与辛普森悖论的数学条件
我们可以将总体相关系数拆解为组内效应与组间效应的组合,这个拆解基于全协方差定律与全方差定律。
假设我们根据离散分组变量 ,将总体分为 个组,每个组的权重为,即第 组的样本占比。
根据全协方差定律,总体协方差可以拆解为:
等式右侧第一项为组内协方差的加权平均,代表控制了分组变量Z后, 和 之间真实的组内线性关系;第二项为组间均值的协方差,代表不同分组之间, 的组均值与 的组均值的协同波动程度。
同理,根据全方差定律, 和 的总体方差可以拆解为:
总体皮尔逊相关系数是总体协方差与总体标准差乘积的比值,因此它由组内协方差、组间协方差、组内方差、组间方差共同决定。
辛普森悖论发生的数学条件: 当组内协方差的加权平均的符号,与组间均值的协方差的符号相反,且组间协方差的绝对值足够大,足以压倒组内协方差的加权平均时,就会发生辛普森悖论。
具体来说,若每个组内X和Y都呈负相关,即,但组间均值的协方差为正且绝对值足够大,导致总体协方差 ,最终总体相关系数为正,与组内相关系数的符号完全相反。
我们通过代码模拟经典的辛普森悖论场景,可视化分组数据与全量数据的相关关系差异,验证上述数学条件。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
n_per_group = 100
# 生成3个分组的数据,组内均为负相关
# 组1:低分组
x1 = np.random.normal(2, 0.8, n_per_group)
y1 = -0.8 * x1 + np.random.normal(12, 0.8, n_per_group)
r1, _ = stats.pearsonr(x1, y1)
# 组2:中分组
x2 = np.random.normal(5, 0.8, n_per_group)
y2 = -0.8 * x2 + np.random.normal(20, 0.8, n_per_group)
r2, _ = stats.pearsonr(x2, y2)
# 组3:高分组
x3 = np.random.normal(8, 0.8, n_per_group)
y3 = -0.8 * x3 + np.random.normal(28, 0.8, n_per_group)
r3, _ = stats.pearsonr(x3, y3)
# 聚合全量数据
x_all = np.concatenate([x1, x2, x3])
y_all = np.concatenate([y1, y2, y3])
r_all, _ = stats.pearsonr(x_all, y_all)
# 计算全协方差拆解
# 组内协方差的加权平均
cov_within = (np.cov(x1, y1)[0,1] + np.cov(x2, y2)[0,1] + np.cov(x3, y3)[0,1]) / 3
# 组间均值的协方差
group_means_x = [np.mean(x1), np.mean(x2), np.mean(x3)]
group_means_y = [np.mean(y1), np.mean(y2), np.mean(y3)]
cov_between = np.cov(group_means_x, group_means_y)[0,1]
# 总体协方差
cov_total = np.cov(x_all, y_all)[0,1]
# 可视化
fig, ax = plt.subplots(figsize=(12, 8))
# 绘制各组散点与回归线
groups = [
('低分组', x1, y1, r1, '#377eb8'),
('中分组', x2, y2, r2, '#4daf4a'),
('高分组', x3, y3, r3, '#984ea3')
]
for label, x, y, r, color in groups:
ax.scatter(x, y, alpha=0.7, color=color, s=50, edgecolors='white', label=f'{label} (组内r={r:.2f})')
slope, intercept, _, _, _ = stats.linregress(x, y)
x_fit = np.linspace(min(x), max(x), 100)
ax.plot(x_fit, slope * x_fit + intercept, color=color, linewidth=3)
# 绘制整体回归线
slope_all, intercept_all, _, _, _ = stats.linregress(x_all, y_all)
x_fit_all = np.linspace(min(x_all), max(x_all), 100)
ax.plot(x_fit_all, slope_all * x_fit_all + intercept_all, color='black', linestyle='--', linewidth=3, label=f'整体回归线 (整体r={r_all:.2f})')
# 绘制各组均值点
ax.scatter(group_means_x, group_means_y, color='red', marker='X', s=200, edgecolors='black', zorder=5, label='各组均值点')
# 添加协方差拆解信息
info_text = (
f"组内协方差加权平均 = {cov_within:.4f}\n"
f"组间均值协方差 = {cov_between:.4f}\n"
f"总体协方差 = {cov_total:.4f}\n"
f"组内相关系数均为负,整体相关系数为正,辛普森悖论成立"
)
ax.text(0.05, 0.95, info_text, transform=ax.transAxes, fontsize=12,
verticalalignment='top', bbox=dict(boxstyle='round', facecolor='white', alpha=0.9))
ax.set_title('辛普森悖论:分组负相关 vs 整体正相关', fontsize=16)
ax.set_xlabel('X', fontsize=14)
ax.set_ylabel('Y', fontsize=14)
ax.grid(True, linestyle=':', alpha=0.6)
ax.legend(fontsize=12)
plt.tight_layout()
plt.show()
执行结果如下:
生态谬误
生态谬误是辛普森悖论的延伸,指的是用聚合层面的相关系数推断个体层面的相关关系,会产生严重的偏差甚至完全错误的结论。
在社会学、经济学、公共卫生等领域,我们经常会遇到聚合层面的数据,比如城市、省份、国家层面的统计指标。如果我们直接计算这些聚合指标的相关系数,并将其结论推广到个体层面,就会陷入生态谬误。
最经典的例子是,在国家层面,人均巧克力消费量与诺贝尔奖获得数量呈极强的正相关,但这并不意味着个体吃巧克力越多,获得诺贝尔奖的概率越高。国家层面的相关关系,完全无法推广到个体层面。
我们通过代码模拟生态谬误的场景,对比个体层面与聚合层面的相关系数差异,直观展示这种偏差。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
# 模拟10个城市,每个城市200个个体
n_cities = 10
n_individuals_per_city = 200
# 每个城市的收入水平均值(城市层面的潜在变量)
city_income_mean = np.linspace(3000, 15000, n_cities)
# 存储个体层面数据
individual_income = []
individual_spending = []
city_labels = []
# 生成个体数据
for city_idx, income_mean in enumerate(city_income_mean):
# 个体收入围绕城市均值波动
income = np.random.normal(income_mean, 2000, n_individuals_per_city)
# 个体消费与个体收入的真实关系:弱正相关,相关系数约0.2
spending = 0.2 * income + np.random.normal(income_mean * 0.3, 1500, n_individuals_per_city)
individual_income.extend(income)
individual_spending.extend(spending)
city_labels.extend([city_idx] * n_individuals_per_city)
# 转换为数组
individual_income = np.array(individual_income)
individual_spending = np.array(individual_spending)
city_labels = np.array(city_labels)
# 计算个体层面的相关系数
r_individual, _ = stats.pearsonr(individual_income, individual_spending)
# 计算城市层面的聚合数据(均值)
city_income_agg = []
city_spending_agg = []
for city_idx in range(n_cities):
mask = city_labels == city_idx
city_income_agg.append(np.mean(individual_income[mask]))
city_spending_agg.append(np.mean(individual_spending[mask]))
city_income_agg = np.array(city_income_agg)
city_spending_agg = np.array(city_spending_agg)
# 计算城市层面的相关系数
r_city, _ = stats.pearsonr(city_income_agg, city_spending_agg)
# 可视化
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(16, 7))
# 个体层面散点图
ax1.scatter(individual_income, individual_spending, alpha=0.3, s=10, color='#377eb8')
slope1, intercept1, _, _, _ = stats.linregress(individual_income, individual_spending)
x_fit1 = np.linspace(min(individual_income), max(individual_income), 100)
ax1.plot(x_fit1, slope1 * x_fit1 + intercept1, color='black', linestyle='--', linewidth=3)
ax1.set_title(f'个体层面:收入 vs 消费\nPearson r = {r_individual:.4f}', fontsize=14)
ax1.set_xlabel('个体月收入', fontsize=12)
ax1.set_ylabel('个体月消费', fontsize=12)
ax1.grid(True, linestyle=':', alpha=0.6)
# 城市层面散点图
ax2.scatter(city_income_agg, city_spending_agg, color='#e41a1c', s=150, marker='o', edgecolors='black')
slope2, intercept2, _, _, _ = stats.linregress(city_income_agg, city_spending_agg)
x_fit2 = np.linspace(min(city_income_agg), max(city_income_agg), 100)
ax2.plot(x_fit2, slope2 * x_fit2 + intercept2, color='black', linestyle='--', linewidth=3)
ax2.set_title(f'城市聚合层面:平均收入 vs 平均消费\nPearson r = {r_city:.4f}', fontsize=14)
ax2.set_xlabel('城市月均收入', fontsize=12)
ax2.set_ylabel('城市月均消费', fontsize=12)
ax2.grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
# 输出结果
print(f"个体层面相关系数: {r_individual:.4f}")
print(f"城市聚合层面相关系数: {r_city:.4f}")
执行结果如下:
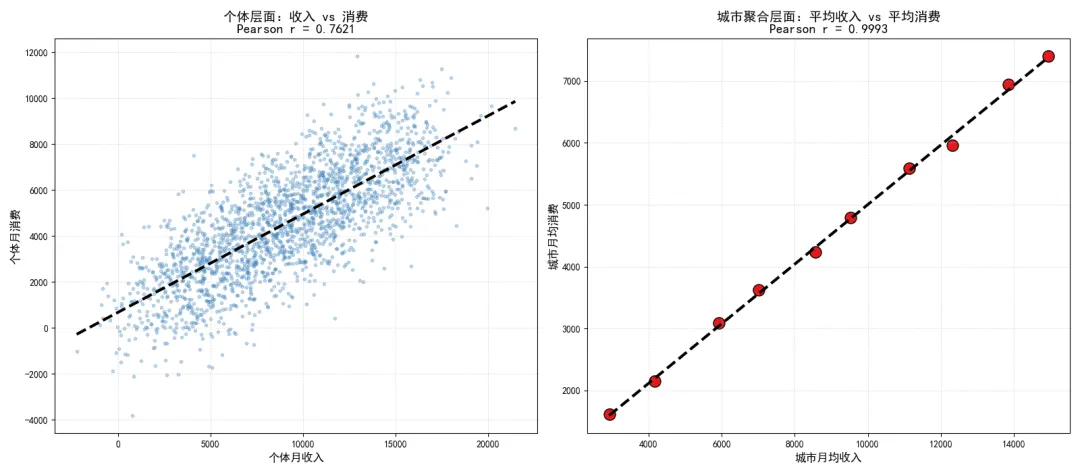
从模拟结果可以看到,个体层面收入与消费的相关系数仅为 左右,属于弱相关;但聚合到城市层面后,相关系数接近,呈现出完美的正相关。如果我们直接用城市层面的强相关,推断个体收入越高消费越高,就会严重高估个体层面的相关强度,陷入生态谬误。
7线性性本质与适用边界
通过前面的推导与模拟,我们已经多次强调,皮尔逊相关系数只能捕捉变量之间的线性依赖关系。本节我们将从数学上严格证明这一点,通过经典的非线性案例展示相关系数的失效场景,最终明确皮尔逊相关系数的核心适用边界。
线性性的数学本质
皮尔逊相关系数为的充要条件是,两个变量之间不存在线性依赖关系,而非不存在任何依赖关系。
我们可以从线性回归的角度来理解这一点。当皮尔逊相关系数 时, 对 的回归系数,这意味着最优的线性拟合线是一条水平直线, 的线性变化完全无法解释 的变化。但这并不代表 和 之间没有关系,它们之间可能存在极强的非线性函数关系,只是这种关系无法用一条直线来拟合。
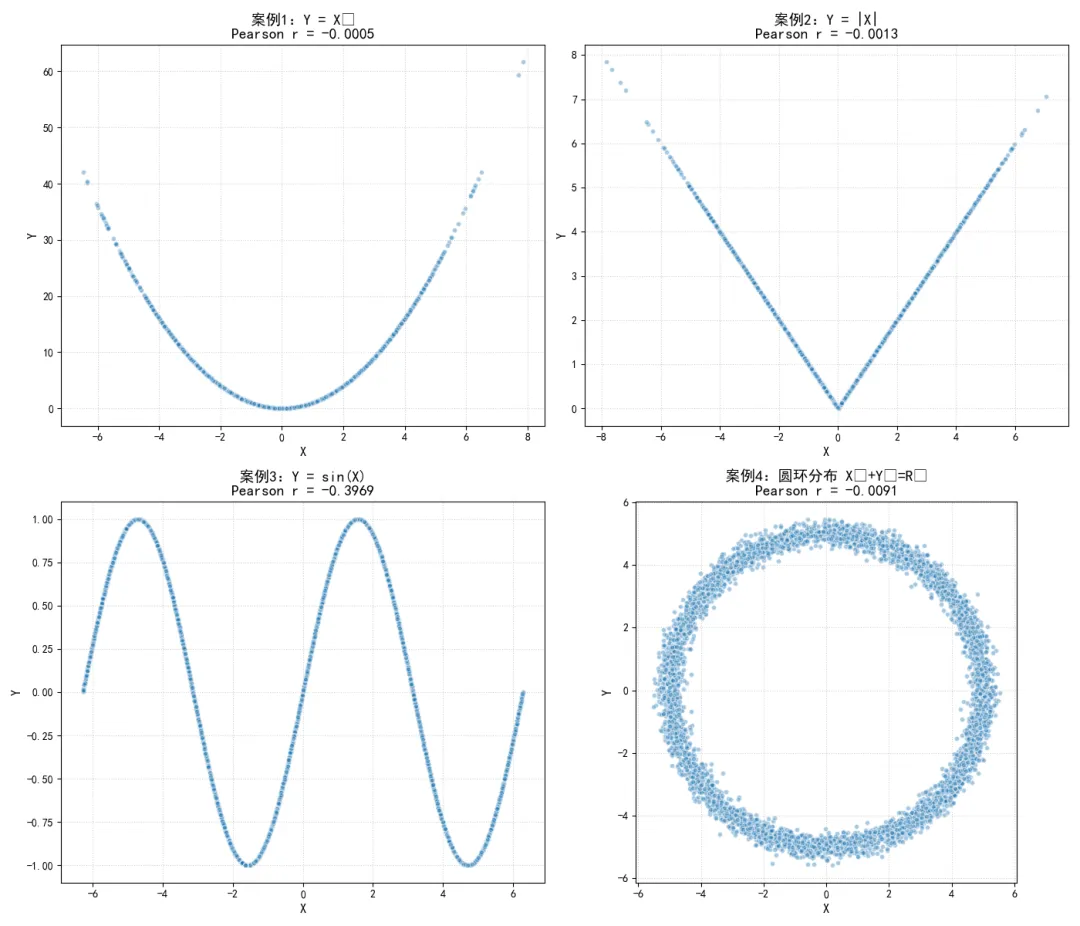
经典非线性失效案例
我们通过四个经典的非线性模型,从数学上推导相关系数为0的过程,同时通过代码可视化这些强非线性关系下,皮尔逊相关系数失效的场景。
案例1:二次函数关系
假设 服从对称分布,比如区间 上的均匀分布,或者均值为的正态分布,此时 ,且 的奇数阶矩为0。
我们计算 和 的协方差:
协方差为0,因此皮尔逊相关系数 。
尽管 完全由 确定性决定,两者之间存在完美的二次函数关系,但皮尔逊相关系数却为0,完全无法捕捉这种非线性依赖。
案例2:绝对值关系
同样假设X服从关于0对称的分布,此时 是一个奇函数,在对称区间上的期望为0:
因此协方差 ,相关系数 。
案例3:正弦函数关系
假设 服从区间 上的均匀分布,此时 是一个偶函数,而我们计算协方差时:
这里需要注意,当 的区间为 时,相关系数并不为0;但当我们将区间扩展为 时, 在对称区间上的积分会相互抵消,,此时相关系数 。
案例4:圆环分布
假设 和 服从二维圆环分布,即 ,其中 服从区间 上的均匀分布, 为固定半径。
计算协方差:
因此,相关系数 。
尽管 和 之间存在完美的确定性函数关系,给定 的值可以完全确定 的取值范围,但皮尔逊相关系数依然为0。
我们通过代码可视化这四个案例,验证相关系数的计算结果,直观展示皮尔逊相关系数对非线性关系的盲区。
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# 设置中文字体
plt.rcParams['font.sans-serif'] = ['SimHei']
plt.rcParams['axes.unicode_minus'] = False
# 设定随机种子
np.random.seed(42)
n = 5000
# 创建可视化画布
fig, axes = plt.subplots(2, 2, figsize=(14, 12))
axes = axes.flatten()
# 案例1:Y = X²
x1 = np.random.normal(0, 2, n)
y1 = x1 ** 2
r1, _ = stats.pearsonr(x1, y1)
axes[0].scatter(x1, y1, alpha=0.4, s=20, edgecolors='white')
axes[0].set_title(f'案例1:Y = X²\nPearson r = {r1:.4f}', fontsize=14)
axes[0].set_xlabel('X', fontsize=12)
axes[0].set_ylabel('Y', fontsize=12)
axes[0].grid(True, linestyle=':', alpha=0.6)
# 案例2:Y = |X|
x2 = np.random.normal(0, 2, n)
y2 = np.abs(x2)
r2, _ = stats.pearsonr(x2, y2)
axes[1].scatter(x2, y2, alpha=0.4, s=20, edgecolors='white')
axes[1].set_title(f'案例2:Y = |X|\nPearson r = {r2:.4f}', fontsize=14)
axes[1].set_xlabel('X', fontsize=12)
axes[1].set_ylabel('Y', fontsize=12)
axes[1].grid(True, linestyle=':', alpha=0.6)
# 案例3:Y = sin(X),X~U(-2π, 2π)
x3 = np.random.uniform(-2 * np.pi, 2 * np.pi, n)
y3 = np.sin(x3)
r3, _ = stats.pearsonr(x3, y3)
axes[2].scatter(x3, y3, alpha=0.4, s=20, edgecolors='white')
axes[2].set_title(f'案例3:Y = sin(X)\nPearson r = {r3:.4f}', fontsize=14)
axes[2].set_xlabel('X', fontsize=12)
axes[2].set_ylabel('Y', fontsize=12)
axes[2].grid(True, linestyle=':', alpha=0.6)
# 案例4:圆环分布
theta = np.random.uniform(0, 2 * np.pi, n)
r = np.random.normal(5, 0.2, n)
x4 = r * np.cos(theta)
y4 = r * np.sin(theta)
r4, _ = stats.pearsonr(x4, y4)
axes[3].scatter(x4, y4, alpha=0.4, s=20, edgecolors='white')
axes[3].set_title(f'案例4:圆环分布 X²+Y²=R²\nPearson r = {r4:.4f}', fontsize=14)
axes[3].set_xlabel('X', fontsize=12)
axes[3].set_ylabel('Y', fontsize=12)
axes[3].set_aspect('equal')
axes[3].grid(True, linestyle=':', alpha=0.6)
plt.tight_layout()
plt.show()
执行结果如下:
皮尔逊相关系数的核心适用边界
基于前面的所有性质推导与模拟验证,我们可以明确皮尔逊相关系数的核心适用前提与边界:
一是变量之间存在线性关系。这是最核心的前提,皮尔逊相关系数仅能度量线性依赖关系,对任何形式的非线性依赖都会失效,甚至给出完全错误的结论。
二是变量为连续型随机变量。皮尔逊相关系数的定义基于方差与协方差,仅适用于连续型变量,不适用于分类变量、有序等级变量。
三是变量服从二元正态分布。这是相关系数统计推断的核心前提。只有当两个变量服从二元正态分布时,不相关才等价于独立,样本相关系数的抽样分布才能通过Fisher Z变换正态化,相关的假设检验与置信区间计算才有效。
四十数据中无强异常值与高杠杆点。皮尔逊相关系数对异常值与高杠杆点极其敏感,单个极端点可以完全改变相关系数的大小与符号,导致分析结果失真。
五是*数据具有同质性,无潜在分组结构。如果数据中存在潜在的分组变量,可能会出现辛普森悖论,导致整体相关系数与分组内的真实相关关系完全相反,产生误导性结论。
本节总结
在本节中,我们从代数、几何、统计推断三个维度,系统拆解了皮尔逊相关系数的核心性质与边界约束,完成了对这个最常用统计量的全面解构。
在代数性质层面,我们证明了皮尔逊相关系数的对称性、绝对边界性、标准化变量的协方差等价性,以及独立变量的相关系数为0的性质,明确了它的基础代数约束。
在线性变换性质层面,我们推导了平移变换的绝对不变性与尺度变换的符号规则,证明了任意线性变换都不会改变相关系数的绝对值,仅可能反转其符号,解释了相关系数的无量纲特性。
在几何性质层面,我们将相关系数映射为 维样本空间中去中心化向量的夹角余弦值,揭示了它与线性回归系数的内在关联,证明了相关系数的平方等于线性回归的决定系数 ,为相关系数提供了直观的方差解释率解读。
在抽样性质层面,我们明确了样本相关系数是总体相关系数的一致但有偏估计量,推导了它的渐近正态性,提供了小样本下的偏差校正方法,解决了小样本场景下的估计偏差问题。
在扰动性质层面,我们量化了异常值与高杠杆点对相关系数的影响力,通过模拟实验展示了单个极端点对相关系数的强扰动性,明确了皮尔逊相关系数的非稳健性。
在分组数据性质层面,我们通过全相关定律拆解了总体相关系数的组内与组间效应,明确了辛普森悖论的数学条件,揭示了聚合数据带来的生态谬误,强调了分层分析的重要性。
最后,我们通过数学推导与经典案例,明确了皮尔逊相关系数的线性性本质,展示了它在非线性关系下的完全失效,最终划定了皮尔逊相关系数的核心适用边界。
