NC代码分享:有 python+R 的单细胞和空间转录组数据挖掘类文献
- 2026-04-02 05:43:57
今天周末,来给大家分享一个高分文献数据挖掘类的代码。文献于20245月23号23 发表在 nature communications 杂志上,标题为《Single-cell and spatial transcriptomics analysis of non-small cell lung cancer》。


0
1https://gitlab.com/cvejic-group/lung
python代码:
R版本的代码:
空间部分的分析代码:
都是都是免费公开可以下载的!
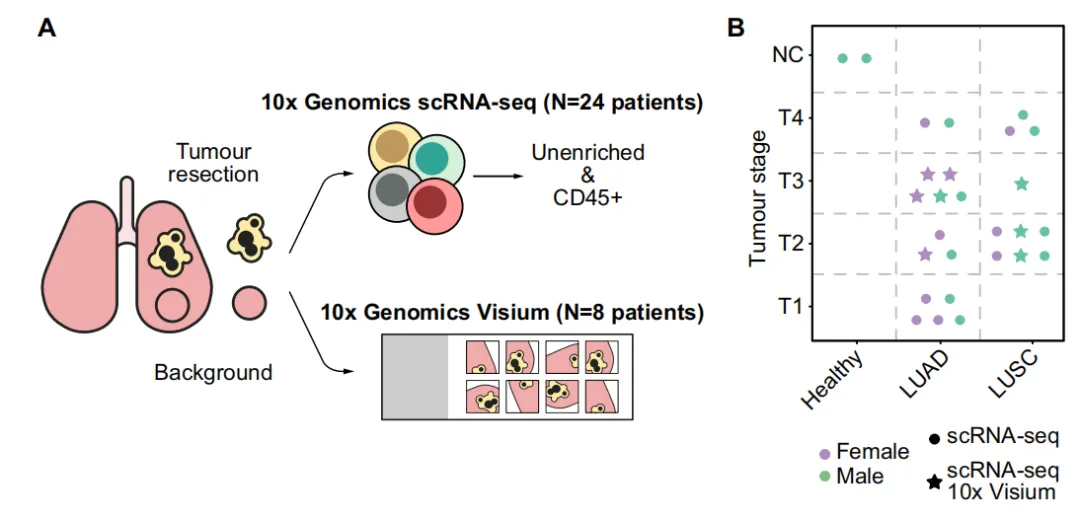
scRNA-seq:25个癌症样本+2个正常健康样本,通过分选获得 CD45+ 免疫细胞(补充图1A)及肿瘤细胞与其他非免疫细胞群(使用CD235a抗体柱去除红细胞),并进行单细胞RNA测序。
10x Visium测序:对来自八名患者的两个连续10微米切片进行了10× Visium分析,其中七名患者的样本与用于单细胞RNA测序的样本相匹配。我们共分析了36个切片,其中肿瘤切片20个,背景切片16个,肿瘤区域每个空间点的平均UMI计数为6894,背景区域每个空间点的平均UMI计数为3350。
样本表型详细信息见:Supplementary Data 1。
https://www.ebi.ac.uk/biostudies/
scRNA-seq数据:E-MTAB-13526
cat id.txt |whilereadiddoecho"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/526/E-MTAB-13526/Files/${id}-barcodes.tsv.gz"echo"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/526/E-MTAB-13526/Files/${id}-features.tsv.gz"echo"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/526/E-MTAB-13526/Files/${id}-matrix.mtx.gz"done >down.sh# 运行nohup bash down.sh 1>down.log 2>&1 &wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/526/E-MTAB-13526/Files/10X_Lung_Healthy_Background_Annotated_v2.h5adwget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/526/E-MTAB-13526/Files/10X_Lung_Tumour_Annotated_v2.h5ad
Visium数据:E-MTAB-13530
cat id.txt |whilereadiddoecho"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/530/E-MTAB-13530/Files/${id}-spatial.tar"echo"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/530/E-MTAB-13530/Files/${id}-filtered_feature_bc_matrix.h5"echo"wget -c https://ftp.ebi.ac.uk/biostudies/fire/E-MTAB-/530/E-MTAB-13530/Files/${id}-web_summary.html"done >down.sh# 运行nohup bash down.sh 1>down.log 2>&1 &
共鉴定出 895,806 个高质量细胞,其中 503,549 个来源于肿瘤组织,392,257 个来源于癌旁背景组织与健康组织(以下简称B/H)。识别出 monocytes, macrophages, dendritic cells (DCs), mast cells, natural killer (NK) cells, T cells, B cells and non-immune cells(图1C、1D)。
未检测到中性粒细胞,极有可能是因为其对采集后降解过程,特别是冻融循环较为敏感。
比较奇怪的点:发现一个同时表达髓系基因(LYZ、CD68、CD14、MRC1)和上皮基因(KRT19、EPCAM)的细胞群(图1D–F)。
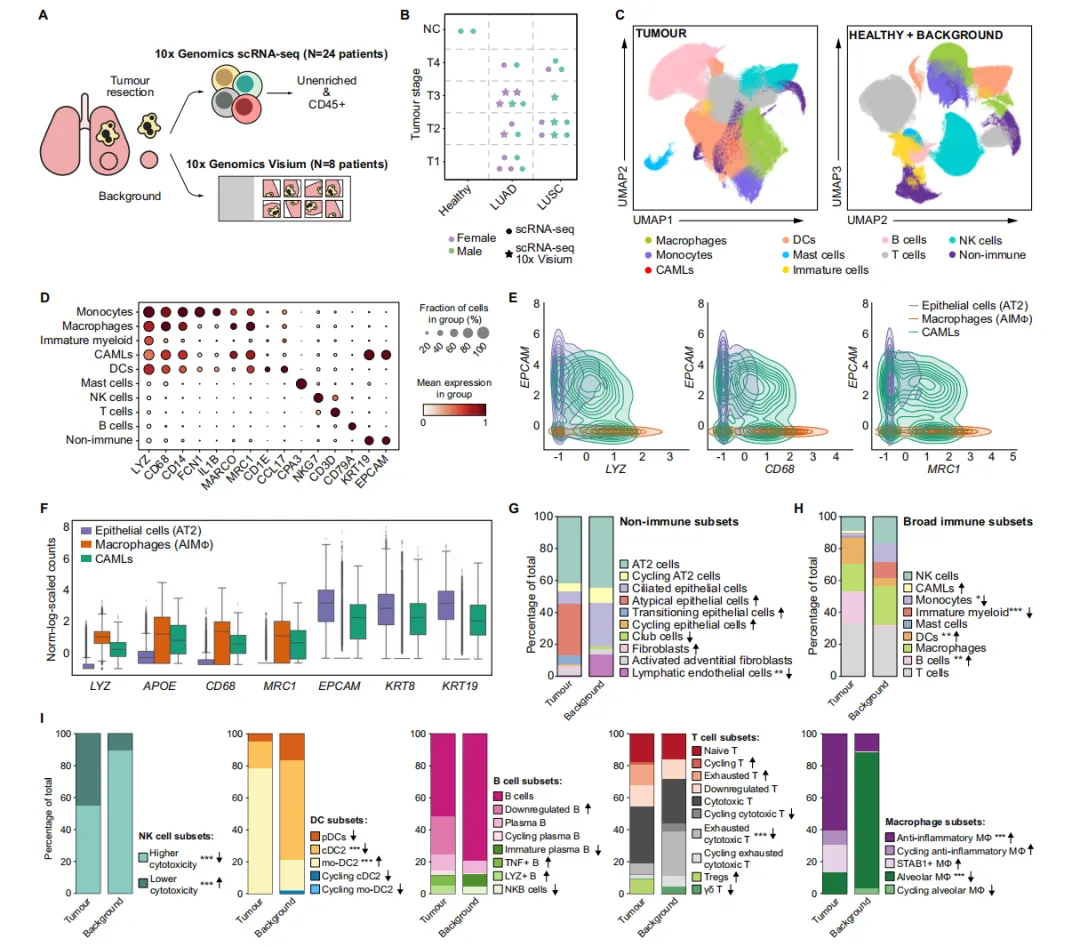
A 热图展示每种免疫细胞类型相对丰度之间的皮尔逊相关性。
B 热图展示肺腺癌和肺鳞癌中按宽泛细胞注释汇总的所有细胞类型之间的配体-受体相互作用数量。
C 桑基图展示cellphoneDB检测到的选定免疫检查点分子在肺腺癌和肺鳞癌中的肿瘤特异性相互作用。
D 点图展示中突出的免疫检查点基因和细胞类型,按肿瘤类型分面。
E 桑基图展示cellphoneDB检测到的VEGFA/B相互作用因子在肺腺癌和肺鳞癌中的肿瘤特异性相互作用。
F 桑基图展示cellphoneDB检测到的EGFR相互作用因子在肺腺癌和肺鳞癌中的肿瘤特异性相互作用。
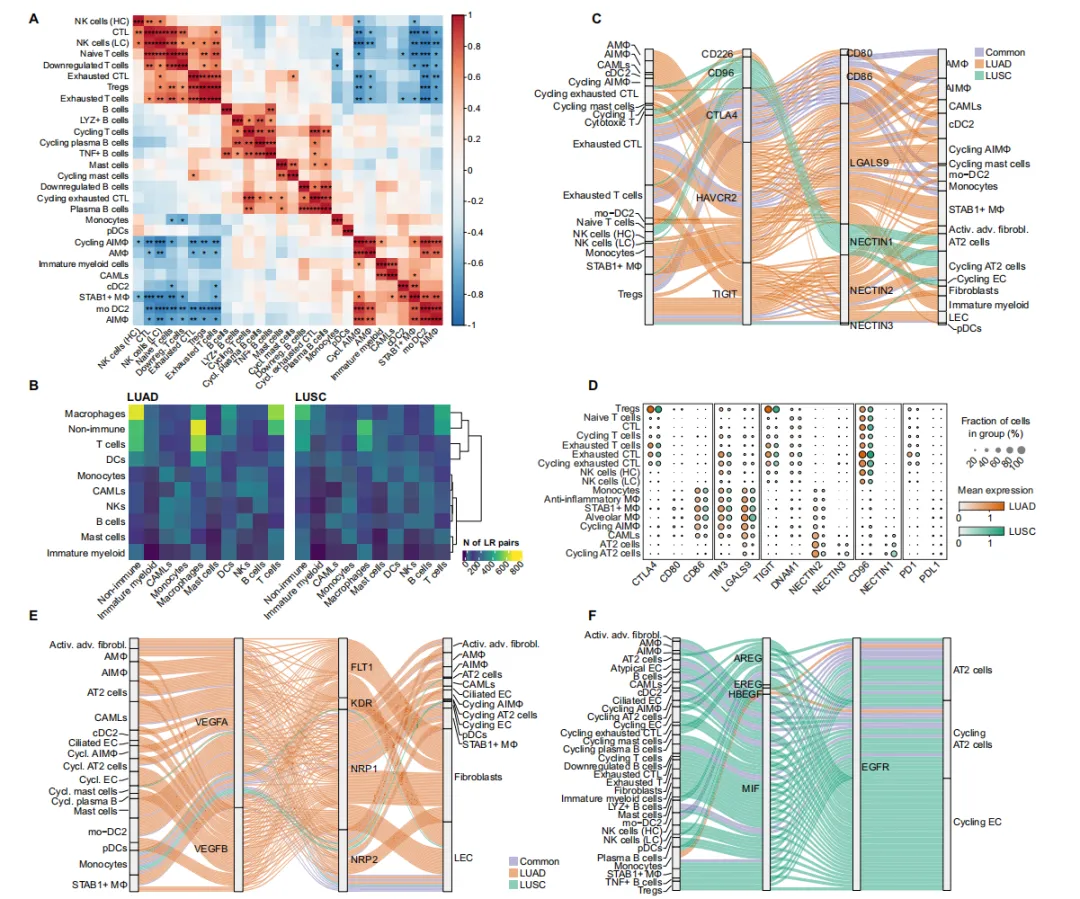
A cell2location估计的AT2细胞、AIMɸ和Treg细胞的丰度。
B cell2location细胞丰度估计计算的免疫(左)和非免疫(右)细胞类型的相对比例。
C 空间配体-受体(LR)共定位热图。
D 箱线图显示在每个分析的切片中,肿瘤与背景间显著差异的共定位LR对的频率。
E 空间图像展示了在肿瘤(上)和背景(下)中LR对被共表达定位的spot位置,包括NRP1-VEGFA、NECTIN2-TIGIT、PD1-PDL1、CD96-NECTIN1和HAVCR2-LGALS9。
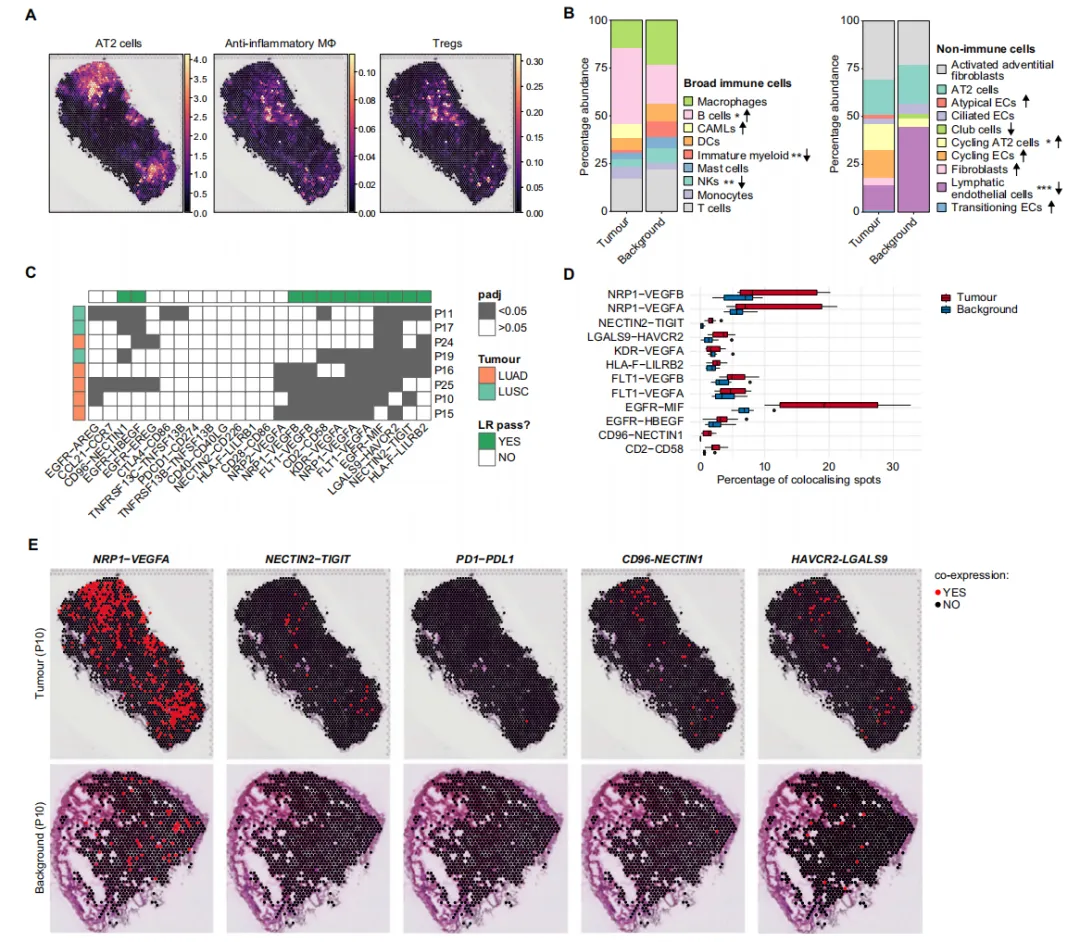
A CNA 分析。该图显示了通过 CopyKat 估算的肿瘤数据集中不同细胞类型和患者在每个染色体臂上的染色体获得(红线)和丢失(蓝线)。
B 叠加在肿瘤中非免疫细胞类型扩散图(力导向布局——FLE 嵌入)上的 PAGA 图。
C 前三张图——病理注释,显示肿瘤浸润区域(左)、Visium 斑点上肿瘤区域的分箱(中)以及通过质控(QC)的斑点(右)。后三张图——在同一切片上,通过 cell2location 估算的 AT2 细胞(左)、增殖性 AT2 细胞(中)和非典型上皮细胞(右)的丰度,叠加了病理学家对肿瘤浸润的注释(绿色轮廓)。
D 使用 clusterProfiler R 软件包,基于 AT2 细胞在肿瘤与背景中上调的差异表达基因功能
E 来自一名代表性患者肿瘤中 AT2 细胞和 CAMLs 的 CNA 详细概览。
F 散点图,显示肿瘤数据集中每种细胞类型之间,基于其获得和丢失分布计算的丢失(x 轴)和获得(y 轴)的 KL 散度。
G 空间图像,展示了在三个代表性肿瘤切片上通过 cell2location 估算的 AT2 细胞和 CAMLs 的细胞丰度。
H 基于所有肿瘤切片中通过 QC 的斑点上的细胞类型组成(由 cell2location 估算)计算的相关系数矩阵的层次聚类。
I 基于所有肿瘤切片中通过 QC 的斑点上细胞类型丰度的 q05 估算值(由 cell2location 估算)构建的非负矩阵分解。
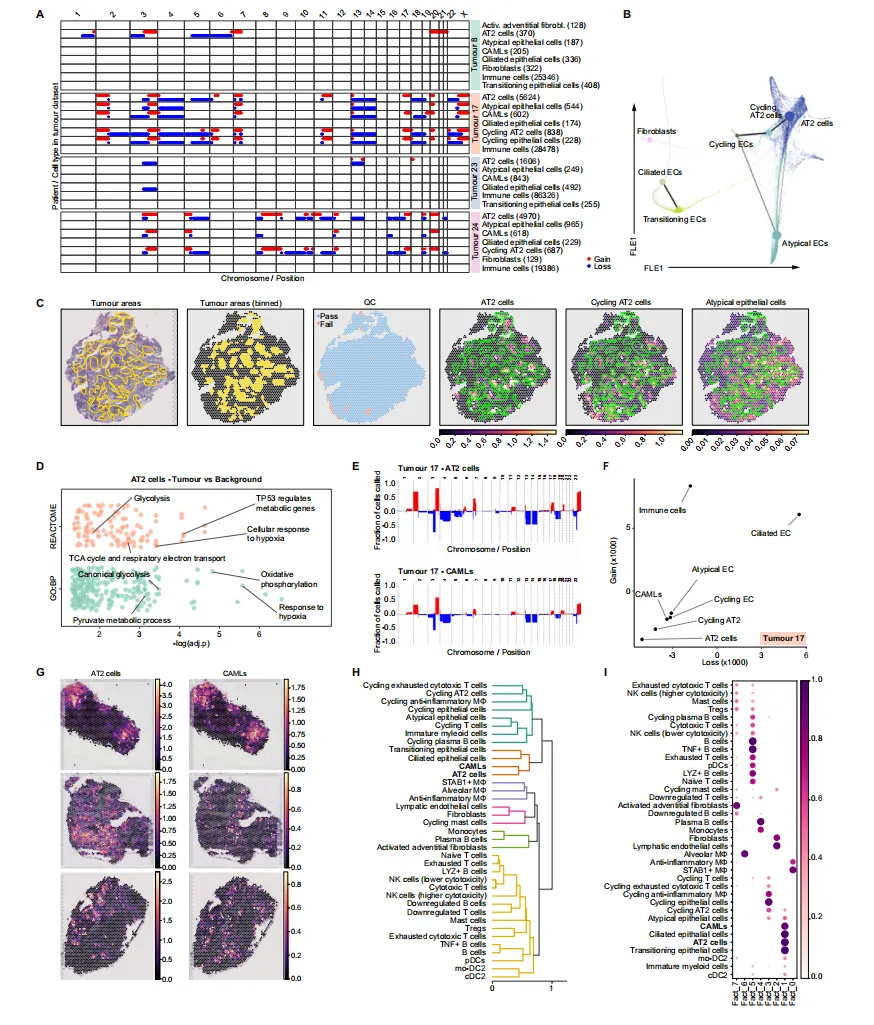
A 肿瘤 vs 背景中 AIMɸ 差异表达基因的火山图。
B 肺泡巨噬细胞和 AIMɸ 在肿瘤 vs 背景中上调的差异表达基因功能。
C 肿瘤和背景组织切片上 CD68 和中性脂质(BODIPY 493/503)的免疫组化染色。
D 肿瘤和背景切片中 BODIPY 信号覆盖的面积。
E 肿瘤(左)和背景(右)组织切片上 CD68 和 STAB1 的免疫组化染色。
F CD68⁺ 巨噬细胞群体中 STAB1⁺ 细胞的定量。
G 肿瘤组织切片上 CD68、STAB1 和 PanCK 的染色。
H 非小细胞肺癌中 CD68⁺ 巨噬细胞群体内 STAB1⁺CD68⁺ 细胞的定量。
I 点图显示肿瘤中所有巨噬细胞亚群和 CAMLs 中“STAB1 特征基因”的表达情况。
J 肿瘤中肺泡巨噬细胞 vs STAB1 巨噬细胞的 差异火山图。
K 肿瘤中肺泡巨噬细胞 vs STAB1 巨噬细胞(上)和 AIMɸ vs STAB1 巨噬细胞(下)的差异表达基因功能。
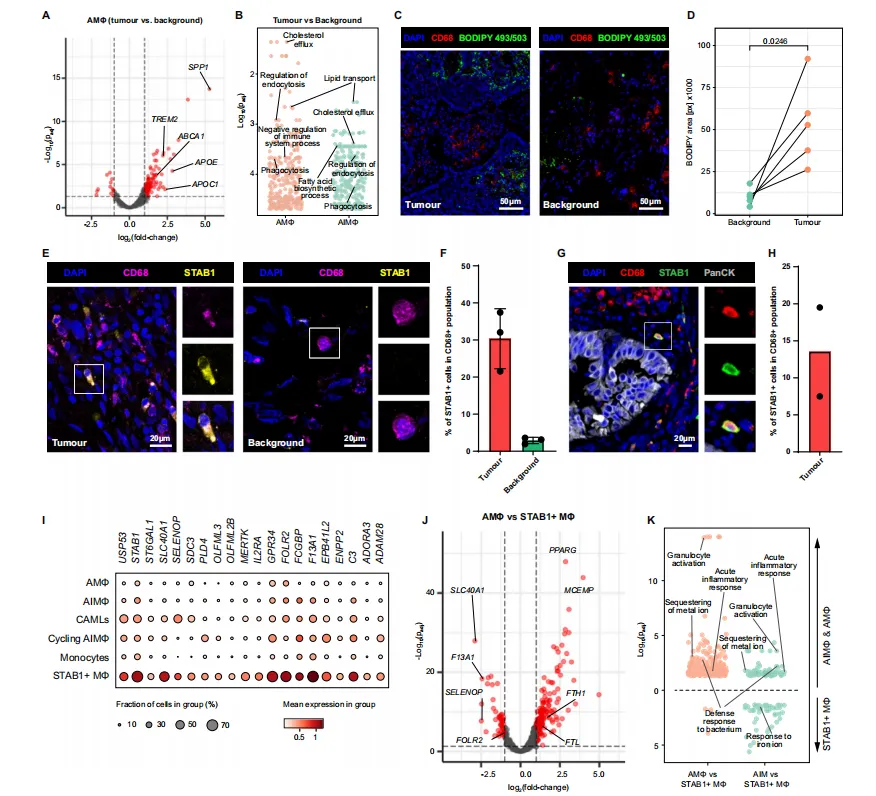
A 在整合后的主成分空间(肿瘤髓系 + 背景髓系 + 胎儿肺髓系)中对每个细胞计算相关系数,并进行层次聚类。
B 公开的人类胎儿肺细胞图谱中识别的髓系细胞和祖细胞群体中“STAB1 基因特征”的表达水平。
C 点图,显示选定的胎儿肺巨噬细胞群体中“STAB1 基因特征”内每个基因的表达。
D 公开的 MoMac-VERSE 数据集中识别的各个细胞群中“STAB1 基因特征”的表达水平。
E 点图,显示来自 MoMac-VERSE 的选定巨噬细胞群体中“STAB1 基因特征”内每个基因的表达。
F 在公开的“MoMac-VERSE”数据集中识别的髓系细胞和祖细胞群体中“AMɸ 基因特征”的表达水平。
G 公开的人类胎儿肺细胞图谱中识别的髓系细胞和祖细胞群体中“AMɸ 基因特征”的表达水平。
H 点图,显示在“MoMac-VERSE”数据集中识别的选定巨噬细胞群体中“AMɸ 基因特征”内每个基因的表达。
I 点图,显示选定的胎儿肺巨噬细胞群体中“AMɸ 基因特征”内每个基因的表达。
今天分享到这里~
