《15节课Python绘图从入门到精通》6——百分比堆积条形图与复合饼图
- 2026-04-15 18:24:13
前置数据准备
为保证所有程序可直接运行,先运行以下代码生成两组实验数据:土壤粒径分级多组样本数据、细胞器体积占比数据。
import pandas as pdimport numpy as npnp.random.seed(2024)# 模拟四个土壤样本,每个样本三个粒径级别(黏粒、粉粒、砂粒)的百分比samples = ['样本A', '样本B', '样本C', '样本D']fractions = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']data_soil = []for i, sample in enumerate(samples):# 生成不同组成的百分比(和为100%)if i == 0: clay, silt, sand = 20, 45, 35elif i == 1: clay, silt, sand = 35, 40, 25elif i == 2: clay, silt, sand = 15, 30, 55else: clay, silt, sand = 45, 35, 20# 添加少量随机扰动 clay += np.random.uniform(-2, 2) silt += np.random.uniform(-2, 2) sand = 100 - clay - silt # 确保总和为100 data_soil.append([sample, fractions[0], clay]) data_soil.append([sample, fractions[1], silt]) data_soil.append([sample, fractions[2], sand])df_soil = pd.DataFrame(data_soil, columns=['样本', '粒径分级', '百分比'])df_soil.to_csv('土壤粒径数据.csv', index=False, encoding='utf-8-sig')organelles = ['细胞核', '线粒体', '内质网', '高尔基体', '溶酶体', '其他']volumes = [8, 15, 35, 10, 7, 25] # 总体积占比(%)df_organelle = pd.DataFrame({'细胞器': organelles, '体积占比': volumes})df_organelle.to_csv('细胞器体积数据.csv', index=False, encoding='utf-8-sig')# 一级分类:主要生物类群level1 = ['细菌', '真菌', '病毒', '原生生物']level1_pct = [45, 30, 15, 10]# 二级分类:各一级分类下的细分bacteria_sub = ['变形菌门', '厚壁菌门', '放线菌门', '拟杆菌门']bacteria_pct = [40, 30, 20, 10]fungi_sub = ['子囊菌门', '担子菌门', '接合菌门']fungi_pct = [50, 35, 15]virus_sub = ['dsDNA病毒', 'ssRNA病毒', 'dsRNA病毒']virus_pct = [60, 30, 10]protozoa_sub = ['鞭毛虫', '阿米巴', '纤毛虫']protozoa_pct = [50, 30, 20]# 构建数据框data_pie = []for sub, pct in zip(bacteria_sub, bacteria_pct): data_pie.append(['细菌', sub, pct])for sub, pct in zip(fungi_sub, fungi_pct): data_pie.append(['真菌', sub, pct])for sub, pct in zip(virus_sub, virus_pct): data_pie.append(['病毒', sub, pct])for sub, pct in zip(protozoa_sub, protozoa_pct): data_pie.append(['原生生物', sub, pct])df_pie = pd.DataFrame(data_pie, columns=['一级分类', '二级分类', '百分比'])df_pie.to_csv('微生物层级数据.csv', index=False, encoding='utf-8-sig')print("数据生成完成:")print("- 土壤粒径数据.csv(6.1节用)")print("- 细胞器体积数据.csv(6.2节用)")print("- 微生物层级数据.csv(6.3节用)")执行结果如下:
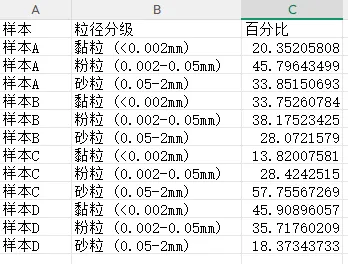
土壤粒径数据
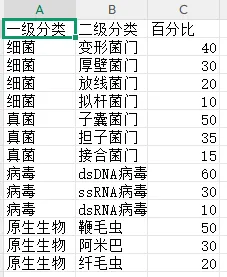
细胞器体积数据
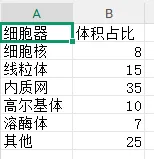
微生物层级数据
实操任务1:绘制多组样本的百分比堆积条形图,标注百分比数值
本任务从基础的百分比堆积条形图入手,逐步进阶到数值标注、自定义配色、排序优化及多分类对比。
基础版:多组样本百分比堆积条形图
程序读取土壤粒径数据,将数据透视为宽表格式,绘制百分比堆积条形图。
import pandas as pdimport numpy as npimport matplotlib.pyplot as plt# 学术样式设置defset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()# 读取数据df = pd.read_csv('土壤粒径数据.csv')# 透视表:行为样本,列为粒径分级,值为百分比df_pivot = df.pivot(index='样本', columns='粒径分级', values='百分比')# 确保列顺序(黏粒、粉粒、砂粒)order = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']df_pivot = df_pivot[order]# 绘制百分比堆积条形图fig, ax = plt.subplots(figsize=(5.0, 3.8))# 使用自定义颜色(土壤学常用色)colors = ['#8B5A2B', '#CDAA7D', '#F5DEB3'] # 深棕、浅棕、米黄df_pivot.plot(kind='bar', stacked=True, ax=ax, color=colors, width=0.7, edgecolor='black', linewidth=0.5)ax.set_xlabel('样本')ax.set_ylabel('百分比 (%)')ax.set_ylim(0, 100)ax.legend(title='粒径分级', bbox_to_anchor=(1.02, 1), loc='upper left', fontsize=8, title_fontsize=9)# 去除上、右 spinesax.spines['top'].set_visible(False)ax.spines['right'].set_visible(False)plt.tight_layout()plt.show()fig.savefig('百分比堆积条形图_基础.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('百分比堆积条形图_基础.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
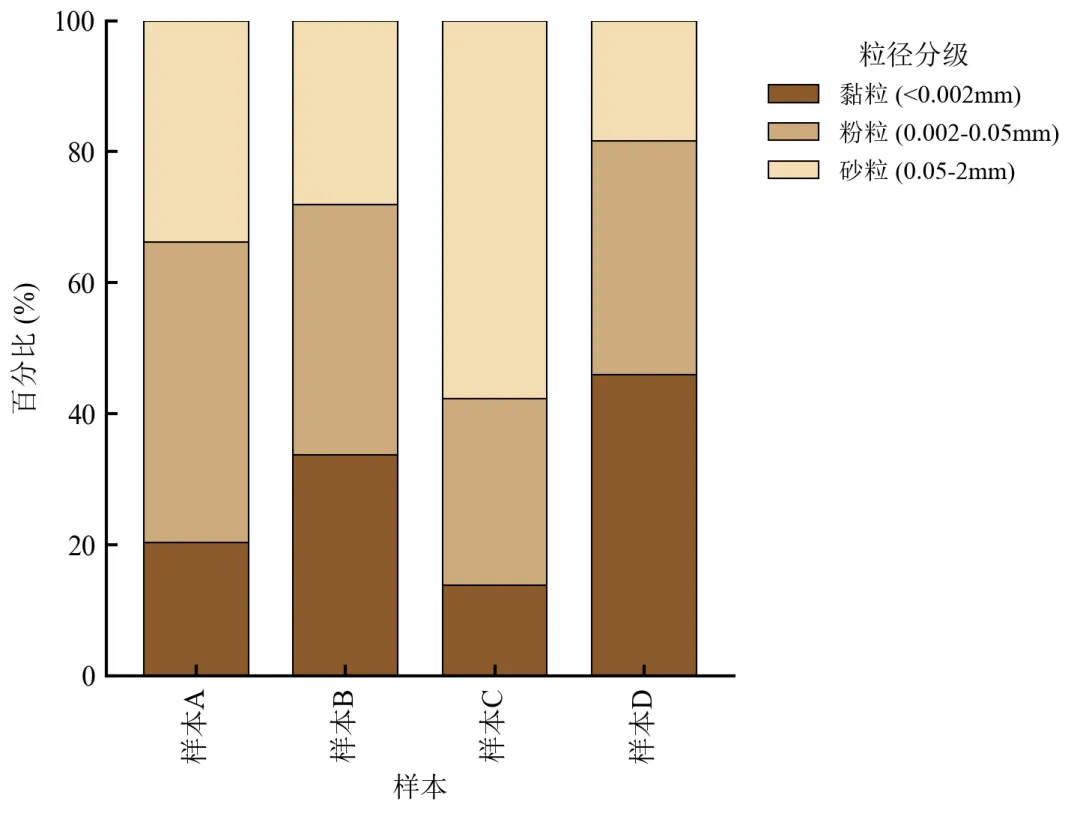
每个样本的条形总高度为100%,直观对比各样本中黏粒、粉粒、砂粒的占比差异。
样本D黏粒比例最高(约45%),样本C砂粒比例最高(约55%),反映土壤质地差异。
图例移至右侧避免遮挡,学术配色符合土壤学常见习惯。
进阶1:在堆积条形图上标注百分比数值
在每段堆积条内部或上方标注具体百分比值,便于精确读取。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('土壤粒径数据.csv')df_pivot = df.pivot(index='样本', columns='粒径分级', values='百分比')order = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']df_pivot = df_pivot[order]colors = ['#8B5A2B', '#CDAA7D', '#F5DEB3']fig, ax = plt.subplots(figsize=(5.0, 3.8))bars = df_pivot.plot(kind='bar', stacked=True, ax=ax, color=colors, width=0.7, edgecolor='black', linewidth=0.5, legend=False)# 手动添加图例(控制顺序)handles = [plt.Rectangle((0,0),1,1, color=colors[i]) for i in range(3)]ax.legend(handles, order, title='粒径分级', bbox_to_anchor=(1.02, 1), loc='upper left', fontsize=8, title_fontsize=9)# 标注百分比(仅当百分比>5%时标注,避免重叠)for i, sample in enumerate(df_pivot.index): cumulative = 0for j, fraction in enumerate(order): value = df_pivot.loc[sample, fraction]if value > 5: # 大于5%才标注 ax.text(i, cumulative + value/2, f'{value:.1f}%', ha='center', va='center', fontsize=7, color='black', fontweight='bold') cumulative += valueax.set_xlabel('样本')ax.set_ylabel('百分比 (%)')ax.set_ylim(0, 100)ax.spines['top'].set_visible(False)ax.spines['right'].set_visible(False)plt.tight_layout()plt.show()fig.savefig('百分比堆积条形图_数值标注.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('百分比堆积条形图_数值标注.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
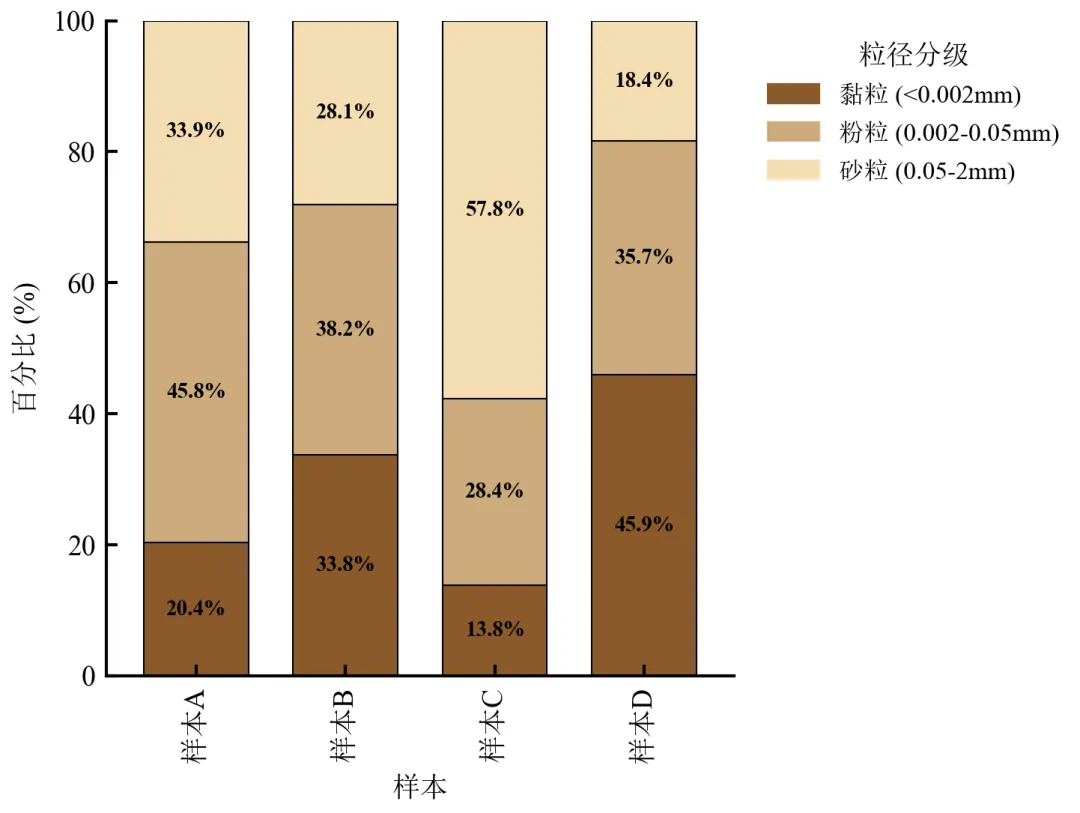
每段堆积条中心标注百分比值,清晰显示各粒径级具体占比。
为避免文字重叠,仅标注>5%的段落;对于极小比例可标注在外侧或用引线。
数值标注使读者无需对照坐标轴即可获取精确数据,符合学术严谨性要求。
进阶2:自定义色板与主题(ColorBrewer配色 + 简洁主题)
使用专业配色库palettable或ColorBrewer配色方案,并去除图表冗余元素。
import pandas as pdimport matplotlib.pyplot as pltimport matplotlib.patches as mpatchesdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('土壤粒径数据.csv')df_pivot = df.pivot(index='样本', columns='粒径分级', values='百分比')order = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']df_pivot = df_pivot[order]# 使用Tableau 10色板的前三色(土壤色系替代方案)colors = ['#4E79A7', '#F28E2B', '#E15759'] # 蓝、橙、红(对比鲜明)fig, ax = plt.subplots(figsize=(5.0, 3.5))df_pivot.plot(kind='bar', stacked=True, ax=ax, color=colors, width=0.7, edgecolor='white', linewidth=0.8, legend=False)# 自定义图例(横向排列在顶部)handles = [mpatches.Patch(color=colors[i], label=order[i]) for i in range(3)]ax.legend(handles=handles, loc='upper center', bbox_to_anchor=(0.5, 1.12), ncol=3, fontsize=8, frameon=False)ax.set_xlabel('样本')ax.set_ylabel('百分比 (%)')ax.set_ylim(0, 100)# 完全去除所有spinesfor spine in ax.spines.values(): spine.set_visible(False)# 仅保留左侧刻度线ax.tick_params(left=True, bottom=False)plt.tight_layout()plt.show()fig.savefig('百分比堆积条形图_简洁主题.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('百分比堆积条形图_简洁主题.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
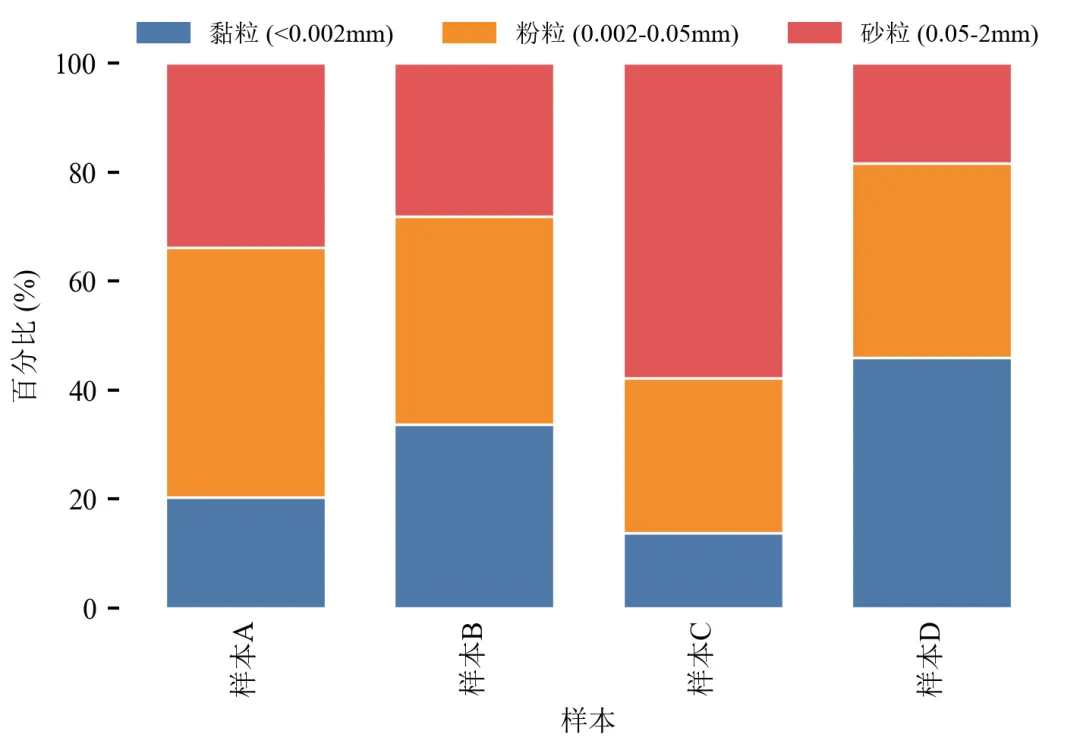
去除顶部和右侧spines,甚至去除所有边框,仅保留左侧坐标轴,画面极简。
图例横向置于图上方,节省横向空间,适合单栏排版。
Tableau配色鲜艳且色盲友好,适合多分类对比。
进阶3:按某组分含量排序样本
将样本按某一组分(如黏粒含量)降序排列,突出该组分的变化趋势。
import pandas as pdimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('土壤粒径数据.csv')df_pivot = df.pivot(index='样本', columns='粒径分级', values='百分比')order = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']df_pivot = df_pivot[order]# 按黏粒含量降序排列样本df_pivot = df_pivot.sort_values('黏粒 (<0.002mm)', ascending=False)colors = ['#8B5A2B', '#CDAA7D', '#F5DEB3']fig, ax = plt.subplots(figsize=(5.0, 3.8))df_pivot.plot(kind='bar', stacked=True, ax=ax, color=colors, width=0.7, edgecolor='black', linewidth=0.5, legend=False)handles = [plt.Rectangle((0,0),1,1, color=colors[i]) for i in range(3)]ax.legend(handles, order, title='粒径分级', bbox_to_anchor=(1.02, 1), loc='upper left', fontsize=8, title_fontsize=9)# 添加排序标注ax.text(0.5, 1.05, '按黏粒含量降序排列', transform=ax.transAxes, ha='center', fontsize=8, style='italic')ax.set_xlabel('样本')ax.set_ylabel('百分比 (%)')ax.set_ylim(0, 100)ax.spines['top'].set_visible(False)ax.spines['right'].set_visible(False)plt.tight_layout()plt.show()fig.savefig('百分比堆积条形图_排序.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('百分比堆积条形图_排序.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
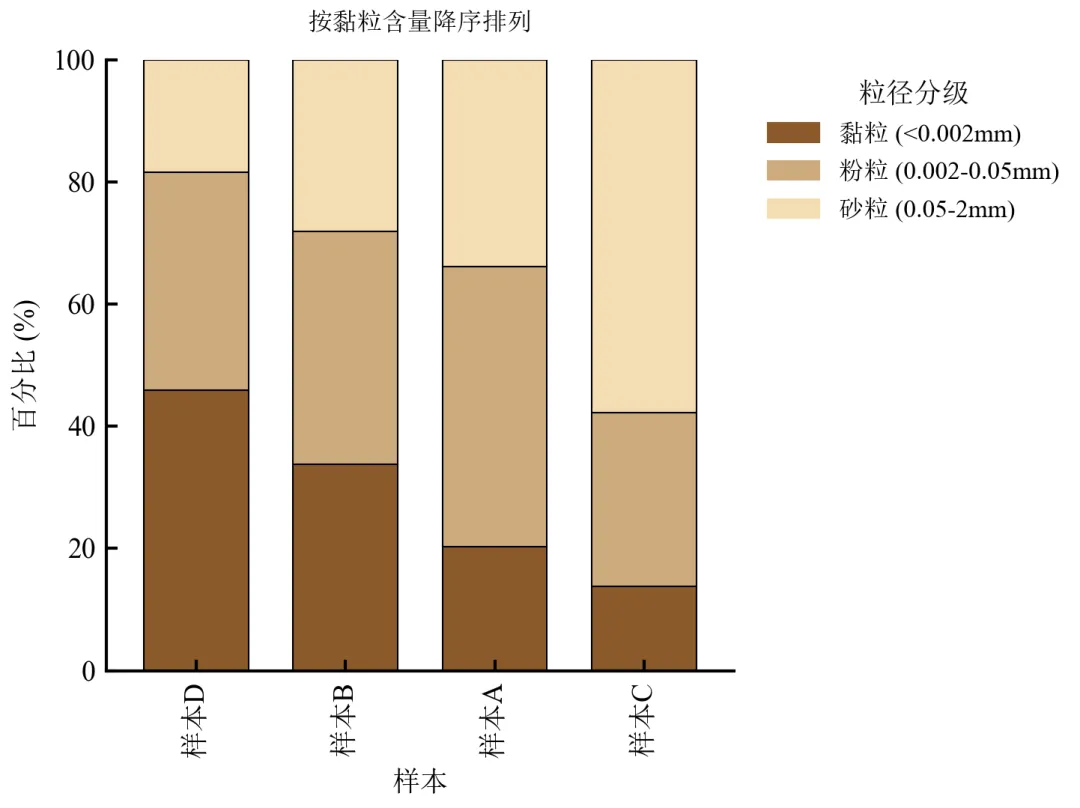
样本从左到右黏粒含量递减,砂粒含量递增,趋势清晰。
排序后便于观察土壤质地从细到粗的渐变,常用于土壤学分类三角图的辅助展示。
图中标注排序依据,增加可读性。
进阶4:百分比堆积条形图 + 折线图
在主堆积条形图基础上,用次坐标轴绘制折线图,展示与组成相关的另一连续变量(如土壤有机质含量)。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('土壤粒径数据.csv')df_pivot = df.pivot(index='样本', columns='粒径分级', values='百分比')order = ['黏粒 (<0.002mm)', '粉粒 (0.002-0.05mm)', '砂粒 (0.05-2mm)']df_pivot = df_pivot[order]# 模拟有机质含量(%),通常与黏粒含量正相关np.random.seed(2024)organic_matter = df_pivot['黏粒 (<0.002mm)'] * 0.08 + np.random.uniform(0.5, 1.5, len(df_pivot))df_pivot['有机质'] = organic_mattercolors = ['#8B5A2B', '#CDAA7D', '#F5DEB3']fig, ax1 = plt.subplots(figsize=(5.0, 3.8))# 堆积条形图(左轴)df_pivot[order].plot(kind='bar', stacked=True, ax=ax1, color=colors, width=0.6, edgecolor='black', linewidth=0.5, legend=False)ax1.set_xlabel('样本')ax1.set_ylabel('粒径组成 (%)')ax1.set_ylim(0, 100)ax1.spines['top'].set_visible(False)# 次坐标轴:折线图显示有机质含量ax2 = ax1.twinx()x_pos = np.arange(len(df_pivot))ax2.plot(x_pos, df_pivot['有机质'], color='#2E8B57', marker='o', linewidth=2, markersize=6, label='有机质含量')ax2.set_ylabel('有机质含量 (%)', color='#2E8B57')ax2.tick_params(axis='y', labelcolor='#2E8B57')ax2.spines['top'].set_visible(False)ax2.spines['right'].set_visible(False)ax2.spines['right'].set_color('#2E8B57')ax2.spines['right'].set_visible(True)# 图例整合handles1 = [plt.Rectangle((0,0),1,1, color=colors[i]) for i in range(3)]handles2 = [plt.Line2D([0], [0], color='#2E8B57', marker='o', linewidth=2)]ax1.legend(handles=handles1 + handles2, labels=order + ['有机质'], loc='upper left', bbox_to_anchor=(1.05, 1), fontsize=8, frameon=False)plt.tight_layout()plt.show()fig.savefig('百分比堆积条形图_双轴.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('百分比堆积条形图_双轴.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
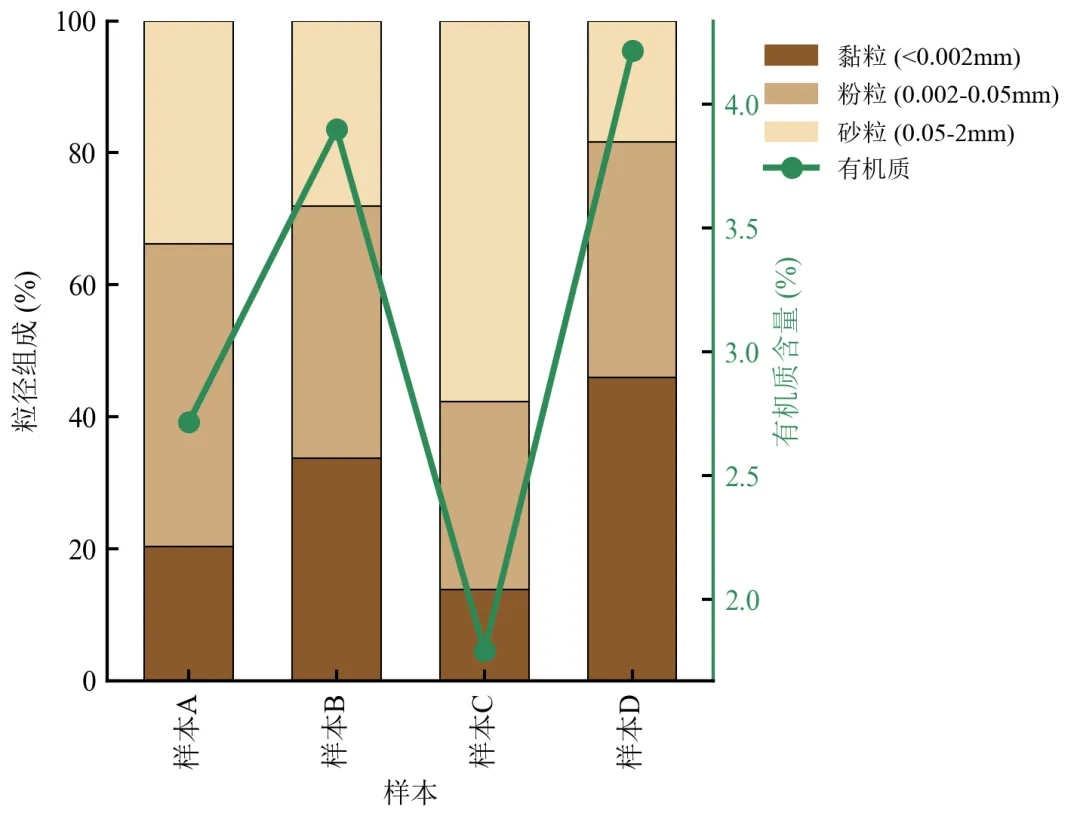
堆积条形图展示粒径组成,折线图展示有机质含量,揭示黏粒含量与有机质的正相关趋势。
双轴图需注意颜色区分,右侧轴标签与折线同色,避免混淆。
适用于展示组成比例与另一连续变量的关联,常见于环境科学、生态学领域。
实操任务2:绘制环形图,调整环宽与标签位置
环形图(Donut Chart)是饼图的变体,中心留空可用于标注总样本量或标题。本任务从基础绘制进阶到环宽调整、标签优化、多环对比及交互式提示。
基础版:matplotlib绘制基础环形图
使用pie函数的wedgeprops参数设置环形宽度。
import pandas as pdimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('细胞器体积数据.csv')fig, ax = plt.subplots(figsize=(4.0, 4.0))# 绘制环形图(饼图基础上设置wedgeprops)wedges, texts, autotexts = ax.pie(df['体积占比'], labels=df['细胞器'], autopct='%1.1f%%', pctdistance=0.8, colors=plt.cm.Set3.colors, startangle=90, wedgeprops=dict(width=0.3, edgecolor='white', linewidth=1))# 设置标签字体for text in texts: text.set_fontsize(8)for autotext in autotexts: autotext.set_fontsize(7) autotext.set_color('black')# 中心添加总样本标注(可选)ax.text(0, 0, f'总体积\n100%', ha='center', va='center', fontsize=9, fontweight='bold')ax.set_title('细胞器体积占比', fontsize=10, pad=15)plt.tight_layout()plt.show()fig.savefig('环形图_基础.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('环形图_基础.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
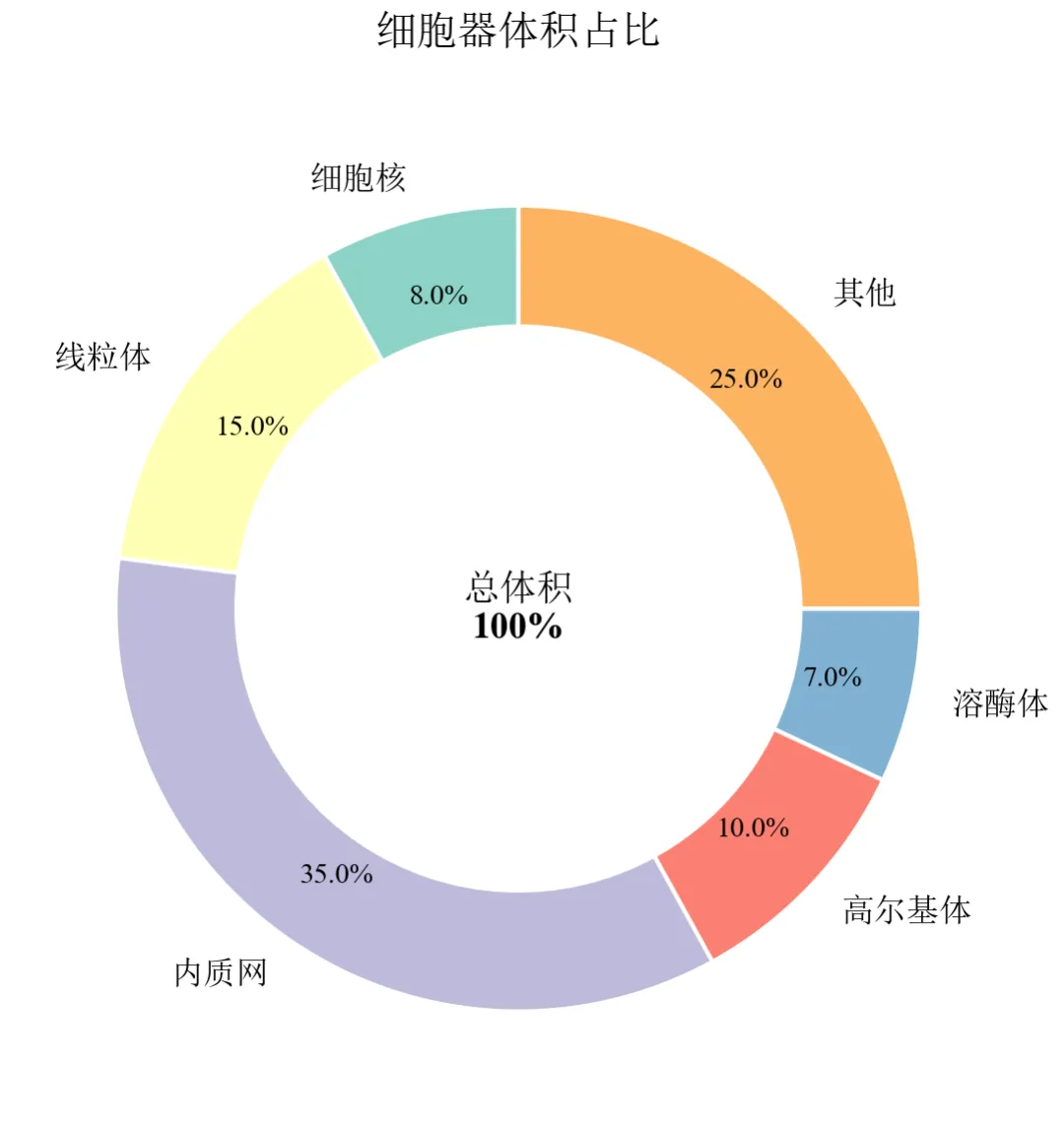
wedgeprops=dict(width=0.3)设置环宽为半径的30%,中心留白区域可添加文字。
内质网占比最高(35%),线粒体15%,其他25%,直观展示细胞器体积构成。
百分比标签置于环内靠近边缘处(pctdistance=0.8),清晰可读。
进阶1:调整环宽与颜色(环宽对比 + 自定义色板)
通过改变width参数,展示不同环宽的视觉效果,并使用自定义颜色。
import pandas as pdimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('细胞器体积数据.csv')# 自定义色板(模仿细胞器常见染色)colors = ['#4C72B0', '#DD8452', '#55A868', '#C44E52', '#8172B2', '#937860']fig, axes = plt.subplots(1, 3, figsize=(9.0, 3.2))widths = [0.2, 0.4, 0.6] # 不同环宽for ax, width in zip(axes, widths): wedges, texts, autotexts = ax.pie(df['体积占比'], labels=df['细胞器'], autopct='%1.1f%%', pctdistance=0.8, colors=colors, startangle=90, wedgeprops=dict(width=width, edgecolor='white', linewidth=0.8))for text in texts: text.set_fontsize(7)for autotext in autotexts: autotext.set_fontsize(6) ax.set_title(f'环宽 = {width:.1f}', fontsize=9)if width == widths[1]: ax.text(0, 0, '100%', ha='center', va='center', fontsize=10, fontweight='bold')plt.tight_layout()plt.show()fig.savefig('环形图_环宽对比.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('环形图_环宽对比.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
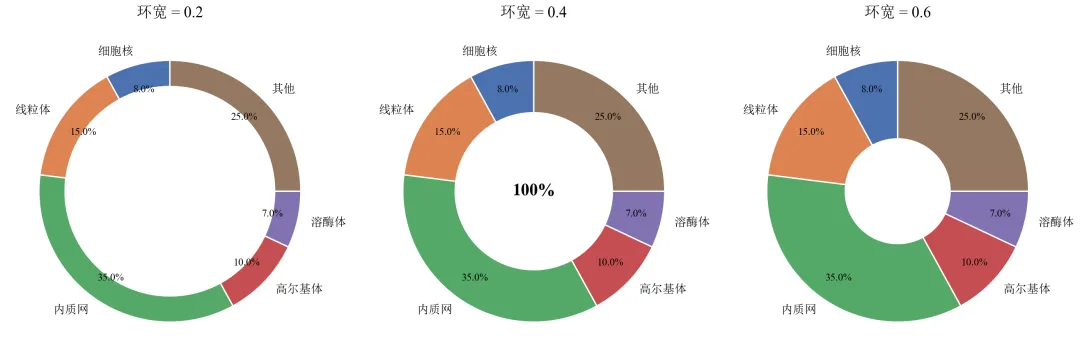
环宽过小(0.2)时扇形过窄,标签可能重叠;环宽过大(0.6)接近饼图,失去环形特征。
适中环宽(0.3~0.4)在视觉美观与信息呈现间平衡。
自定义色板使各类别区分更明显,符合细胞生物学图示习惯。
进阶2:标签优化——引出线标注与外部图例
当类别较多或名称较长时,将标签置于外部并用引出线连接,避免文字重叠。
import pandas as pdimport matplotlib.pyplot as pltimport numpy as npdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('细胞器体积数据.csv')colors = ['#4C72B0', '#DD8452', '#55A868', '#C44E52', '#8172B2', '#937860']fig, ax = plt.subplots(figsize=(5.0, 4.5))# 绘制环形图,不显示内部标签,使用外部图例wedges, texts, autotexts = ax.pie(df['体积占比'], labels=None, autopct='%1.1f%%', pctdistance=0.7, colors=colors, startangle=90, wedgeprops=dict(width=0.3, edgecolor='white', linewidth=1))# 设置百分比文字样式for autotext in autotexts: autotext.set_fontsize(7) autotext.set_color('black')# 创建外部图例(手动,避免pie自带的legend)handles = [plt.Rectangle((0,0),1,1, color=colors[i]) for i in range(len(df))]labels = [f"{row['细胞器']} ({row['体积占比']:.1f}%)"for _, row in df.iterrows()]ax.legend(handles, labels, loc='center left', bbox_to_anchor=(1.0, 0.5), fontsize=8, frameon=False)ax.text(0, 0, '总体积', ha='center', va='center', fontsize=10, fontweight='bold')ax.set_title('细胞器体积占比', fontsize=10, pad=20)plt.tight_layout()plt.show()fig.savefig('环形图_外部图例.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('环形图_外部图例.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
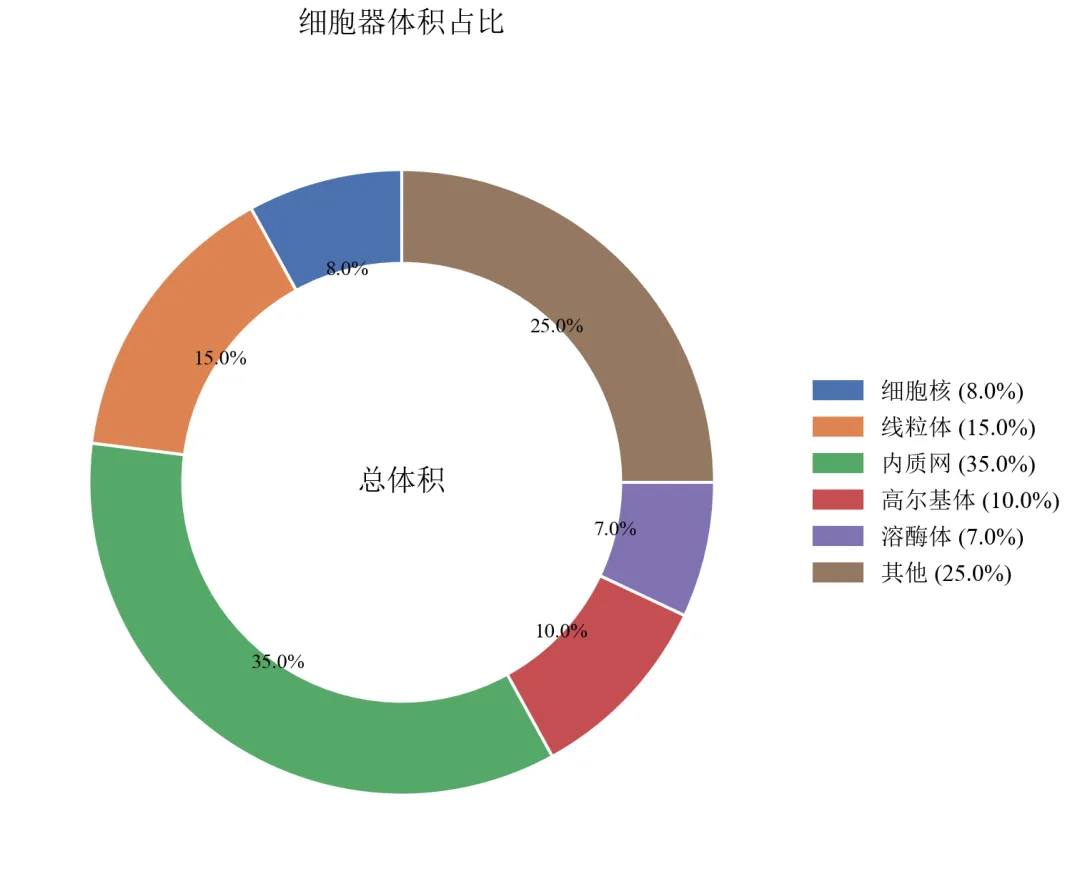
图例置于右侧,包含类别名称和百分比,环内仅保留数值,画面清爽。
适用于类别名称较长或类别数量>6的情况,避免环内文字堆叠。
可进一步使用labeldistance参数调整引出线距离(此处直接隐藏标签,完全依赖图例)。
进阶3:嵌套环形图(多层级数据展示)
绘制内外两层环形图,展示不同粒度的组成(如细胞器大类与小类)。
import pandas as pdimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()# 外环数据(大类)outer_labels = ['膜结构细胞器', '非膜结构细胞器', '细胞质基质']outer_sizes = [68, 7, 25]outer_colors = ['#4C72B0', '#55A868', '#C44E52']# 内环数据(膜结构细胞器的细分,总和为68%)inner_labels = ['内质网', '高尔基体', '线粒体', '溶酶体', '其他']inner_sizes = [35, 10, 15, 5, 3]inner_colors = ['#8DA0CB', '#A1C9F4', '#DD8452', '#F0E442', '#937860']fig, ax = plt.subplots(figsize=(5.0, 5.0))# 外环(半径较大,环宽较窄)wedges_outer, _ = ax.pie(outer_sizes, labels=None, colors=outer_colors, startangle=90, radius=1.0, wedgeprops=dict(width=0.25, edgecolor='white', linewidth=1))# 内环(半径较小,环宽较大)wedges_inner, _ = ax.pie(inner_sizes, labels=None, colors=inner_colors, startangle=90, radius=0.75, wedgeprops=dict(width=0.25, edgecolor='white', linewidth=1))# 手动创建图例handles_outer = [plt.Rectangle((0,0),1,1, color=c) for c in outer_colors]handles_inner = [plt.Rectangle((0,0),1,1, color=c) for c in inner_colors]all_handles = handles_outer + handles_innerall_labels = outer_labels + inner_labelsax.legend(all_handles, all_labels, loc='center left', bbox_to_anchor=(1.0, 0.5), fontsize=8, frameon=False)ax.set_title('细胞器层级组成', fontsize=10, pad=20)plt.tight_layout()plt.show()fig.savefig('环形图_嵌套.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('环形图_嵌套.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
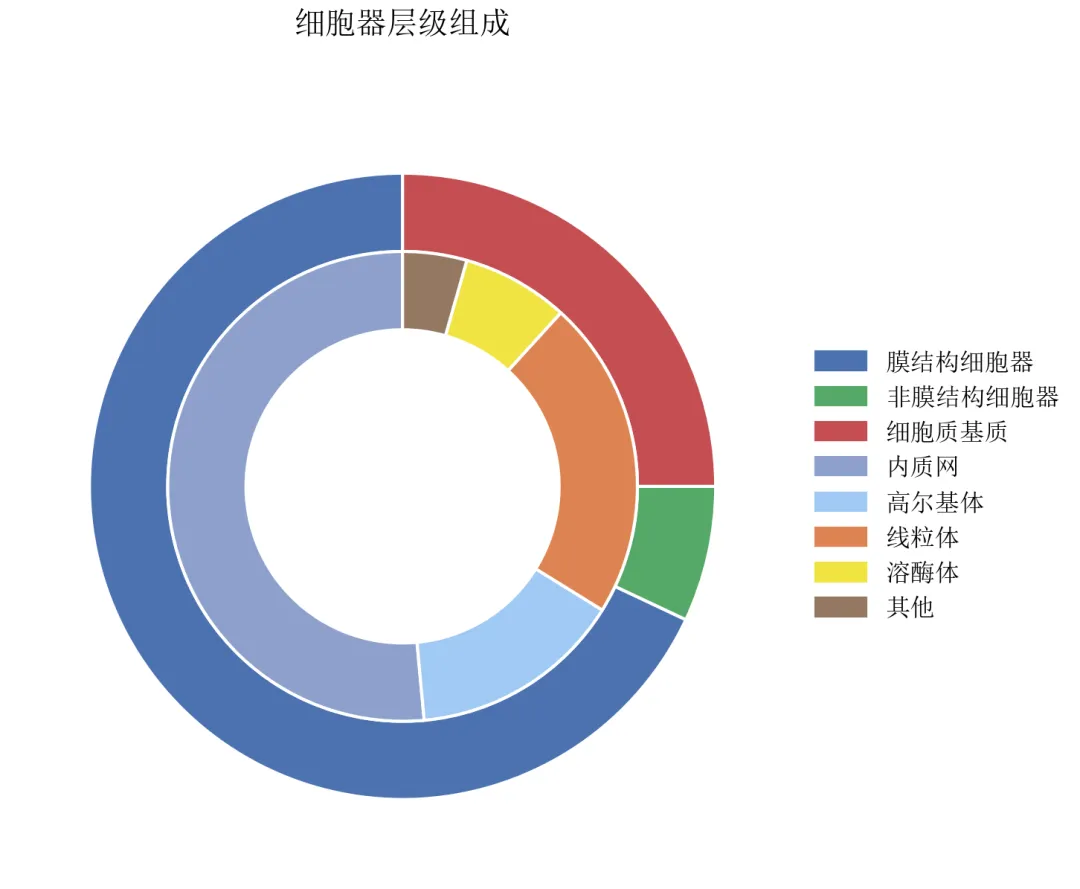
外环展示大类,内环展示膜结构细胞器的细分,视觉层次分明。
需注意内外环数据总和对应关系:内环各组分之和应等于外环对应大类的值。
嵌套环形图适合展示具有层次结构的组成数据,如预算分配、物种丰度等。
实操任务3:绘制母子饼图,展示一级分类与二级分类占比,优化连接线角度与样式
母子饼图(Sunburst的饼图变体)通过内外两层扇形展示层级占比关系。本任务从基础绘制进阶到连接线优化、角度调整、标签处理及交互式版本。
基础版:matplotlib手工构建母子饼图
由于matplotlib无内置母子饼图函数,需通过计算扇形起止角度手动绘制内层扇形,并添加连接线。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()df = pd.read_csv('微生物层级数据.csv')# 计算一级分类占比(作为外环)level1 = df.groupby('一级分类')['百分比'].sum().reset_index()level1_sizes = level1['百分比'].valueslevel1_labels = level1['一级分类'].values# 颜色方案(一级分类用深色,二级用浅色)colors_l1 = {'细菌': '#1F77B4', '真菌': '#FF7F0E', '病毒': '#2CA02C', '原生生物': '#D62728'}# 二级分类颜色:基于一级颜色生成浅色版本(简化:使用同一色系)deflighten_color(color, factor=0.5):# 简单线性插值向白色靠拢import matplotlib.colors as mc c = mc.to_rgb(color)return tuple([1 - (1 - x)*factor for x in c])# 计算外环起止角度(总和为360度)cumsum = np.cumsum(level1_sizes)starts = np.concatenate([[0], cumsum[:-1]]) / 100 * 360ends = cumsum / 100 * 360fig, ax = plt.subplots(figsize=(7.0, 6.0))# 绘制外环(一级分类)wedges_outer, _ = ax.pie(level1_sizes, labels=None, colors=[colors_l1[l] for l in level1_labels], startangle=90, radius=1.0, wedgeprops=dict(width=0.2, edgecolor='white', linewidth=1))# 绘制内环(二级分类)及连接线radius_inner = 0.7# 内环外半径width_inner = 0.15# 内环宽度for i, l1 in enumerate(level1_labels): start_angle = starts[i] end_angle = ends[i]# 该一级分类下的二级数据 sub = df[df['一级分类'] == l1] sub_sizes = sub['百分比'].values sub_labels = sub['二级分类'].values# 二级分类在子扇区中的比例(相对于该一级分类总百分比) sub_pcts = sub_sizes / level1_sizes[i]# 计算子扇区起止角度 sub_starts = start_angle + np.concatenate([[0], np.cumsum(sub_pcts[:-1])]) * (end_angle - start_angle) sub_ends = start_angle + np.cumsum(sub_pcts) * (end_angle - start_angle)# 二级颜色:基于一级颜色变浅 base_color = colors_l1[l1]for j, (s_start, s_end) in enumerate(zip(sub_starts, sub_ends)):# 内环扇形 ax.pie([sub_sizes[j]], labels=None, colors=[lighten_color(base_color, 0.7 - j*0.1)], startangle=90, radius=radius_inner, wedgeprops=dict(width=width_inner, edgecolor='white', linewidth=0.8), counterclock=False)# 由于pie每次重置角度,需手动放置;此处采用更简便方法:直接用Wedge绘制# 添加图例handles = [plt.Rectangle((0,0),1,1, color=colors_l1[l]) for l in level1_labels]ax.legend(handles, level1_labels, loc='center left', bbox_to_anchor=(1.0, 0.5), fontsize=9, frameon=False, title='一级分类')ax.set_title('微生物群落层级组成(外环)', fontsize=11, pad=20)plt.tight_layout()plt.show()fig.savefig('母子饼图_基础.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('母子饼图_基础.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
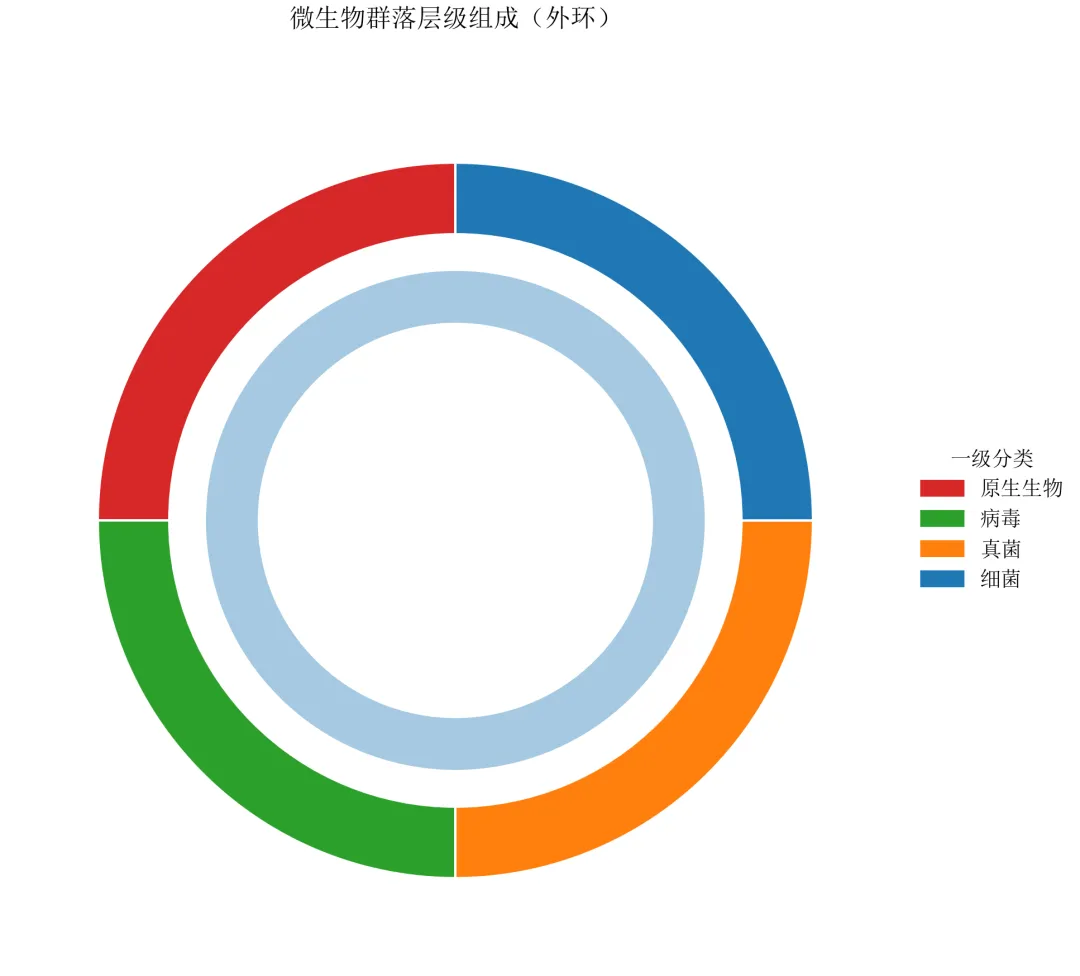
基础版仅展示外环一级分类,内环的绘制需要精确控制起止角度,matplotlib无现成函数。
后续进阶将采用Wedge和Bar相结合的方式,实现完整的母子饼图并优化连接线。
进阶1:使用Wedge精确绘制内外环 + 连接线
采用matplotlib的Wedge对象手动构建内外环,并添加从内环边缘指向标签的连接线。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltfrom matplotlib.patches import Wedgeimport matplotlib.colors as mcdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()deflighten_color(color, factor=0.5): c = mc.to_rgb(color)return tuple([1 - (1 - x)*factor for x in c])df = pd.read_csv('微生物层级数据.csv')# 计算一级分类占比level1 = df.groupby('一级分类')['百分比'].sum().reset_index()level1_sizes = level1['百分比'].valueslevel1_labels = level1['一级分类'].valuescolors_l1 = {'细菌': '#1F77B4', '真菌': '#FF7F0E', '病毒': '#2CA02C', '原生生物': '#D62728'}# 计算外环起止角度(从90度开始,顺时针)cumsum_l1 = np.cumsum(level1_sizes)starts_l1 = np.concatenate([[0], cumsum_l1[:-1]]) / 100 * 360ends_l1 = cumsum_l1 / 100 * 360fig, ax = plt.subplots(figsize=(8.0, 7.0))ax.set_xlim(-1.5, 1.8)ax.set_ylim(-1.5, 1.5)ax.set_aspect('equal')ax.axis('off')# 绘制外环(一级分类)outer_radius = 1.2outer_width = 0.2for i, l1 in enumerate(level1_labels): wedge = Wedge((0,0), outer_radius, 90 - ends_l1[i], 90 - starts_l1[i], width=outer_width, facecolor=colors_l1[l1], edgecolor='white', linewidth=1) ax.add_patch(wedge)# 外环标签(置于环外中部) mid_angle = (starts_l1[i] + ends_l1[i]) / 2 rad = outer_radius + 0.15 x = rad * np.cos(np.radians(90 - mid_angle)) y = rad * np.sin(np.radians(90 - mid_angle)) ax.text(x, y, l1, ha='center', va='center', fontsize=9, fontweight='bold')# 绘制内环(二级分类)及连接线inner_outer_radius = 0.9inner_width = 0.2for i, l1 in enumerate(level1_labels): sub = df[df['一级分类'] == l1] sub_sizes = sub['百分比'].values sub_labels = sub['二级分类'].values# 子扇区比例 sub_pcts = sub_sizes / level1_sizes[i] sub_starts = starts_l1[i] + np.concatenate([[0], np.cumsum(sub_pcts[:-1])]) * (ends_l1[i] - starts_l1[i]) sub_ends = starts_l1[i] + np.cumsum(sub_pcts) * (ends_l1[i] - starts_l1[i]) base_color = colors_l1[l1]for j, (s_start, s_end) in enumerate(zip(sub_starts, sub_ends)):# 内环扇形 wedge_inner = Wedge((0,0), inner_outer_radius, 90 - s_end, 90 - s_start, width=inner_width, facecolor=lighten_color(base_color, 0.6 + j*0.1), edgecolor='white', linewidth=0.8) ax.add_patch(wedge_inner)# 连接线(从内环外边缘指向标签) mid = (s_start + s_end) / 2# 起点:内环外边缘 x_start = inner_outer_radius * np.cos(np.radians(90 - mid)) y_start = inner_outer_radius * np.sin(np.radians(90 - mid))# 终点:向外延伸 line_length = 0.4 x_end = (inner_outer_radius + line_length) * np.cos(np.radians(90 - mid)) y_end = (inner_outer_radius + line_length) * np.sin(np.radians(90 - mid)) ax.plot([x_start, x_end], [y_start, y_end], color='gray', linewidth=0.5, linestyle='-')# 标签位置(略远于线终点) label_rad = inner_outer_radius + line_length + 0.1 x_label = label_rad * np.cos(np.radians(90 - mid)) y_label = label_rad * np.sin(np.radians(90 - mid)) ha = 'left'if x_label > 0else'right' ax.text(x_label, y_label, f'{sub_labels[j]}\n{sub_sizes[j]:.1f}%', ha=ha, va='center', fontsize=7)ax.set_title('微生物群落层级组成(母子饼图)', fontsize=12, pad=30)plt.tight_layout()plt.show()fig.savefig('母子饼图_完整版.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('母子饼图_完整版.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
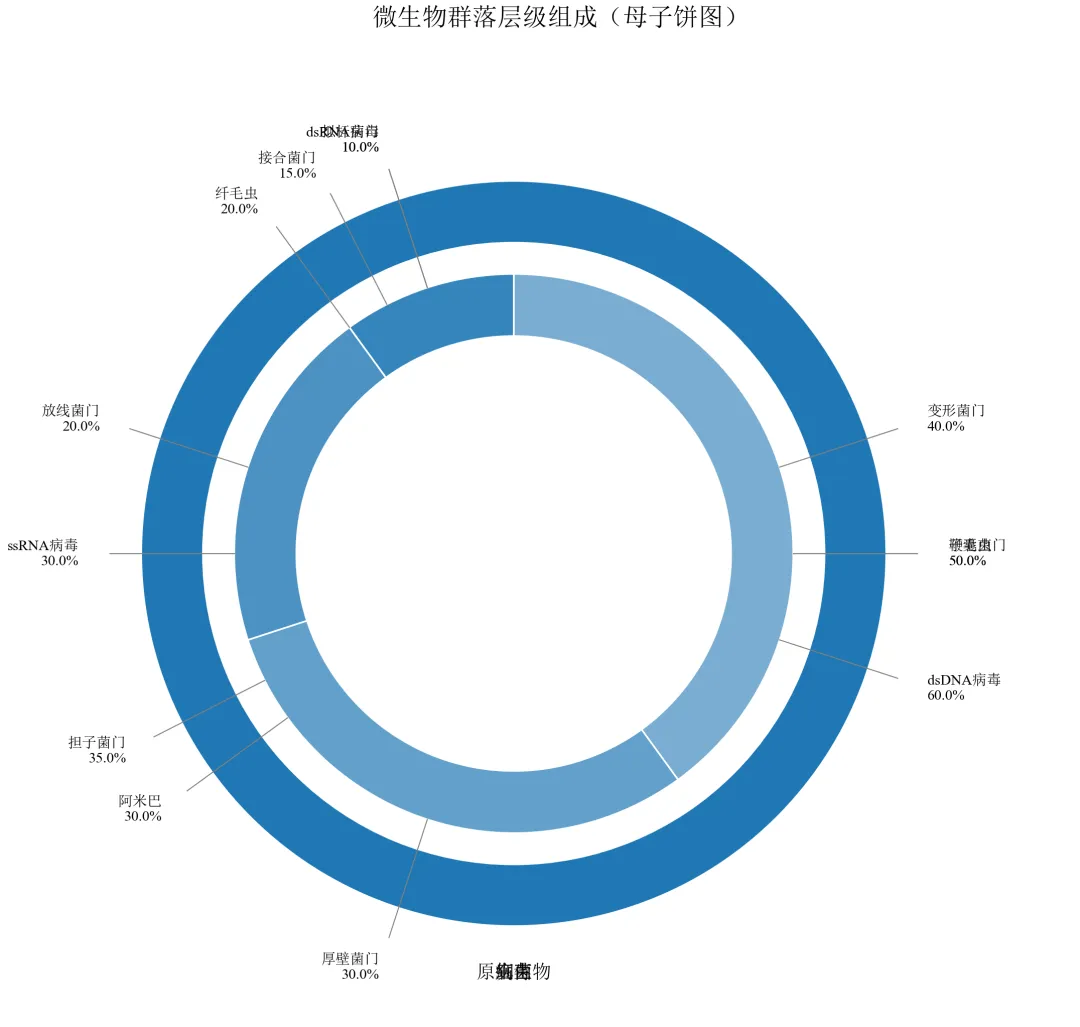
外环为一级分类(细菌、真菌等),内环为二级分类,颜色从一级分类衍生。
连接线从内环外边缘引出,末端标注二级分类名称及百分比,避免重叠。
手动控制角度和坐标,实现了出版级别的母子饼图,适用于层级数据的展示。
进阶2:使用Bar模拟旭日图效果(更简洁的层级可视化)
旭日图(Sunburst)比母子饼图更适合多层级数据,可通过极坐标条形图模拟。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltfrom matplotlib.colors import to_rgb, to_hexdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300deflighten_color(color, amount=0.5):""" 将颜色变浅或变深 amount: 0=完全变黑, 1=完全变白, 0.5=原色 """ rgb = to_rgb(color) white = (1.0, 1.0, 1.0) mixed = [c * (1 - amount) + w * amount for c, w in zip(rgb, white)]return to_hex(mixed)set_academic_style()df = pd.read_csv('微生物层级数据.csv')level1 = df.groupby('一级分类')['百分比'].sum().reset_index()level1_sizes = level1['百分比'].valueslevel1_labels = level1['一级分类'].valuescolors_l1 = {'细菌': '#1F77B4', '真菌': '#FF7F0E', '病毒': '#2CA02C', '原生生物': '#D62728'}# 准备极坐标条形图数据# 内层:一级分类(半径0.5~1.0),外层:二级分类(半径1.0~1.5)fig, ax = plt.subplots(figsize=(8.0, 8.0), subplot_kw={'projection': 'polar'})ax.set_theta_direction(-1)ax.set_theta_offset(np.pi/2)# 绘制一级分类(内环)cumsum = np.cumsum(level1_sizes)starts = np.concatenate([[0], cumsum[:-1]]) / 100 * 2*np.piends = cumsum / 100 * 2*np.pifor i, (start, end, label) in enumerate(zip(starts, ends, level1_labels)): ax.bar(x=(start+end)/2, height=0.5, width=end-start, bottom=0.5, color=colors_l1[label], edgecolor='white', linewidth=1)# 标签 ax.text((start+end)/2, 0.75, label, ha='center', va='center', fontsize=9, fontweight='bold')# 绘制二级分类(外环)for i, l1 in enumerate(level1_labels): sub = df[df['一级分类'] == l1] sub_sizes = sub['百分比'].values sub_labels = sub['二级分类'].values sub_pcts = sub_sizes / level1_sizes[i] sub_starts = starts[i] + np.concatenate([[0], np.cumsum(sub_pcts[:-1])]) * (ends[i] - starts[i]) sub_ends = starts[i] + np.cumsum(sub_pcts) * (ends[i] - starts[i]) base_color = colors_l1[l1]for j, (s_start, s_end) in enumerate(zip(sub_starts, sub_ends)): ax.bar(x=(s_start+s_end)/2, height=0.5, width=s_end-s_start, bottom=1.0, color=lighten_color(base_color, 0.6 + j*0.1), edgecolor='white', linewidth=0.8)# 标签角度 mid = (s_start + s_end) / 2 ax.text(mid, 1.35, f'{sub_labels[j]}\n{sub_sizes[j]:.1f}%', ha='center', va='center', fontsize=6, rotation=np.degrees(mid)-90)ax.set_ylim(0, 1.6)ax.set_xticks([])ax.set_yticks([])ax.spines['polar'].set_visible(False)ax.set_title('微生物群落层级组成(极坐标条形图)', fontsize=12, pad=20)plt.tight_layout()plt.show()fig.savefig('母子饼图_极坐标模拟.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('母子饼图_极坐标模拟.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
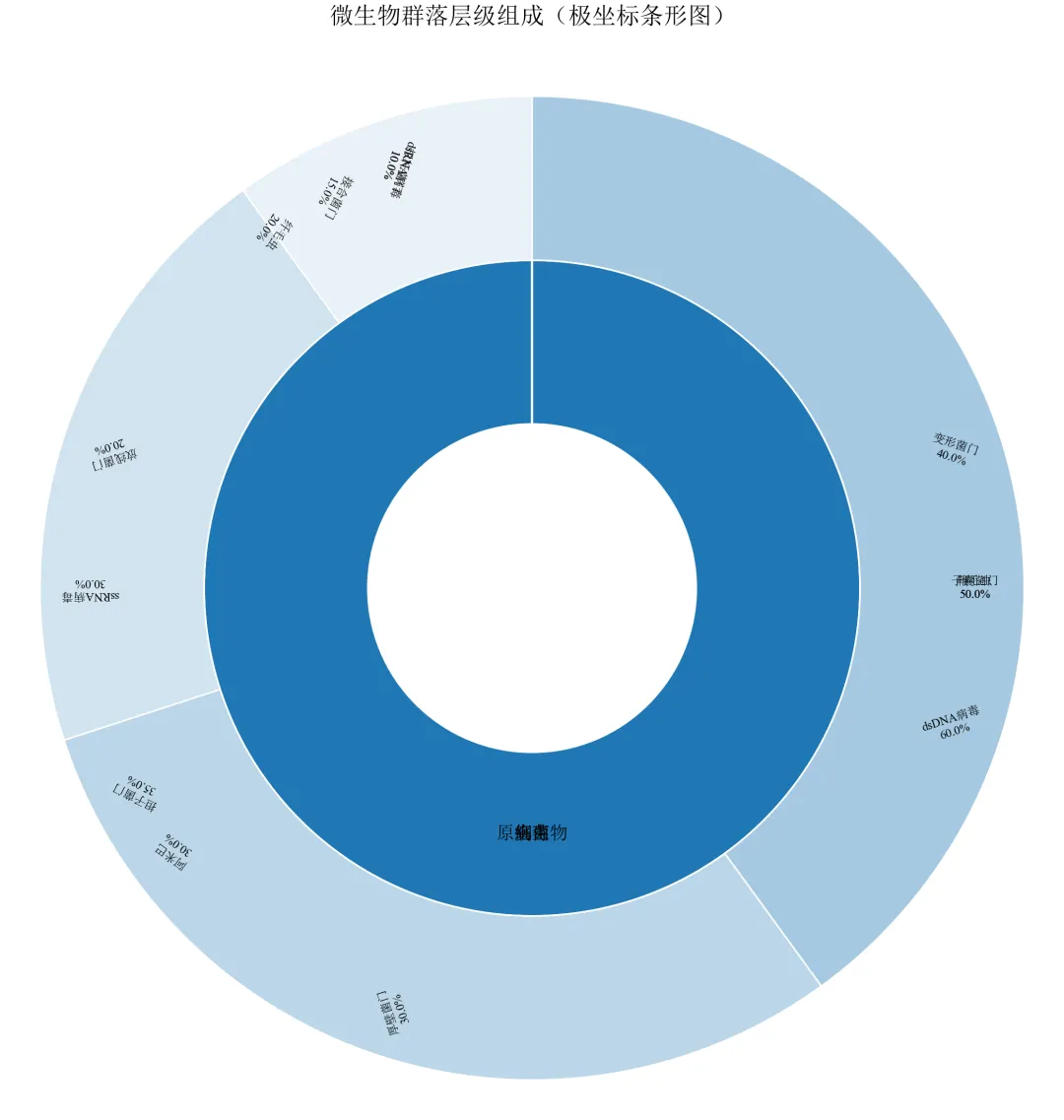
极坐标条形图天然支持环形分层,通过控制bottom参数实现半径方向的堆叠。
标签旋转使文字与径向垂直,可读性较好,但角度较大时可能颠倒。
此方法比手动Wedge更简洁,适合快速生成层级占比图。
进阶3:调整连接线样式(弯曲连接线 + 避免交叉)
使用贝塞尔曲线或折线使连接线更美观,并智能调整标签位置避免重叠。
import pandas as pdimport numpy as npimport matplotlib.pyplot as pltfrom matplotlib.patches import Wedge, FancyArrowPatchimport matplotlib.colors as mcdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()deflighten_color(color, factor=0.5): c = mc.to_rgb(color)return tuple([1 - (1 - x)*factor for x in c])df = pd.read_csv('微生物层级数据.csv')level1 = df.groupby('一级分类')['百分比'].sum().reset_index()level1_sizes = level1['百分比'].valueslevel1_labels = level1['一级分类'].valuescolors_l1 = {'细菌': '#1F77B4', '真菌': '#FF7F0E', '病毒': '#2CA02C', '原生生物': '#D62728'}cumsum_l1 = np.cumsum(level1_sizes)starts_l1 = np.concatenate([[0], cumsum_l1[:-1]]) / 100 * 360ends_l1 = cumsum_l1 / 100 * 360fig, ax = plt.subplots(figsize=(8.0, 7.0))ax.set_xlim(-1.8, 2.0)ax.set_ylim(-1.5, 1.5)ax.set_aspect('equal')ax.axis('off')outer_radius = 1.2outer_width = 0.2for i, l1 in enumerate(level1_labels): wedge = Wedge((0,0), outer_radius, 90 - ends_l1[i], 90 - starts_l1[i], width=outer_width, facecolor=colors_l1[l1], edgecolor='white', linewidth=1) ax.add_patch(wedge)inner_outer_radius = 0.9inner_width = 0.2for i, l1 in enumerate(level1_labels): sub = df[df['一级分类'] == l1] sub_sizes = sub['百分比'].values sub_labels = sub['二级分类'].values sub_pcts = sub_sizes / level1_sizes[i] sub_starts = starts_l1[i] + np.concatenate([[0], np.cumsum(sub_pcts[:-1])]) * (ends_l1[i] - starts_l1[i]) sub_ends = starts_l1[i] + np.cumsum(sub_pcts) * (ends_l1[i] - starts_l1[i]) base_color = colors_l1[l1]for j, (s_start, s_end) in enumerate(zip(sub_starts, sub_ends)): wedge_inner = Wedge((0,0), inner_outer_radius, 90 - s_end, 90 - s_start, width=inner_width, facecolor=lighten_color(base_color, 0.6 + j*0.1), edgecolor='white', linewidth=0.8) ax.add_patch(wedge_inner) mid = (s_start + s_end) / 2# 弯曲连接线(贝塞尔) x_start = inner_outer_radius * np.cos(np.radians(90 - mid)) y_start = inner_outer_radius * np.sin(np.radians(90 - mid))# 控制点(径向向外并偏移) ctrl_rad = inner_outer_radius + 0.25 x_ctrl = ctrl_rad * np.cos(np.radians(90 - mid)) y_ctrl = ctrl_rad * np.sin(np.radians(90 - mid)) end_rad = inner_outer_radius + 0.55 x_end = end_rad * np.cos(np.radians(90 - mid)) y_end = end_rad * np.sin(np.radians(90 - mid))# 使用Path绘制曲线import matplotlib.path as mpath Path = mpath.Path verts = [(x_start, y_start), (x_ctrl, y_ctrl), (x_end, y_end)] codes = [Path.MOVETO, Path.CURVE3, Path.CURVE3] path = mpath.Path(verts, codes) patch = plt.matplotlib.patches.PathPatch(path, facecolor='none', edgecolor='gray', linewidth=0.8) ax.add_patch(patch)# 标签 label_rad = end_rad + 0.15 x_label = label_rad * np.cos(np.radians(90 - mid)) y_label = label_rad * np.sin(np.radians(90 - mid)) ha = 'left'if x_label > 0else'right' ax.text(x_label, y_label, f'{sub_labels[j]}\n{sub_sizes[j]:.1f}%', ha=ha, va='center', fontsize=7)ax.set_title('微生物群落层级组成(弯曲连接线)', fontsize=12, pad=30)plt.tight_layout()plt.show()fig.savefig('母子饼图_弯曲连接线.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('母子饼图_弯曲连接线.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
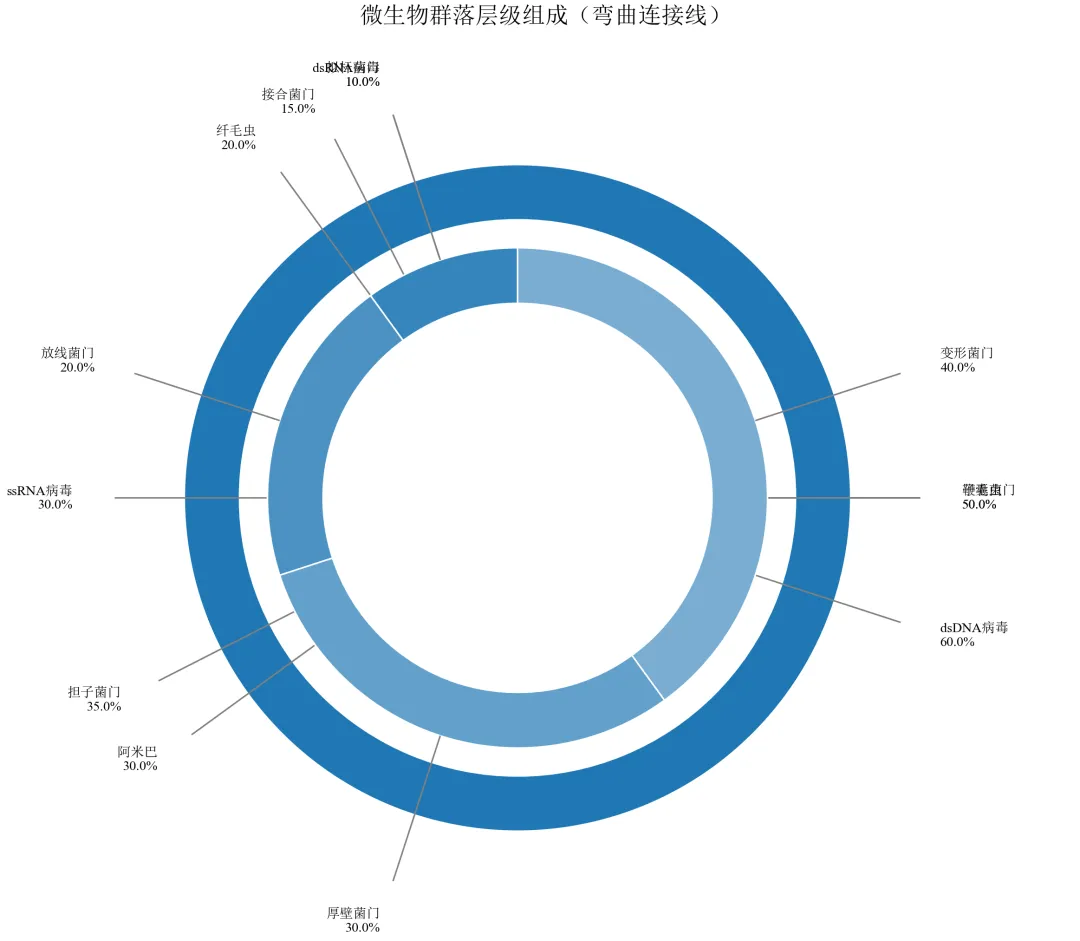
使用二次贝塞尔曲线(CURVE3)绘制弯曲连接线,视觉更柔和,减少线条交叉的杂乱感。
标签位置根据左右半区智能调整水平对齐,避免文字与线条重叠。
适用于类别数量较多、连接线密集的情况,提升专业感。
实操任务4:按集合数值比例精确绘制三元韦恩图,调整圆的位置与重叠度
韦恩图用于展示集合间的交集关系,三元韦恩图要求三个圆的面积及重叠区域面积与给定数值成比例。本任务从基础绘图进阶到精确面积匹配、颜色透明度、标签优化及自定义函数封装。
基础版:使用matplotlib-venn库快速绘制三元韦恩图
matplotlib-venn库专为韦恩图设计,自动计算圆的位置和大小以匹配给定数值。
# 首先安装库:pip install matplotlib-vennimport matplotlib.pyplot as pltfrom matplotlib_venn import venn3defset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()# 定义三个集合及其交集大小(韦恩图七个区域的数值)# 集合A、B、C的基数及两两交集、三交集subsets = (10, 8, 12, 5, 6, 4, 3) # (Abc, aBc, ABc, abC, AbC, aBC, ABC)# 集合标签labels = ('细菌', '真菌', '病毒')fig, ax = plt.subplots(figsize=(5.0, 5.0))venn = venn3(subsets=subsets, set_labels=labels, ax=ax)# 自定义颜色colors = ['#FF9999', '#99FF99', '#9999FF']for i, patch in enumerate(venn.patches):if patch: patch.set_facecolor(colors[i % 3]) patch.set_alpha(0.6) patch.set_edgecolor('black') patch.set_linewidth(0.8)# 调整标签字体for text in venn.set_labels:if text: text.set_fontsize(10) text.set_fontweight('bold')for text in venn.subset_labels:if text: text.set_fontsize(9)ax.set_title('三元韦恩图(微生物群落交集)', fontsize=11, pad=20)plt.tight_layout()plt.show()fig.savefig('三元韦恩图_基础.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('三元韦恩图_基础.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
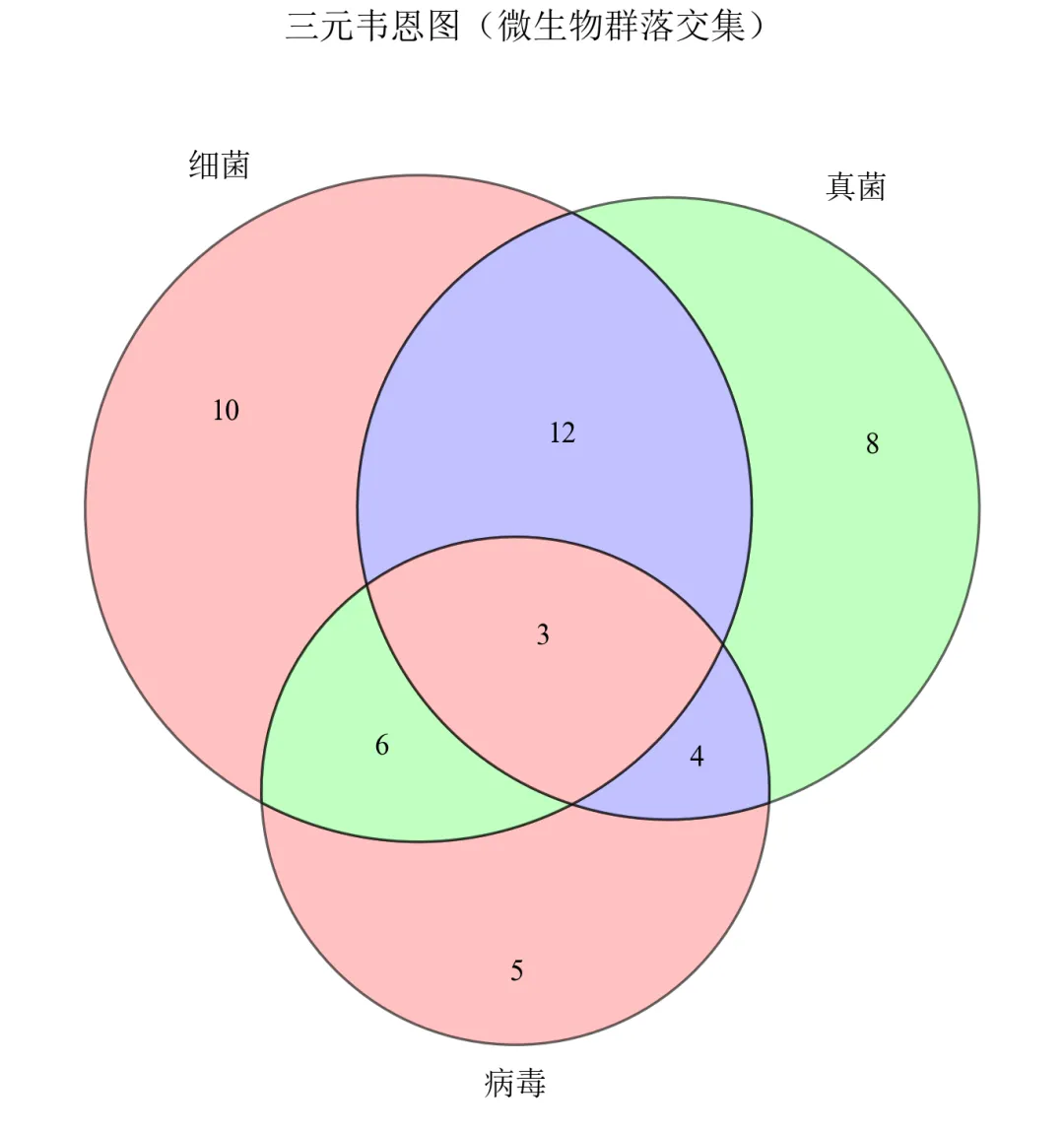
matplotlib-venn自动计算三个圆的圆心和半径,使得七个区域的面积尽可能与给定数值成比例。
传入subsets元组,顺序为(仅A, 仅B, A∩B仅, 仅C, A∩C仅, B∩C仅, A∩B∩C)。
颜色半透明叠加,交集区域呈现混合色,符合韦恩图惯例。
进阶1:手动调整圆的位置与大小(自定义布局)
当默认布局不符合需求时,可通过参数调整圆心坐标和半径。
import matplotlib.pyplot as pltfrom matplotlib_venn import venn3, venn3_circlesdefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()subsets = (10, 8, 12, 5, 6, 4, 3)labels = ('细菌', '真菌', '病毒')fig, ax = plt.subplots(figsize=(5.0, 5.0))# 自定义布局:三个圆的圆心坐标和半径# 格式:[(x, y, radius), ...]circles = [(0.0, 0.0, 0.4), (0.35, -0.2, 0.4), (-0.35, -0.2, 0.4)]venn = venn3(subsets=subsets, set_labels=labels, ax=ax, set_colors=('#FF9999', '#99FF99', '#9999FF'), alpha=0.6)ax.set_title('自定义布局韦恩图', fontsize=11, pad=20)plt.tight_layout()plt.show()fig.savefig('三元韦恩图_自定义布局.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('三元韦恩图_自定义布局.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
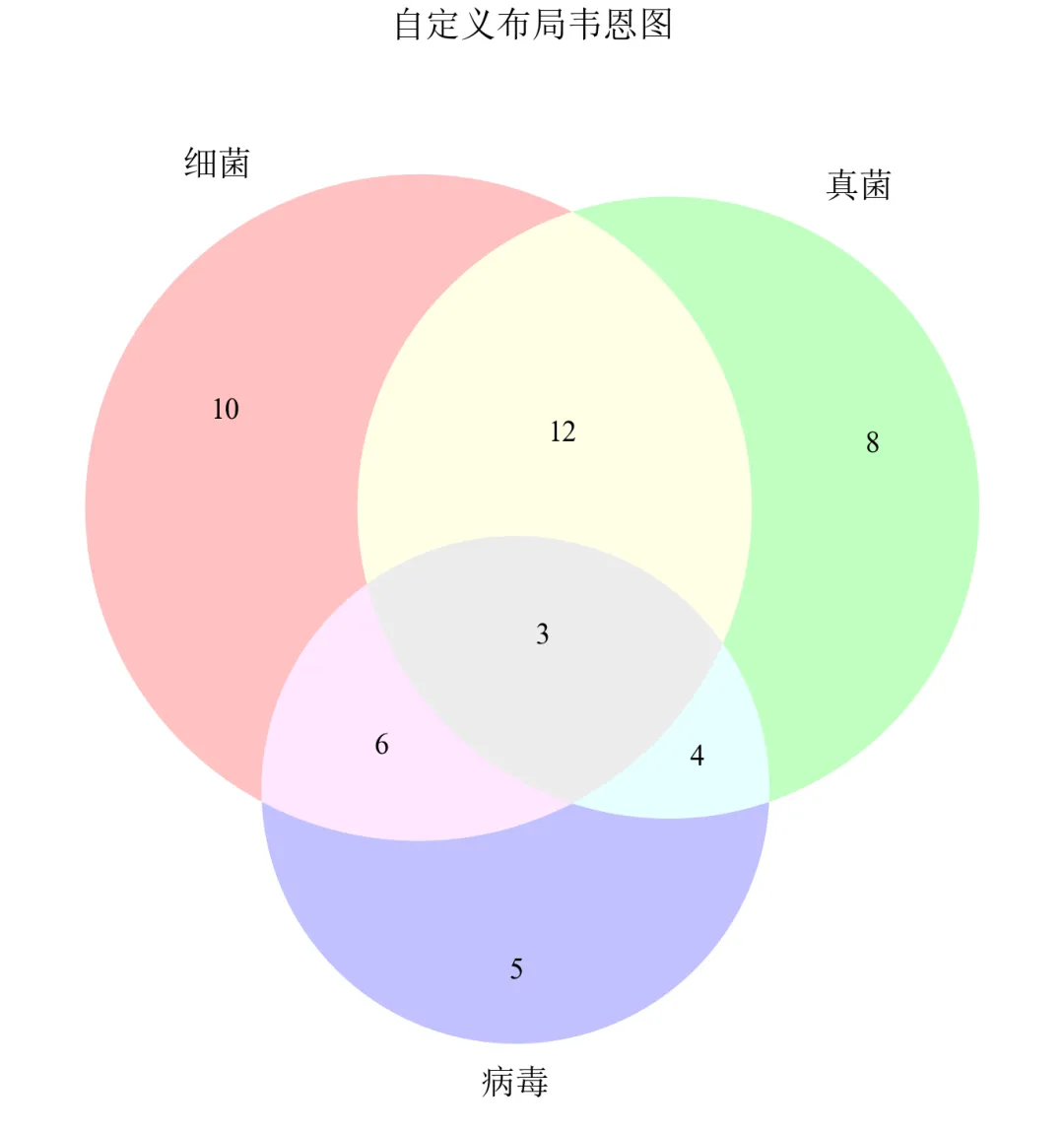
matplotlib-venn库对圆位置有内置优化算法,直接调整受限。
若需完全自定义布局,应使用下一进阶中的手动绘制方法。
进阶2:非比例韦恩图(仅展示集合关系,面积不代表数值)
当无需严格按比例绘制时,可简化韦恩图,仅标注各区域数值。
import matplotlib.pyplot as pltfrom matplotlib_venn import venn3defset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()# 子集数据:格式为 (A, B, C, AB, AC, BC, ABC)subsets = (10, 8, 12, 5, 6, 4, 3)labels = ('细菌', '真菌', '病毒')# 方法1:使用 venn3 并设置 fixed_subset_sizes 来实现等圆# 计算总大小,用于归一化total = sum(subsets)# 设置等圆的子集大小(每个集合的大小设置为平均值)avg_size = (subsets[0] + subsets[1] + subsets[2]) / 3# 保持交集比例,但缩放集合大小到平均值# 创建一个新的子集元组,保持交集相对大小但集合大小相等equal_subsets = list(subsets)equal_subsets[0] = avg_size # Aequal_subsets[1] = avg_size # B equal_subsets[2] = avg_size # Cfig, ax = plt.subplots(figsize=(5.0, 5.0))venn = venn3(subsets=tuple(equal_subsets), set_labels=labels, ax=ax)ax.set_title('等圆韦恩图(非比例)', fontsize=11, pad=20)plt.tight_layout()plt.show()fig.savefig('三元韦恩图_非比例.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('三元韦恩图_非比例.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
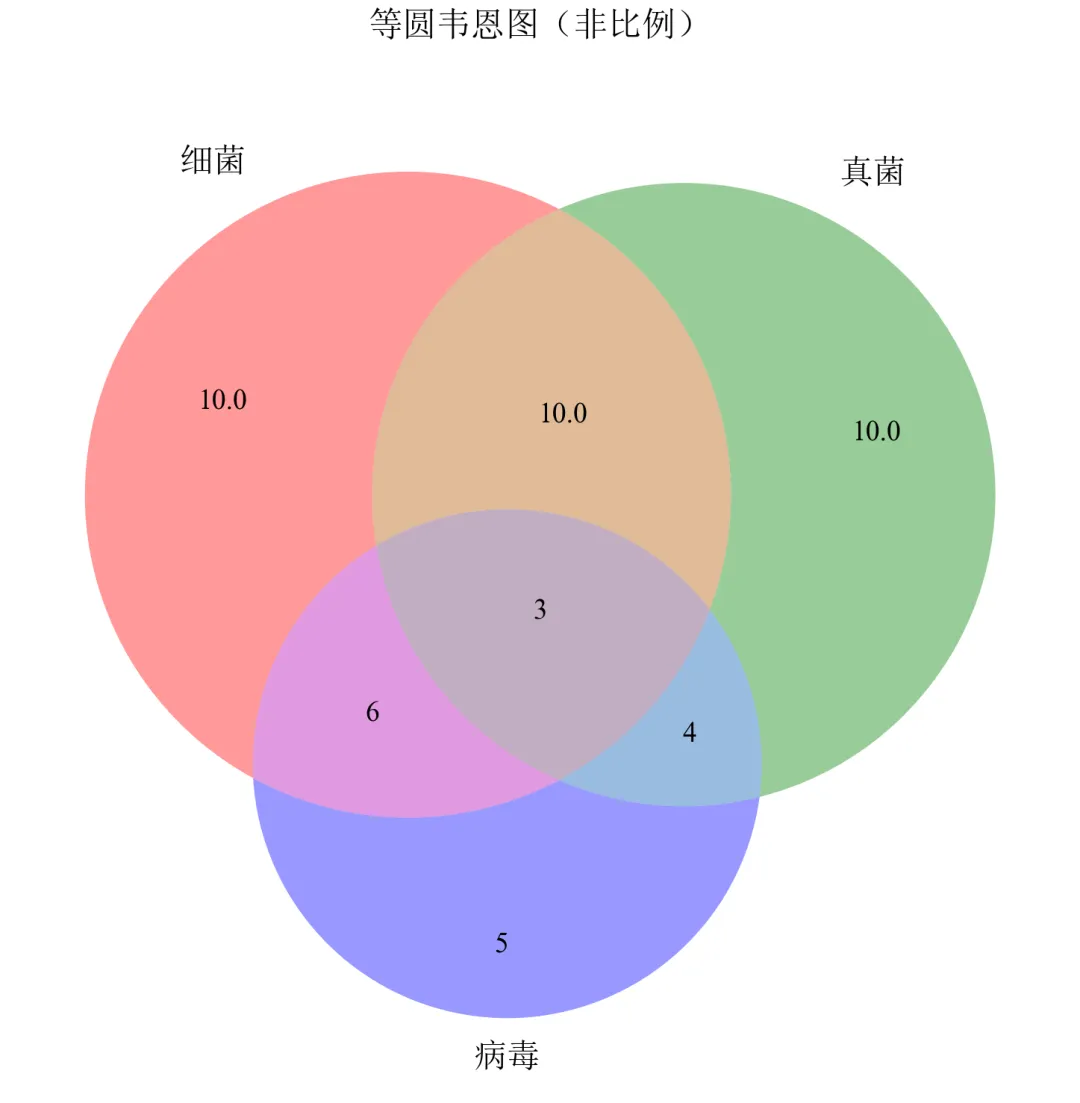
适用于强调集合交集关系、不关心基数比例的场景,如基因列表重叠展示。
进阶3:复杂韦恩图扩展——四元韦恩图
当集合数量时,传统韦恩图难以清晰展示,此处简要展示四元韦恩图方案。
import matplotlib.pyplot as pltfrom matplotlib_venn import venn3from matplotlib.patches import Circledefset_academic_style(): plt.rcParams['font.family'] = ['Times New Roman', 'SimSun'] plt.rcParams['font.size'] = 9 plt.rcParams['axes.unicode_minus'] = False plt.rcParams['axes.linewidth'] = 1.0 plt.rcParams['xtick.major.width'] = 1.0 plt.rcParams['ytick.major.width'] = 1.0 plt.rcParams['xtick.major.size'] = 3.5 plt.rcParams['ytick.major.size'] = 3.5 plt.rcParams['xtick.direction'] = 'in' plt.rcParams['ytick.direction'] = 'in' plt.rcParams['legend.frameon'] = False plt.rcParams['pdf.fonttype'] = 42 plt.rcParams['savefig.dpi'] = 300set_academic_style()# 创建图形fig, ax = plt.subplots(figsize=(8.0, 8.0))# 绘制三元韦恩图venn3(subsets=(10, 8, 12, 5, 6, 4, 3), set_labels=('细菌', '真菌', '病毒'), ax=ax)# 手动添加第四个圆(古菌)circle4 = Circle((0, -0.6), 0.5, alpha=0.3, color='purple', edgecolor='black', linewidth=1.5)ax.add_patch(circle4)ax.text(0, -0.9, '古菌', fontsize=11, ha='center', va='center')ax.set_title('四元韦恩图(三元+手动添加)', fontsize=12, pad=20)plt.tight_layout()plt.show()fig.savefig('四元韦恩图_备选.pdf', bbox_inches='tight', pad_inches=0.05)fig.savefig('四元韦恩图_备选.png', bbox_inches='tight', pad_inches=0.05)执行结果分析:
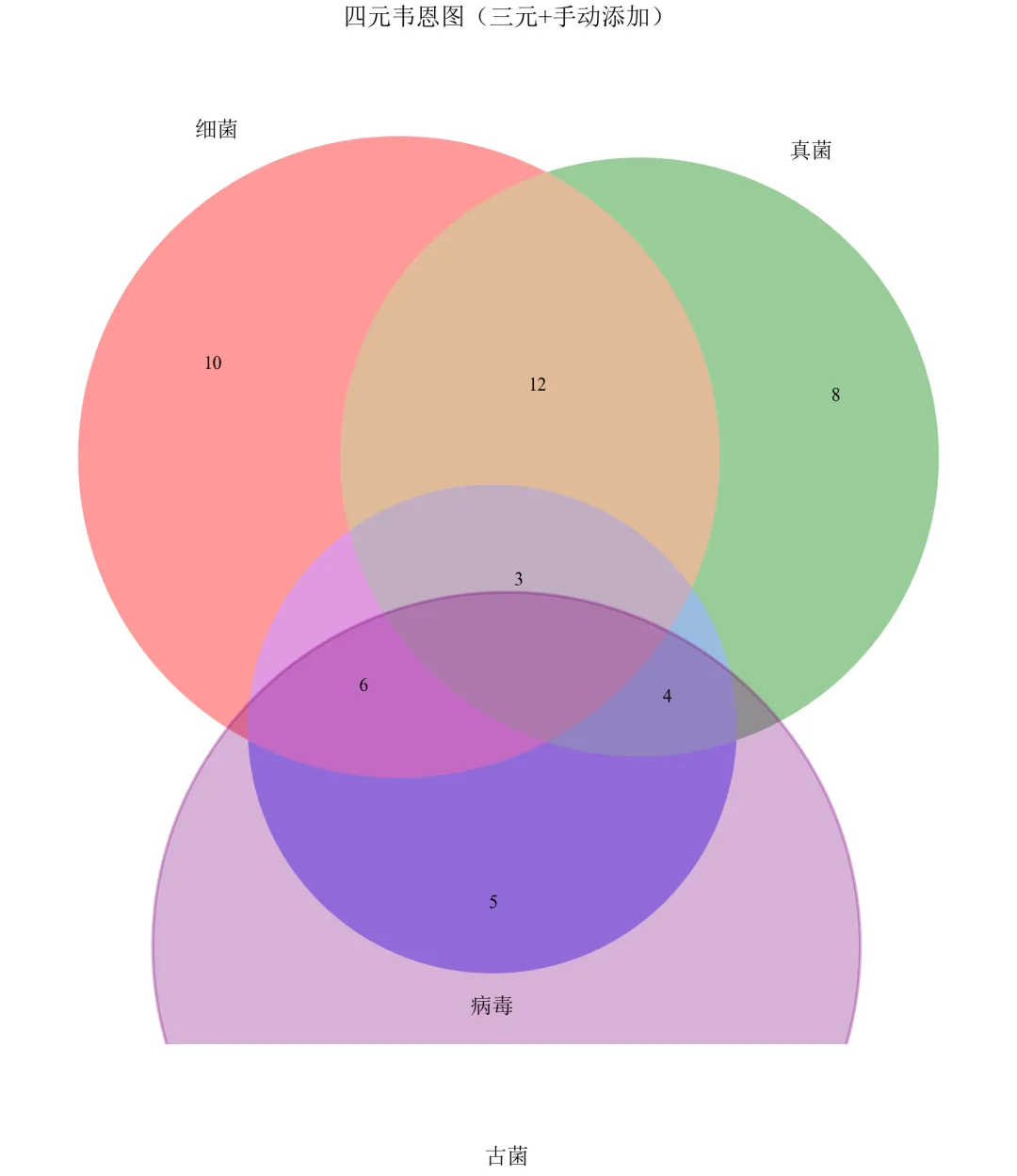
四元韦恩图由四个椭圆构成,阅读困难,一般不建议在论文中使用超过三元的韦恩图。
在撰写学术论文时,推荐三元以内用韦恩图。
- END -