新学期充电:单细胞基础--进阶--python分析培训班 ;空间转录组培训班 (Visium HD、Xenium、Stereo-seq)
- 2026-03-12 02:07:18

2:单细胞数据下载、读取、处理,以Cancer Cell文章为例系统讲解单细胞数据质控
3:公共数据库单细胞数据常见文件读取方式,Seurat数据结构深入解读及多篇CNS单细胞数据的可视化,3D umap展示【Science】
4:多个样本循环结构整合,使用Harmony和CCA去除批次效应【Nat Genet】
5:机器注释singleR、Transfer 映射、手动注释等四种方法注释细胞类型
6:跟着CNS文章进行marker 基因画图展示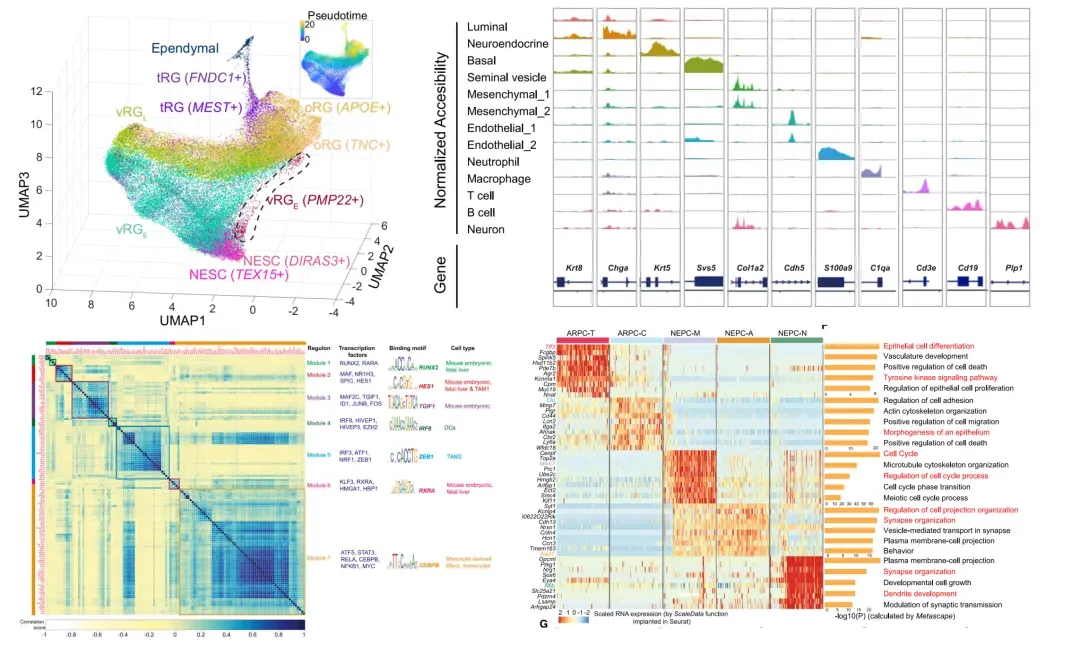
7:单细胞亚群再次降维聚类、注释和metadata的理解
9:不同分组差异基因展示,多分组火山图,瀑布图
10:KEGG/GO通路富集和GESA/GSVA通路活性打分
11:单细胞测序不同分组的相同cluster差异程度3维PCA展示以及差异热图展示【Cell】
12:轨迹分析:slingshot、Monocle2拟时间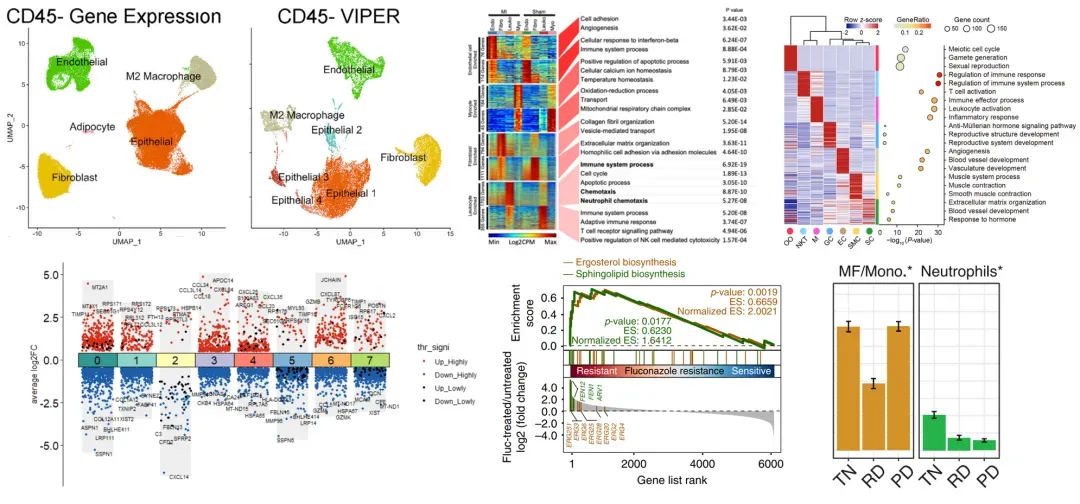
13:CellChat多分组数据集差异分析【Nat Med】
14:NicheNet to link ligands from cells in TME and the EMT program in tumor cells.【Cancer Cell】
15:染色体拷贝数变异:inferCNV copykat
16:使用SCENIC进行转录调控网络分析和核心驱动基因鉴定【Nat Med】
17:跟着Nature文章源代码进行完整文献复现
18:实践课(课程总结,带领学员使用自测数据完成整体分析流程)


单细胞分析问题
可扫描左侧二维码咨询

华 哥 生 信
2:scATAC:motif富集分析、染色质共可及性、转录因子的footprint
3:scATAC的伪时间分析【Nat Genet】
4:以Nature文章为例系统讲解scRNA-seq与scATAC-seq联合分析【Nat Genet】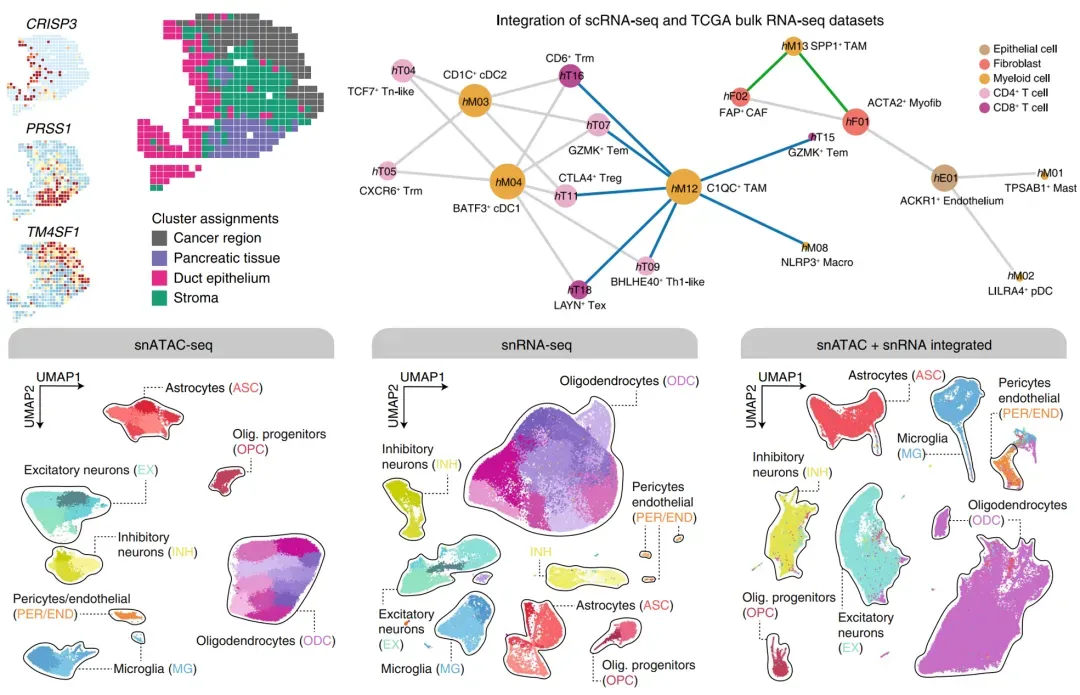
5:CITE–seq对单细胞转录组和膜蛋白进行定量分析【Nat Med】
6:scRepertoire系统分析TCR和BCR数据【Nature】
7:Scissor、BayesPrism进行Bulk和单细胞的联合分析【Science】
8:scRNA-seq和bulk RNA-seq数据联合分析推断细胞类群互作网络【Cell】
9:MAGIC 利用流形学习还原单细胞的基因表达【Cell】
10:hdWGCNA单细胞转录组加权基因共表达网络分析【Cell】
11:使用VISION算法推断单细胞代谢活性【Cancer Discovery】
12:百万细胞数分析方法:Metacell
13:CellRanger处理单细胞上游数据,loom文件生成
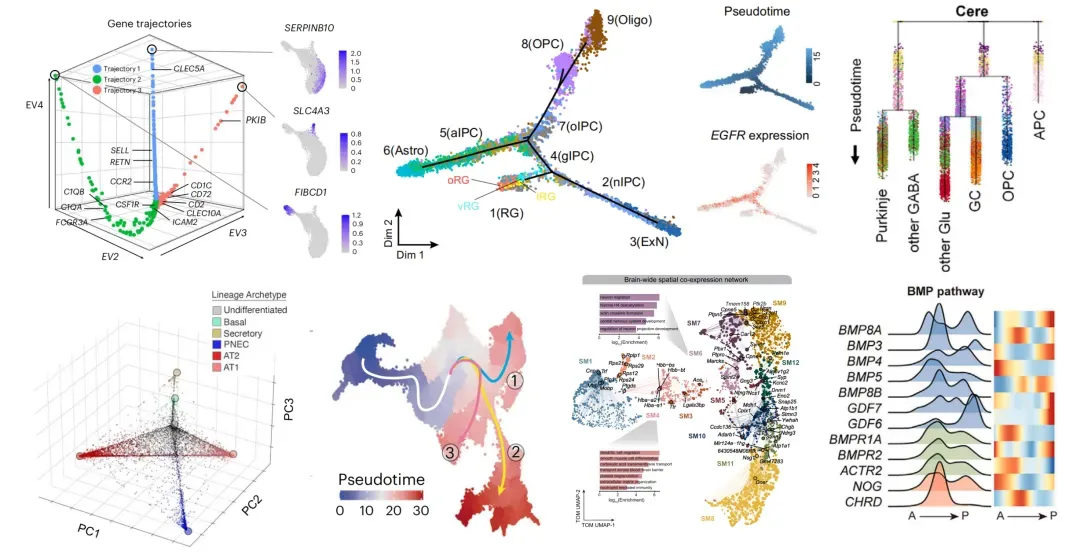
14:CytoTRACE进行拟时间分析,基因表达量随PC1轴的变化 【Cell】
15:3D Diffusion Pseudotime Analysis diffusion component【Cell Stem Cell】
16:Monocle2拟时间与CytoTRACE结合的个性化绘图【Nat Med】
17:Monocle3在三维空间轨迹与scVelo结合 【Nature】
18:Differences in pathway activities scored per cell by GSVA【Nat Med】
19:SCEVAN表征细胞的克隆结构【Science】
20:inferCNV结合UPhyloplot2分析肿瘤进化
21:geneNMF鉴定不同的生物学功能【Cell】,不同cluster的异质性确定【Cancer Cell】
22:CNS文章作图美化
23:scTenifoldKnk:单细胞RNA测序数据进行虚拟基因敲除分析,预测特定
基因在某一细胞群体中敲低后的整体基因表达谱变化
24:scPagwas采用多基因回归模型对一组性状相关基因进行优先排序,并通过将途径活性转化的单细胞RNA测序(scRNA-seq)数据与全基因组关联研究(GWAS)汇总数据相结合,揭示性状相关的细胞亚群。
25:Beyondcell进行药敏分析和药物治疗预测
26:SoupX:进行RNA污染检测和矫正


单细胞分析问题
可扫描左侧二维码咨询

华 哥 生 信
1.Spyder和Anaconda安装
2.环境配置;基本语法、数据类型等
3.Python控制流与函数(条件语句、循环语句、函数定义、返回值)
第2节:Python数据结构进阶
1.列表、元组、字典、集合高级用法
2.Python包(numpy、pandas、matplotlib等)
第3节:Shell基础命令学习了解Shell,基础命令学习(文件操作、权限管理)
第4节:Scanpy单细胞基础分析流程
scanpy 单个样本的单细胞分析流程
AnnData 对象层级结构理解
Leiden算法、Louvain算法(Python)
scanpy 多种单细胞数据文件读取
scrublet去除双细胞
第5节:多个样本数据整合方法
1.ingest和BBKNN:多个样本数据整合
2.scVI和harmonypy:整合多个高维数据集的算法
第6节:单细胞注释方法
1.CellTypist 自定义高精度和低精度注释出细胞的亚群
2.scCODA(Python):基于贝叶斯模型精准分析单细胞组成差异,识别与条件相关的细胞类型丰度变化
第7节:功能富集分析
1.GSEApy:python版本的功能富集分析
2.PROGENy(Python)活性打分(基于转录组数据预测细胞内信号通路活性,帮助揭示细胞功能的调控机制)
第8节:转录因子调控网络分析-pySCENIC转录因子分析
第9节:细胞间通讯分析方法
1.CellphoneDB:整合多物种配体-受体互作与统计建模,系统解析细胞间通讯网络与功能模块
2.LIANA+(Python):整合多组学互作与概率建模,精准量化细胞间配体-受体活性并解析功能特异性通讯网络
第10节:单细胞发育轨迹推断-Palantir进行单细胞发育轨迹推断分析
第11节:降维与轨迹识别方法
1.PHATE同时保留局部结构(local structure) 以及全局结构(global structure)对单细胞数据降维【Nature】
2.Slingshot(Python)轨迹分析
3.PAGA轨迹推断
4.将velocity 与PAGA联合分析【Nature】
第12节:RNA速率分析 - scVelo:RNA速率分析
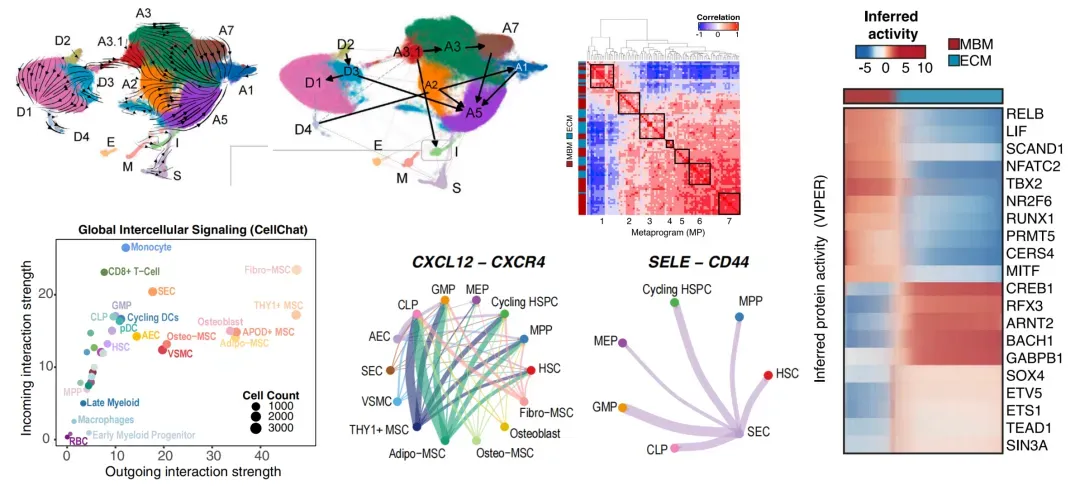
第13节:扰动分析——CellOracle 结合基因调控网络与机器学习,动态模拟细胞命运决策的扰动响应与转录重编程
第14节:百万细胞数分析方法:Metacell (R)、Supercell(Python)
第15节:muon—— Single-cell RNA-seq and ATAC-seq integration
第16节:Scirpy TCR/BCR分析工具
第17节:hotspot 空间聚集识别方法识别单细胞数据中具有显著空间聚集的区域,揭示细胞间的局部相互作用
第18节:CellRank:基于马尔可夫过程和RNA速率的细胞命运预测
第19节:scFEA:代谢分析(自定义代谢通量建模,从单细胞数据解析高精度代谢网络和低覆盖基因谱,揭示细胞代谢重编程。)
第20节:染色体拷贝数推断inferCNVpy: python版的inferCNV
第21节:metaVIPER 自定义蛋白活性推断,整合多组学数据解析高精度调控网络和低信噪比样本,揭示关键驱动蛋白
第22节:drug2cell: 单细胞尺度解析药物扰动响应,量化靶点机制与细胞特异性药效网络
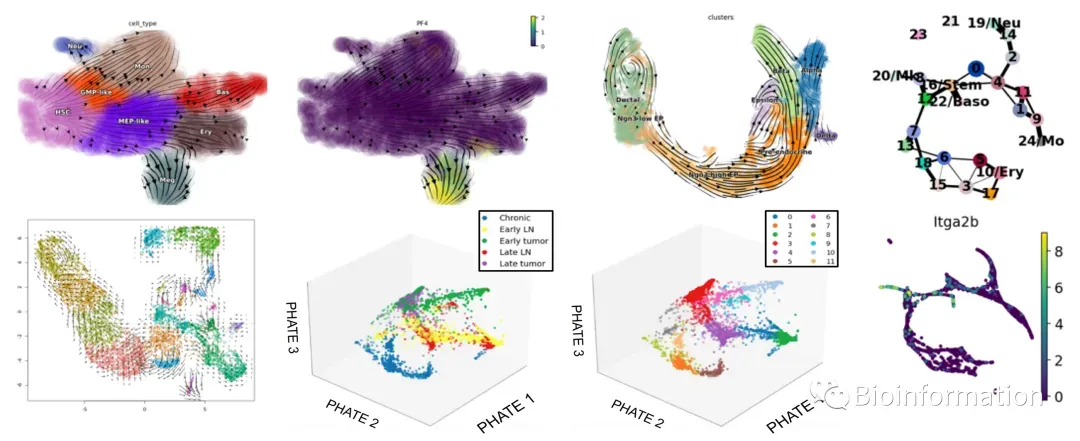
第23节:scAge: 单细胞水平解析衰老相关基因表达动态,量化细胞年龄状态与衰老轨迹
第24节:scTE : 单细胞转座子表达分析工具,解析转座子活性与细胞异质性关联(转座元件分析)
第25节:MAGIC :使用数据扩散从单细胞数据中恢复基因的相互作用
第26节:CellOracle:通过单细胞多组学(转录组+表观组)数据推断细胞命运调控网络的计算工具
第27节:scDRS:将单细胞RNA-seq数据中的单个细胞与疾病GWASs相关联
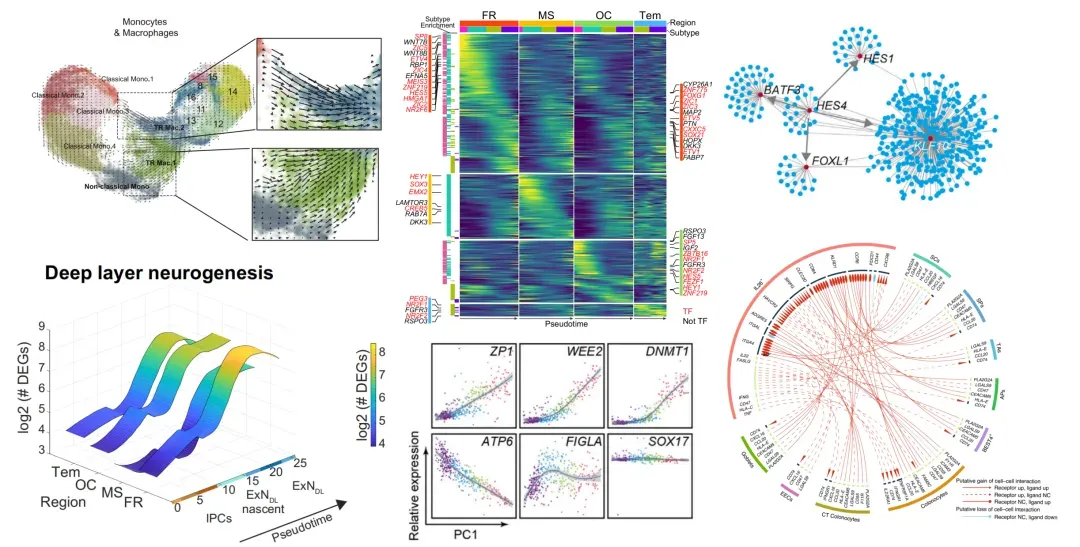
►►►
空转班内容介绍
第1节:Python编程语言入门
1.Spyder和Anaconda安装
2.环境配置;基本语法、数据类型等
第2节:Python数据结构进阶
1.列表、元组、字典、集合高级用法
2.Python包(numpy、pandas、matplotlib等)
第3节:空间转录组在CNS文章应用
1.空间转录组CNS文章思路解析
2.空间转录组技术在科研领域的应用
第4节:以Nature Genetics文章源代码为例,系统学习squidpy和scanpy的系统分析
1.常规空间转录组数据读取
2.数据质控--scrublet去除双细胞
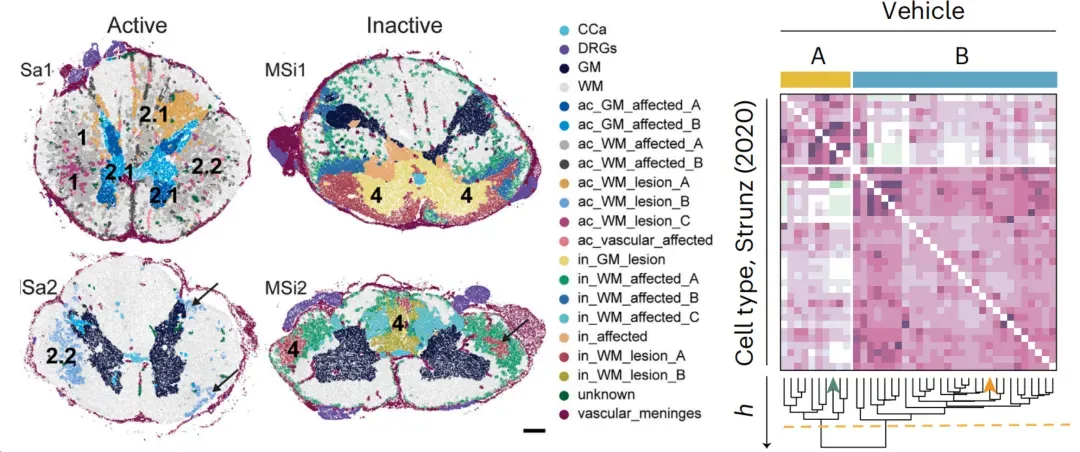
第5节:反卷积算法【Science】源代码
1.CCA锚定算法--【Nature】源代码
2.非负矩阵分解和非负最小二乘
第6节:Visium HD空转数据系统分析【Science】
1.Python的scanpy分析Visium HD数据
2.R语言的Seurat分析Visium HD数据
第7节:Stereo-seq空转数据分析【Cell】源代码
1.Tissue Segmentation、Cell Correction分析
2.SpaTrack、PAGA、RNA Velocity分析
第8节:Cell2location采用贝叶斯层次框架--整合单细胞和空转数据--【Cell】源代码
1.计算单细胞细胞类型的表达特征
第9节:Hotspot识别空间数据集中信息基因(和基因模块)探索空间组织微环境【Nat Genet】
1.计算 KNN 图--【Nat Genet】源代码
2.查找信息基因,将基因分组到模块
3.评估成对基因关联【Nat Med】源代码
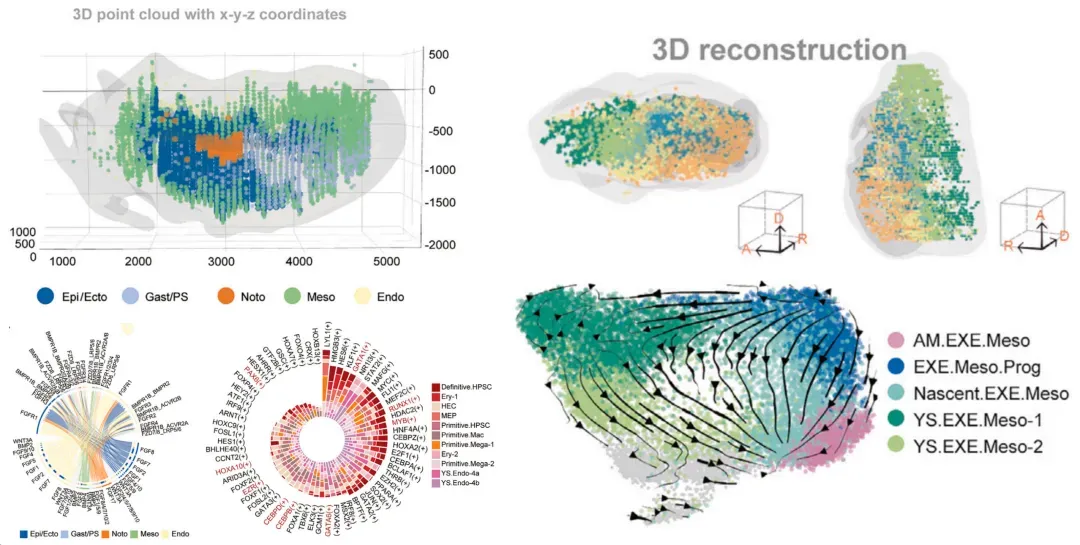
第10节:Banksy--深入地理解细胞间的相互作用和组织构造【Science】
1.空转数据分析之生态位聚类算法Banksy
2.空间转录组学数据中细胞邻居依赖性基因表达的新方法【Neuron】
第11节:表达增强:BayesSpace--利用空间转录组数据中的邻域结构来增加子点级别分辨率的计算方法【Nat Commun】
1.TESLA--利用神经网络CNN算法提高空转的分辨率
第12节:空间转录组的轨迹分析-【Cancer Cell】
1.stlearn:基于全组织SME均一化的PAGA轨迹分析
2.SPATA:空间背景下不同表达的基因和基因集轨迹变化【Cell】
第13节:MISTy--空间细胞共定位【Nat Med】
1.MISTy不仅可以做细胞-细胞之间的dependency
2.基因和基因之间、细胞和通路之间的dependency
第14节:COMMOT--细胞间通讯【Cell】
1.利用最优运输进行空间转录组细胞间通讯分析
2.推断的信号传导与已知下游基因活性相关性【NC】
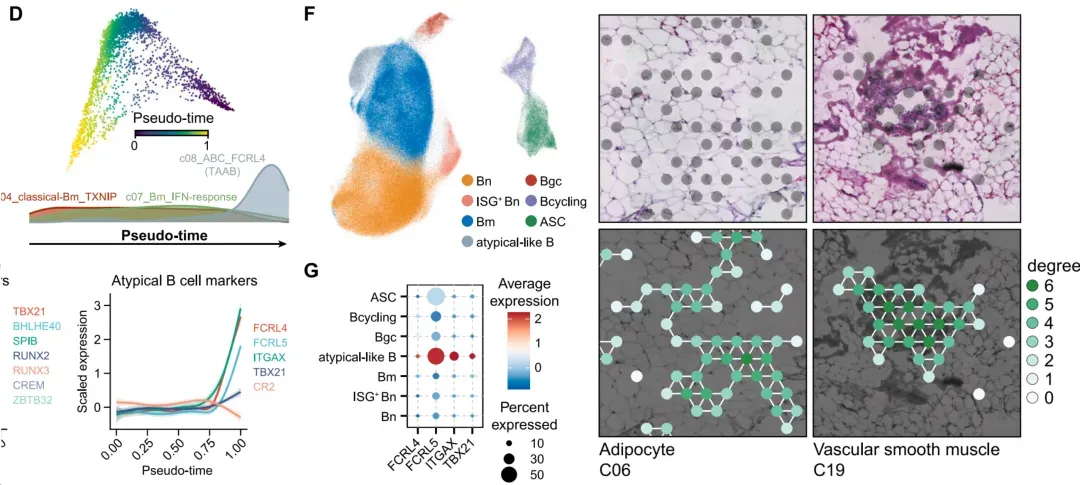
第15节:细胞互作分析 -- NicheNet、CellChat
1.CellChat各种图形可视化【Cell】
2.NicheNet分析配体对下游基因调控
第16节:空转速率分析-SIRV【Nat Med】
1.单细胞分辨率推断空间 RNA 速度【Cell】
第17节:空间细胞网络构建--cell degree
1.构建空间近邻网络【Nat Commun】
2.在空间领域展示细胞网络【Cell】
第18节:空间区域组织模块发现以【Nat Med】
1.深度学习框架的人工智能算法 SPACE
2.ISCHIA细胞类型和转录物在同一位置空间共现
第19节:Giotto|| 空间表达数据分析工具箱
1.PAGE--单细胞数据注释空转的spot【Nature】
2.spatital patterns 提取连续的空间表达模式分析
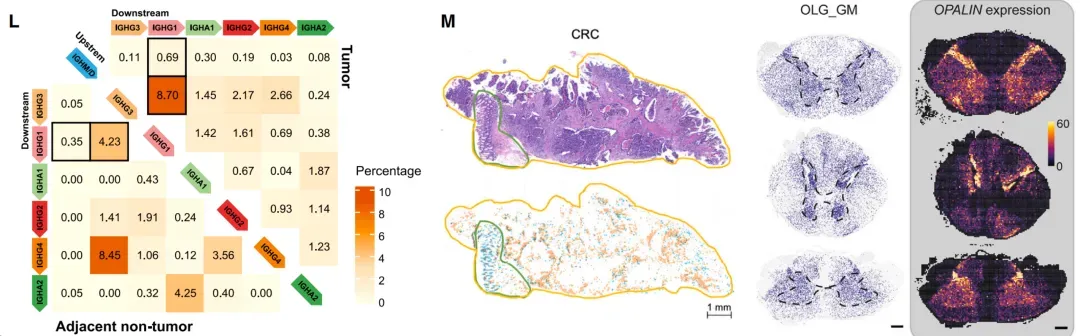
第20节:空间转录组数据三大矩阵分析
1.基因表达矩阵【Nature Metab】
2..细胞类型矩阵【Nature Aging】
第21节:空间分子生态位差异分析---Niche-DE
1.空转数据中的生态位差异基因表达分析
2.可识别上下文依赖性细胞间相互作用
第22节:trendsceek识别基因空间表达趋势
1.空间基因模式基于Python的SpatialDE
2.基于R语言的trendsceek 【Nature】
3.SPARK-X--广义线性空间模型【Nat Methods】
第23节:肿瘤克隆空间演化--空间肿瘤细胞CNV
1. siCNV 分析并构建了克隆进化树【Nature】
2.空间克隆分布与 Gleason 分级相关性
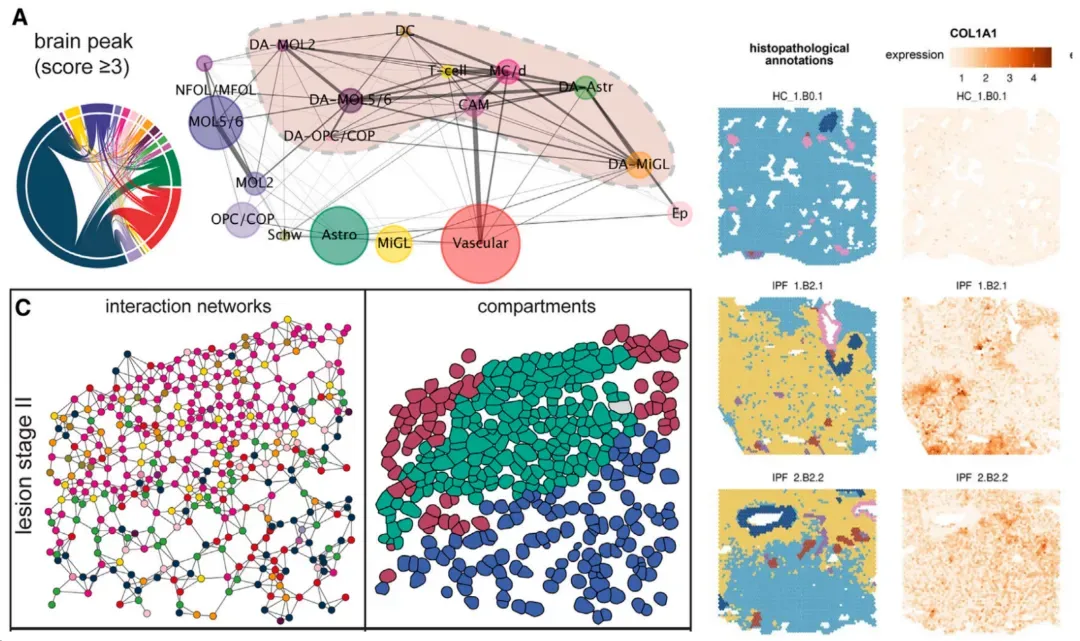
1.神经网络模型StarDist定位图像中的星形细胞
2.基于深度学习Cellpose高质量的细胞分割
第25节:利用pyVIPER算法来定量空间蛋白的活性
1.检查谱系特异性基因调控网络【Cell】
2.基因表达特征转换为蛋白质活性矩阵
第26节:GeneTrajectory单细胞基因轨迹推断
1.构建一个细胞到细胞的 kNN 图【Science】
2.计算基因分布之间基于成对图的 Wasserstein 距离
第27节:pySCENIC转录调控网络,网络特异性评分和轨迹联合分析【Cell Stem Cell】
1.以Cell文章系统讲解pySCENIC源代码
2.以Nat Med多形式可视化调控单元
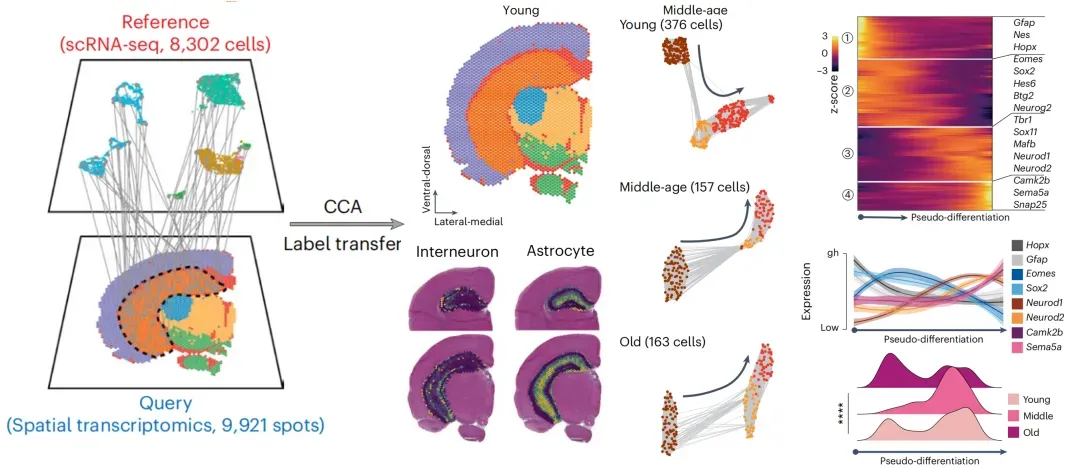
第28节:Xenium原位分析【NC】
1.构建空间邻域图、计算共现概率
2.Squidpy读取xenium数据、邻域富集分析
第29节:实践课(课程总结,带领学员使用自测数据完成整体分析流程)
1.实战答疑
2.课程大总结

01
主讲老师
主讲老师华哥:华哥,中山大学博士,目前在东京大学从事医学人工智能研究。深耕单细胞多组学、空间转录组与机器学习领域6年,培养学员3万余人 ; 指导学员发表CNS主刊文章8篇、一区及子刊90余篇 ; 参与国自然重点、国家重大专项、孔雀计划等项目申报;合作院士团队及国际顶尖实验室,发表SCI论文21篇(PNAS、Cell Rep Med、JACS、Mol Cancer、EMBO Mol Med等顶刊)
02
华哥科研平台介绍
授课理念:将生信内容全部学懂(理解)、学会(会敲代码分析)、学透彻(站在课题顶层设计角度理解)、学以致用(用到自己的标书申请和文章发表中)。
1.从19年开始到现在,我们在生信教育领域深耕六年之久,时间是最好的证明!

2.一对一指导、包教包会是我们开培训班五年来一贯的宗旨。我们敢承诺包教会的底气是来自多年的讲课经验和认真负责的态度。课程结束,答疑不结束!

03
华哥生信线下往期回顾
1.中国抗癌协会举办的肿瘤标志物学术大会,开设华哥生信团队CNS文章空间多组学公益培训专场






1
中间没时间咋办
2
课程售后服务怎样
再好的课程没有完善的后续服务只能让你摸不着脑袋,所以我们课后有完善的一对一指导服务,解决每个学员的所有问题。有问题及时一对一解决,把所有问题解决就学会了
3
两个月后老师还指导我吗

